+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5p97 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | rat catechol O-methyltransferase in complex with 5-(4-fluorophenyl)-2,3-dihydroxy-N-[(1-methylimidazol-4-yl)methyl]benzamide at 1.30A | ||||||
 要素 要素 | Catechol O-methyltransferase | ||||||
 キーワード キーワード | TRANSFERASE / METHYLTRANSFERASE / NEUROTRANSMITTER DEGRADATION | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of homocysteine metabolic process / response to olanzapine / response to risperidone / Enzymatic degradation of dopamine by COMT / Enzymatic degradation of Dopamine by monoamine oxidase / Methylation / norepinephrine secretion / response to dopamine / mastication / catecholamine catabolic process ...positive regulation of homocysteine metabolic process / response to olanzapine / response to risperidone / Enzymatic degradation of dopamine by COMT / Enzymatic degradation of Dopamine by monoamine oxidase / Methylation / norepinephrine secretion / response to dopamine / mastication / catecholamine catabolic process / catechol O-methyltransferase activity / S-adenosylhomocysteine metabolic process / catechol O-methyltransferase / developmental process / renal sodium excretion / renal filtration / S-adenosylmethionine metabolic process / renin secretion into blood stream / dopamine secretion / catecholamine metabolic process / renal albumin absorption / artery development / habituation / cerebellar cortex morphogenesis / dopamine catabolic process / response to salt / glomerulus development / norepinephrine metabolic process / short-term memory / response to angiotensin / fear response / synaptic transmission, dopaminergic / cellular response to phosphate starvation / cellular response to cocaine / estrogen metabolic process / cholesterol efflux / prostaglandin metabolic process / response to food / response to pain / negative regulation of dopamine metabolic process / response to corticosterone / response to temperature stimulus / glycogen metabolic process / response to stress / startle response / dopamine metabolic process / exploration behavior / detection of temperature stimulus involved in sensory perception of pain / behavioral fear response / multicellular organismal response to stress / response to cytokine / response to amphetamine / learning / negative regulation of smooth muscle cell proliferation / kidney development / female pregnancy / visual learning / regulation of blood pressure / response to toxic substance / response to wounding / response to estrogen / memory / cognition / multicellular organism growth / cell body / response to oxidative stress / vesicle / response to lipopolysaccharide / methylation / gene expression / dendritic spine / postsynaptic membrane / learning or memory / response to hypoxia / postsynapse / response to xenobiotic stimulus / axon / dendrite / glutamatergic synapse / magnesium ion binding / membrane / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.3 Å 分子置換 / 解像度: 1.3 Å | ||||||
 データ登録者 データ登録者 | Ehler, A. / Lerner, C. / Rudolph, M.G. | ||||||
 引用 引用 |  ジャーナル: To be published ジャーナル: To be publishedタイトル: Crystal Structure of a COMT complex 著者: Lerner, C. / Rudolph, M.G. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5p97.cif.gz 5p97.cif.gz | 114.9 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5p97.ent.gz pdb5p97.ent.gz | 87.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5p97.json.gz 5p97.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  5p97_validation.pdf.gz 5p97_validation.pdf.gz | 736.4 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  5p97_full_validation.pdf.gz 5p97_full_validation.pdf.gz | 738.2 KB | 表示 | |
| XML形式データ |  5p97_validation.xml.gz 5p97_validation.xml.gz | 13.6 KB | 表示 | |
| CIF形式データ |  5p97_validation.cif.gz 5p97_validation.cif.gz | 20.5 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/p9/5p97 https://data.pdbj.org/pub/pdb/validation_reports/p9/5p97 ftp://data.pdbj.org/pub/pdb/validation_reports/p9/5p97 ftp://data.pdbj.org/pub/pdb/validation_reports/p9/5p97 | HTTPS FTP |
-グループ登録
| ID | G_1002010 (10エントリ) |
|---|---|
| タイトル | Crystal Structure of COMT complex |
| タイプ | undefined |
| 解説 | Crystal Structure of COMT complex |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 1分子 A
| #1: タンパク質 | 分子量: 24772.400 Da / 分子数: 1 / 断片: SOLUBLE FORM, RESIDUES 44-264 / 由来タイプ: 組換発現 / 由来: (組換発現)   |
|---|
-非ポリマー , 6種, 266分子 

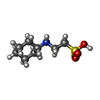








| #2: 化合物 | ChemComp-MG / | ||||||||
|---|---|---|---|---|---|---|---|---|---|
| #3: 化合物 | | #4: 化合物 | ChemComp-NHE / | #5: 化合物 | #6: 化合物 | ChemComp-77K / | #7: 水 | ChemComp-HOH / | |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.19 Å3/Da / 溶媒含有率: 43.83 % |
|---|---|
| 結晶化 | 温度: 295 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 9 / 詳細: AMMONIUM SULPHATE, CHES, PH 9 |
-データ収集
| 回折 | 平均測定温度: 100 K | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SLS SLS  / ビームライン: X10SA / 波長: 1 Å / ビームライン: X10SA / 波長: 1 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 検出器 | タイプ: MARMOSAIC 225 mm CCD / 検出器: CCD / 日付: 2009年5月25日 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射波長 | 波長: 1 Å / 相対比: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 | 解像度: 1.3→44.75 Å / Num. obs: 54116 / % possible obs: 99.6 % / Observed criterion σ(I): -3 / 冗長度: 6.85 % / Biso Wilson estimate: 19.33 Å2 / CC1/2: 0.997 / Rmerge(I) obs: 0.112 / Rrim(I) all: 0.122 / Χ2: 0.983 / Net I/σ(I): 10.72 / Num. measured all: 370775 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 シェル | Diffraction-ID: 1 / Rejects: _
|
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: inhouse model 解像度: 1.3→44.75 Å / Cor.coef. Fo:Fc: 0.973 / Cor.coef. Fo:Fc free: 0.965 / SU B: 1.913 / SU ML: 0.035 / 交差検証法: THROUGHOUT / σ(F): 0 / ESU R: 0.058 / ESU R Free: 0.052 / 立体化学のターゲット値: MAXIMUM LIKELIHOOD 詳細: Ligand has more than one alternate conformation at imidazole part these have not been modeled. Nearby MET has four different conformations.
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.4 Å / 溶媒モデル: BABINET MODEL WITH MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 44.5 Å2 / Biso mean: 11.701 Å2 / Biso min: 6.57 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: final / 解像度: 1.3→44.75 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 1.3→1.334 Å / Total num. of bins used: 20
|
 ムービー
ムービー コントローラー
コントローラー






















 PDBj
PDBj




