| 登録情報 | データベース: PDB / ID: 5niq
|
|---|
| タイトル | exendin-4 variant with dual GLP-1 / glucagon receptor activity |
|---|
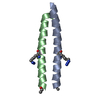
 要素 要素 | Exendin-4 |
|---|
 キーワード キーワード | HORMONE / exendin-4 analogue / dual GLP-1 / glucagon agonist |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
hormone activity / regulation of blood pressure / toxin activity / extracellular region類似検索 - 分子機能 Glucagon/GIP/secretin/VIP / Peptide hormone / Glucagon / GIP / secretin / VIP family signature. / Glucagon like hormones類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Heloderma suspectum (爬虫類) Heloderma suspectum (爬虫類) |
|---|
| 手法 | 溶液NMR / molecular dynamics |
|---|
 データ登録者 データ登録者 | Evers, A. / Kurz, M. |
|---|
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 2017 ジャーナル: J.Med.Chem. / 年: 2017
タイトル: Design of Novel Exendin-Based Dual Glucagon-like Peptide 1 (GLP-1)/Glucagon Receptor Agonists.
著者: Evers, A. / Haack, T. / Lorenz, M. / Bossart, M. / Elvert, R. / Henkel, B. / Stengelin, S. / Kurz, M. / Glien, M. / Dudda, A. / Lorenz, K. / Kadereit, D. / Wagner, M. |
|---|
| 履歴 | | 登録 | 2017年3月24日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2018年2月28日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2019年3月27日 | Group: Data collection / Database references
カテゴリ: citation / citation_author / pdbx_database_proc
Item: _citation.country / _citation.journal_abbrev ..._citation.country / _citation.journal_abbrev / _citation.journal_id_ASTM / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title / _citation.year |
|---|
| 改定 1.2 | 2019年5月8日 | Group: Data collection / カテゴリ: pdbx_nmr_software / Item: _pdbx_nmr_software.name |
|---|
| 改定 2.0 | 2019年9月11日 | Group: Advisory / Atomic model ...Advisory / Atomic model / Data collection / Derived calculations
カテゴリ: atom_site / pdbx_nmr_representative ...atom_site / pdbx_nmr_representative / pdbx_validate_close_contact / pdbx_validate_rmsd_angle / pdbx_validate_torsion / struct_conf / struct_conn / struct_site / struct_site_gen
Item: _atom_site.Cartn_x / _atom_site.Cartn_y ..._atom_site.Cartn_x / _atom_site.Cartn_y / _atom_site.Cartn_z / _pdbx_nmr_representative.conformer_id / _pdbx_validate_close_contact.PDB_model_num / _pdbx_validate_close_contact.auth_atom_id_1 / _pdbx_validate_close_contact.auth_atom_id_2 / _pdbx_validate_close_contact.auth_comp_id_1 / _pdbx_validate_close_contact.auth_seq_id_1 / _pdbx_validate_close_contact.auth_seq_id_2 / _pdbx_validate_close_contact.dist / _pdbx_validate_rmsd_angle.PDB_model_num / _pdbx_validate_rmsd_angle.angle_deviation / _pdbx_validate_rmsd_angle.angle_standard_deviation / _pdbx_validate_rmsd_angle.angle_target_value / _pdbx_validate_rmsd_angle.angle_value / _pdbx_validate_rmsd_angle.auth_atom_id_1 / _pdbx_validate_rmsd_angle.auth_atom_id_2 / _pdbx_validate_rmsd_angle.auth_atom_id_3 / _pdbx_validate_rmsd_angle.auth_comp_id_1 / _pdbx_validate_rmsd_angle.auth_comp_id_2 / _pdbx_validate_rmsd_angle.auth_comp_id_3 / _pdbx_validate_rmsd_angle.auth_seq_id_1 / _pdbx_validate_rmsd_angle.auth_seq_id_2 / _pdbx_validate_rmsd_angle.auth_seq_id_3 / _pdbx_validate_torsion.PDB_model_num / _pdbx_validate_torsion.auth_comp_id / _pdbx_validate_torsion.auth_seq_id / _pdbx_validate_torsion.phi / _pdbx_validate_torsion.psi / _struct_conf.beg_auth_seq_id / _struct_conf.beg_label_seq_id / _struct_conf.end_auth_comp_id / _struct_conf.end_auth_seq_id / _struct_conf.end_label_comp_id / _struct_conf.end_label_seq_id / _struct_conf.pdbx_PDB_helix_length / _struct_conn.pdbx_dist_value / _struct_site.pdbx_num_residues |
|---|
| 改定 2.1 | 2024年10月23日 | Group: Data collection / Database references / Structure summary
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_entry_details / pdbx_modification_feature
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Heloderma suspectum (爬虫類)
Heloderma suspectum (爬虫類) データ登録者
データ登録者 引用
引用 ジャーナル: J.Med.Chem. / 年: 2017
ジャーナル: J.Med.Chem. / 年: 2017 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5niq.cif.gz
5niq.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5niq.ent.gz
pdb5niq.ent.gz PDB形式
PDB形式 5niq.json.gz
5niq.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 5niq_validation.pdf.gz
5niq_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 5niq_full_validation.pdf.gz
5niq_full_validation.pdf.gz 5niq_validation.xml.gz
5niq_validation.xml.gz 5niq_validation.cif.gz
5niq_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/ni/5niq
https://data.pdbj.org/pub/pdb/validation_reports/ni/5niq ftp://data.pdbj.org/pub/pdb/validation_reports/ni/5niq
ftp://data.pdbj.org/pub/pdb/validation_reports/ni/5niq リンク
リンク 集合体
集合体
 要素
要素 Heloderma suspectum (爬虫類) / 参照: UniProt: P26349*PLUS
Heloderma suspectum (爬虫類) / 参照: UniProt: P26349*PLUS 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj



 HSQC
HSQC