+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 5exy | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Crystal structure of in cellulo recombinant CPV1 Polyhedra | ||||||
 要素 要素 | Polyhedrin | ||||||
 キーワード キーワード | VIRAL PROTEIN / in vivo crystal / in cellulo data collection | ||||||
| 機能・相同性 | Cypovirus polyhedrin, Cypovirus 1 type / Cypovirus polyhedrin protein / viral occlusion body / host cell cytoplasm / ADENOSINE-5'-TRIPHOSPHATE / CYTIDINE-5'-TRIPHOSPHATE / GUANOSINE-5'-TRIPHOSPHATE / Polyhedrin 機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |   Bombyx mori cytoplasmic polyhedrosis virus (ウイルス) Bombyx mori cytoplasmic polyhedrosis virus (ウイルス) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.55 Å 分子置換 / 解像度: 1.55 Å | ||||||
 データ登録者 データ登録者 | Boudes, M. / Garriga, D. / Coulibaly, F. | ||||||
 引用 引用 |  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2016 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2016タイトル: A pipeline for structure determination of in vivo-grown crystals using in cellulo diffraction. 著者: Boudes, M. / Garriga, D. / Fryga, A. / Caradoc-Davies, T. / Coulibaly, F. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  5exy.cif.gz 5exy.cif.gz | 114.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb5exy.ent.gz pdb5exy.ent.gz | 88 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  5exy.json.gz 5exy.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  5exy_validation.pdf.gz 5exy_validation.pdf.gz | 1.2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  5exy_full_validation.pdf.gz 5exy_full_validation.pdf.gz | 1.2 MB | 表示 | |
| XML形式データ |  5exy_validation.xml.gz 5exy_validation.xml.gz | 13.2 KB | 表示 | |
| CIF形式データ |  5exy_validation.cif.gz 5exy_validation.cif.gz | 19.2 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ex/5exy https://data.pdbj.org/pub/pdb/validation_reports/ex/5exy ftp://data.pdbj.org/pub/pdb/validation_reports/ex/5exy ftp://data.pdbj.org/pub/pdb/validation_reports/ex/5exy | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 | x 12
| |||||||||
| 単位格子 |
| |||||||||
| Components on special symmetry positions |
|
- 要素
要素
-タンパク質 , 1種, 1分子 A
| #1: タンパク質 | 分子量: 28387.316 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)   Bombyx mori cytoplasmic polyhedrosis virus (ウイルス) Bombyx mori cytoplasmic polyhedrosis virus (ウイルス)細胞株 (発現宿主): Sf9 発現宿主:  参照: UniProt: P11041 |
|---|
-非ポリマー , 6種, 210分子 


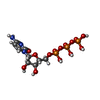







| #2: 化合物 | ChemComp-CL / | ||||||||
|---|---|---|---|---|---|---|---|---|---|
| #3: 化合物 | | #4: 化合物 | ChemComp-ATP / | #5: 化合物 | ChemComp-CTP / | #6: 化合物 | ChemComp-GTP / | #7: 水 | ChemComp-HOH / | |
-詳細
| Has protein modification | Y |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 1.61 Å3/Da / 溶媒含有率: 23.71 % |
|---|---|
| 結晶化 | 温度: 300 K / 手法: in cell 詳細: in vivo crystallization in the cytoplasm of the cell |
-データ収集
| 回折 | 平均測定温度: 100 K Ambient temp details: In cellulo data collection. X-ray beam collimated to 10x10 microns. | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  Australian Synchrotron Australian Synchrotron  / ビームライン: MX2 / 波長: 1 Å / ビームライン: MX2 / 波長: 1 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 検出器 | タイプ: ADSC QUANTUM 315 / 検出器: CCD / 日付: 2014年6月6日 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射 | モノクロメーター: Double crystal (Si111) / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 放射波長 | 波長: 1 Å / 相対比: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 | 解像度: 1.55→30 Å / Num. obs: 26475 / % possible obs: 99.6 % / 冗長度: 5.9 % / Biso Wilson estimate: 8.12 Å2 / Rmerge(I) obs: 0.249 / Rpim(I) all: 0.111 / Rrim(I) all: 0.257 / Χ2: 1.04 / Net I/av σ(I): 7.632 / Net I/σ(I): 4.3 / Num. measured all: 155448 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 反射 シェル | Diffraction-ID: 1 / Rejects: _
|
-位相決定
| 位相決定 | 手法:  分子置換 分子置換 |
|---|
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: PDB entry 2OH5 解像度: 1.55→24.32 Å / Cor.coef. Fo:Fc: 0.9671 / Cor.coef. Fo:Fc free: 0.9501 / SU R Cruickshank DPI: 0.099 / 交差検証法: THROUGHOUT / σ(F): 0 / SU R Blow DPI: 0.074 / SU Rfree Blow DPI: 0.076 / SU Rfree Cruickshank DPI: 0.076
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso max: 97.99 Å2 / Biso mean: 8.16 Å2 / Biso min: 3 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.129 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: final / 解像度: 1.55→24.32 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 1.55→1.61 Å / Total num. of bins used: 13
|
 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj





