| 登録情報 | データベース: PDB / ID: 5emc
|
|---|
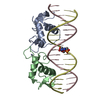
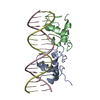
| タイトル | Transcription factor GRDBD and smGRE complex |
|---|
 要素 要素 | - DNA (5'-D(*CP*CP*AP*GP*AP*AP*(5CM)P*AP*TP*CP*AP*TP*GP*TP*TP*(5CM)P*TP*G)-3')
- DNA (5'-D(*CP*CP*AP*GP*AP*AP*(5CM)P*AP*TP*GP*AP*TP*GP*TP*TP*(5CM)P*TP*G)-3')
- Glucocorticoid receptor
|
|---|
 キーワード キーワード | TRANSCRIPTION/DNA / Transcription factor / complex / DNA / TRANSCRIPTION-DNA complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
Regulation of NPAS4 gene transcription / regulation of glucocorticoid biosynthetic process / nuclear glucocorticoid receptor activity / steroid hormone binding / glucocorticoid metabolic process / response to cortisol / PTK6 Expression / neuroinflammatory response / mammary gland duct morphogenesis / microglia differentiation ...Regulation of NPAS4 gene transcription / regulation of glucocorticoid biosynthetic process / nuclear glucocorticoid receptor activity / steroid hormone binding / glucocorticoid metabolic process / response to cortisol / PTK6 Expression / neuroinflammatory response / mammary gland duct morphogenesis / microglia differentiation / maternal behavior / astrocyte differentiation / adrenal gland development / regulation of gluconeogenesis / cellular response to glucocorticoid stimulus / cellular response to steroid hormone stimulus / motor behavior / estrogen response element binding / cellular response to dexamethasone stimulus / nuclear receptor-mediated steroid hormone signaling pathway / FOXO-mediated transcription of oxidative stress, metabolic and neuronal genes / cellular response to transforming growth factor beta stimulus / core promoter sequence-specific DNA binding / steroid binding / TBP-class protein binding / HSP90 chaperone cycle for steroid hormone receptors (SHR) in the presence of ligand / RNA polymerase II transcription regulatory region sequence-specific DNA binding / chromosome segregation / synaptic transmission, glutamatergic / SUMOylation of intracellular receptors / promoter-specific chromatin binding / Hsp90 protein binding / Nuclear Receptor transcription pathway / response to wounding / positive regulation of miRNA transcription / DNA-binding transcription repressor activity, RNA polymerase II-specific / spindle / nuclear receptor activity / Regulation of RUNX2 expression and activity / sequence-specific double-stranded DNA binding / : / positive regulation of neuron apoptotic process / chromatin organization / DNA-binding transcription activator activity, RNA polymerase II-specific / gene expression / Potential therapeutics for SARS / DNA-binding transcription factor activity, RNA polymerase II-specific / nuclear speck / RNA polymerase II cis-regulatory region sequence-specific DNA binding / mitochondrial matrix / DNA-binding transcription factor activity / cell division / negative regulation of DNA-templated transcription / apoptotic process / synapse / centrosome / regulation of DNA-templated transcription / regulation of transcription by RNA polymerase II / protein kinase binding / chromatin / negative regulation of transcription by RNA polymerase II / signal transduction / positive regulation of transcription by RNA polymerase II / protein-containing complex / RNA binding / zinc ion binding / nucleoplasm / identical protein binding / nucleus / membrane / cytoplasm / cytosol類似検索 - 分子機能 Glucocorticoid receptor / Glucocorticoid receptor / Erythroid Transcription Factor GATA-1, subunit A / Erythroid Transcription Factor GATA-1; Chain A / : / Nuclear hormone receptor / Nuclear hormones receptors DNA-binding region signature. / Zinc finger, nuclear hormone receptor-type / Double treble clef zinc finger, C4 type / Nuclear hormone receptors DNA-binding domain profile. ...Glucocorticoid receptor / Glucocorticoid receptor / Erythroid Transcription Factor GATA-1, subunit A / Erythroid Transcription Factor GATA-1; Chain A / : / Nuclear hormone receptor / Nuclear hormones receptors DNA-binding region signature. / Zinc finger, nuclear hormone receptor-type / Double treble clef zinc finger, C4 type / Nuclear hormone receptors DNA-binding domain profile. / c4 zinc finger in nuclear hormone receptors / Nuclear hormone receptor, ligand-binding domain / Nuclear hormone receptor-like domain superfamily / Ligand-binding domain of nuclear hormone receptor / Nuclear receptor (NR) ligand-binding (LBD) domain profile. / Ligand binding domain of hormone receptors / Zinc finger, NHR/GATA-type / 2-Layer Sandwich / Alpha Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト)
synthetic construct (人工物) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / 解像度: 2.3 Å シンクロトロン / 解像度: 2.3 Å |
|---|
 データ登録者 データ登録者 | Su, X.D. / Lian, T. / Jin, J. |
|---|
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Published
タイトル: The effects of cytosine methylation on general transcription factors
著者: Jin, J. / Lian, T. / SU, X.D. |
|---|
| 履歴 | | 登録 | 2015年11月6日 | 登録サイト: RCSB / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2016年6月29日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2020年2月19日 | Group: Data collection / Derived calculations / カテゴリ: diffrn_source / pdbx_struct_oper_list
Item: _diffrn_source.pdbx_synchrotron_site / _pdbx_struct_oper_list.symmetry_operation |
|---|
| 改定 1.2 | 2024年3月20日 | Group: Data collection / Database references / Derived calculations
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / struct_conn
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_conn.conn_type_id / _struct_conn.id / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン / 解像度: 2.3 Å
シンクロトロン / 解像度: 2.3 Å  データ登録者
データ登録者 引用
引用 ジャーナル: To Be Published
ジャーナル: To Be Published 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5emc.cif.gz
5emc.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5emc.ent.gz
pdb5emc.ent.gz PDB形式
PDB形式 5emc.json.gz
5emc.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 5emc_validation.pdf.gz
5emc_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 5emc_full_validation.pdf.gz
5emc_full_validation.pdf.gz 5emc_validation.xml.gz
5emc_validation.xml.gz 5emc_validation.cif.gz
5emc_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/em/5emc
https://data.pdbj.org/pub/pdb/validation_reports/em/5emc ftp://data.pdbj.org/pub/pdb/validation_reports/em/5emc
ftp://data.pdbj.org/pub/pdb/validation_reports/em/5emc リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: NR3C1, GRL
Homo sapiens (ヒト) / 遺伝子: NR3C1, GRL X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  Photon Factory
Photon Factory  / ビームライン: BL-17A / 波長: 0.98 Å
/ ビームライン: BL-17A / 波長: 0.98 Å 解析
解析 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj
















































