[English] 日本語
 Yorodumi
Yorodumi- PDB-4z2x: Crystal structure of a RNA binding domain of a U2 small nuclear r... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4z2x | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of a RNA binding domain of a U2 small nuclear ribonucleoprotein auxiliary factor 2 (U2AF) from mouse at 2.15 A resolution | ||||||
 Components Components | Splicing factor U2AF 65 kDa subunit | ||||||
 Keywords Keywords | RNA BINDING PROTEIN / Canonical RNA binding protein / RNA Splicing / Structural Genomics / Joint Center for Structural Genomics / JCSG / Protein Structure Initiative / PSI-BIOLOGY / Partnership for T-Cell Biology / TCELL | ||||||
| Function / homology |  Function and homology information Function and homology informationmRNA 3'-end processing / RNA Polymerase II Transcription Termination / Transport of Mature mRNA derived from an Intron-Containing Transcript / Protein hydroxylation / mRNA Splicing - Major Pathway / U2AF complex / poly-pyrimidine tract binding / pre-mRNA 3'-splice site binding / C2H2 zinc finger domain binding / commitment complex ...mRNA 3'-end processing / RNA Polymerase II Transcription Termination / Transport of Mature mRNA derived from an Intron-Containing Transcript / Protein hydroxylation / mRNA Splicing - Major Pathway / U2AF complex / poly-pyrimidine tract binding / pre-mRNA 3'-splice site binding / C2H2 zinc finger domain binding / commitment complex / U2-type prespliceosome / molecular function inhibitor activity / negative regulation of mRNA splicing, via spliceosome / spliceosomal complex assembly / Prp19 complex / negative regulation of protein ubiquitination / RNA splicing / positive regulation of RNA splicing / spliceosomal complex / mRNA splicing, via spliceosome / nuclear speck / enzyme binding / nucleus Similarity search - Function | ||||||
| Biological species |  | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / MOLECULAR REPLACEMENT /  molecular replacement / Resolution: 2.15 Å molecular replacement / Resolution: 2.15 Å | ||||||
 Authors Authors | Joint Center for Structural Genomics (JCSG) / Partnership for T-Cell Biology (TCELL) | ||||||
 Citation Citation |  Journal: To be published Journal: To be publishedTitle: Crystal structure of a RNA binding domain of a U2 small nuclear ribonucleoprotein auxiliary factor 2 (U2AF) from mouse at 2.15 A resolution Authors: Joint Center for Structural Genomics (JCSG) / Partnership for T-Cell Biology (TCELL) | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4z2x.cif.gz 4z2x.cif.gz | 99.5 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4z2x.ent.gz pdb4z2x.ent.gz | 75 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4z2x.json.gz 4z2x.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/z2/4z2x https://data.pdbj.org/pub/pdb/validation_reports/z2/4z2x ftp://data.pdbj.org/pub/pdb/validation_reports/z2/4z2x ftp://data.pdbj.org/pub/pdb/validation_reports/z2/4z2x | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  3v4mS S: Starting model for refinement |
|---|---|
| Similar structure data | |
| Other databases |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 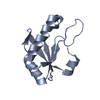
| ||||||||
| 2 | 
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein | Mass: 12033.667 Da / Num. of mol.: 2 / Fragment: RNA binding domain (UNP residues 371-475) Source method: isolated from a genetically manipulated source Source: (gene. exp.)   #2: Water | ChemComp-HOH / | Sequence details | THE CRYSTALLIZATION CONTAINED TWO DIFFERENT CONSTRUCTS OF UNIPROTKB P26369. THE TAGS WERE REMOVED ...THE CRYSTALLIZ | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.1 Å3/Da / Density % sol: 41.46 % |
|---|---|
| Crystal grow | Temperature: 277 K / Method: vapor diffusion, sitting drop Details: 0.2M sodium thiocyanate, 20% polyethylene glycol 3350 |
-Data collection
| Diffraction | Mean temperature: 100 K | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SSRL SSRL  / Beamline: BL11-1 / Wavelength: 0.97879 Å / Beamline: BL11-1 / Wavelength: 0.97879 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: DECTRIS PILATUS 6M / Detector: PIXEL / Date: Jul 2, 2013 Details: Flat mirror (vertical focusing); single crystal Si(111) bent monochromator (horizontal focusing) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Monochromator: single crystal Si(111) bent / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 0.97879 Å / Relative weight: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 2.15→37.9 Å / Num. obs: 11422 / % possible obs: 98.2 % / Observed criterion σ(I): -3 / Redundancy: 3.782 % / Biso Wilson estimate: 35.62 Å2 / Rmerge F obs: 0.998 / Rmerge(I) obs: 0.098 / Rrim(I) all: 0.113 / Net I/σ(I): 12.09 / Num. measured all: 43198 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell |
|
-Phasing
| Phasing | Method:  molecular replacement molecular replacement |
|---|
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 3v4m Resolution: 2.15→37.9 Å / Cor.coef. Fo:Fc: 0.9378 / Cor.coef. Fo:Fc free: 0.9046 / Occupancy max: 1 / Occupancy min: 0.5 / Cross valid method: THROUGHOUT / σ(F): 0 Details: 1. ATOM RECORD CONTAINS SUM OF TLS AND RESIDUAL B FACTORS. ANISOU RECORD CONTAINS SUM OF TLS AND RESIDUAL U FACTORS. 2. NCS RESTRAINTS WERE APPLIED USING BUSTER'S LSSR RESTRAINT REPRESENTATION (-AUTONCS)
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 139.08 Å2 / Biso mean: 46.7017 Å2 / Biso min: 22.07 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.336 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.15→37.9 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 2.15→2.35 Å / Total num. of bins used: 6
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj
