| 登録情報 | データベース: PDB / ID: 4qvb
|
|---|
| タイトル | Mycobacterium tuberculosis protein Rv1155 in complex with co-enzyme F420 |
|---|
 要素 要素 | Rv1155 protein |
|---|
 キーワード キーワード | OXIDOREDUCTASE |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
vitamin B6 metabolic process / coenzyme F420 binding / oxidoreductase activity, acting on the CH-CH group of donors / 酸化還元酵素 / pyridoxal phosphate binding / FMN binding / protein homodimerization activity類似検索 - 分子機能 F420-binding domain, putative / : / Pyridoxamine 5'-phosphate oxidase, putative / Pyridoxamine 5'-phosphate oxidase / Electron Transport, Fmn-binding Protein; Chain A / Pnp Oxidase; Chain A / FMN-binding split barrel / Roll / Mainly Beta類似検索 - ドメイン・相同性 COENZYME F420 / FORMIC ACID / 1,3-PROPANDIOL / S-1,2-PROPANEDIOL / : / F420H(2)-dependent reductase Rv1155類似検索 - 構成要素 |
|---|
| 生物種 |   Mycobacterium tuberculosis (結核菌) Mycobacterium tuberculosis (結核菌) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.3 Å 分子置換 / 解像度: 2.3 Å |
|---|
 データ登録者 データ登録者 | Mashalidis, E.H. / Gittis, A.G. / Tomczak, A. / Abell, C. / Barry III, C.E. / Garboczi, D.N. |
|---|
 引用 引用 |  ジャーナル: Protein Sci. / 年: 2015 ジャーナル: Protein Sci. / 年: 2015
タイトル: Molecular insights into the binding of coenzyme F420 to the conserved protein Rv1155 from Mycobacterium tuberculosis.
著者: Mashalidis, E.H. / Gittis, A.G. / Tomczak, A. / Abell, C. / Barry, C.E. / Garboczi, D.N. |
|---|
| 履歴 | | 登録 | 2014年7月14日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2015年2月25日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2015年5月20日 | Group: Database references |
|---|
| 改定 1.2 | 2024年2月28日 | Group: Data collection / Database references / Derived calculations
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / struct_ref_seq_dif / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.3 Å
分子置換 / 解像度: 2.3 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Protein Sci. / 年: 2015
ジャーナル: Protein Sci. / 年: 2015 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 4qvb.cif.gz
4qvb.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb4qvb.ent.gz
pdb4qvb.ent.gz PDB形式
PDB形式 4qvb.json.gz
4qvb.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 4qvb_validation.pdf.gz
4qvb_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 4qvb_full_validation.pdf.gz
4qvb_full_validation.pdf.gz 4qvb_validation.xml.gz
4qvb_validation.xml.gz 4qvb_validation.cif.gz
4qvb_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/qv/4qvb
https://data.pdbj.org/pub/pdb/validation_reports/qv/4qvb ftp://data.pdbj.org/pub/pdb/validation_reports/qv/4qvb
ftp://data.pdbj.org/pub/pdb/validation_reports/qv/4qvb リンク
リンク 集合体
集合体
 要素
要素


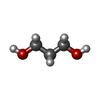

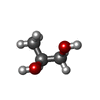
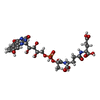








 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 22-BM / 波長: 1 Å
/ ビームライン: 22-BM / 波長: 1 Å 解析
解析 分子置換 / 解像度: 2.3→38.532 Å / SU ML: 0.34 / σ(F): 1.34 / 位相誤差: 28.64 / 立体化学のターゲット値: ML
分子置換 / 解像度: 2.3→38.532 Å / SU ML: 0.34 / σ(F): 1.34 / 位相誤差: 28.64 / 立体化学のターゲット値: ML ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj





