+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 4o72 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Crystal structure of the first bromodomain of human BRD4 in complex with NU7441 | ||||||
 要素 要素 | Bromodomain-containing protein 4 | ||||||
 キーワード キーワード | TRANSCRIPTION/INHIBITOR / BROMODOMAIN / CAP / HUNK1 / MCAP / PROTEIN BINDING-INHIBITOR COMPLEX / MITOTIC CHROMOSOME ASSOCIATED PROTEIN / CELL CYCLE / INHIBITOR / TRANSCRIPTION-INHIBITOR complex | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RNA polymerase II C-terminal domain binding / negative regulation of DNA damage checkpoint / P-TEFb complex binding / negative regulation by host of viral transcription / positive regulation of T-helper 17 cell lineage commitment / positive regulation of G2/M transition of mitotic cell cycle / histone reader activity / RNA polymerase II CTD heptapeptide repeat kinase activity / condensed nuclear chromosome / positive regulation of transcription elongation by RNA polymerase II ...RNA polymerase II C-terminal domain binding / negative regulation of DNA damage checkpoint / P-TEFb complex binding / negative regulation by host of viral transcription / positive regulation of T-helper 17 cell lineage commitment / positive regulation of G2/M transition of mitotic cell cycle / histone reader activity / RNA polymerase II CTD heptapeptide repeat kinase activity / condensed nuclear chromosome / positive regulation of transcription elongation by RNA polymerase II / transcription coregulator activity / lysine-acetylated histone binding / p53 binding / chromosome / regulation of inflammatory response / positive regulation of canonical NF-kappaB signal transduction / Potential therapeutics for SARS / transcription coactivator activity / transcription cis-regulatory region binding / chromatin remodeling / DNA damage response / chromatin binding / regulation of transcription by RNA polymerase II / positive regulation of DNA-templated transcription / enzyme binding / positive regulation of transcription by RNA polymerase II / nucleoplasm / nucleus 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 1.4 Å 分子置換 / 解像度: 1.4 Å | ||||||
 データ登録者 データ登録者 | Zhu, J.-Y. / Ember, S.W. / Watts, C. / Schonbrunn, E. | ||||||
 引用 引用 |  ジャーナル: Acs Chem.Biol. / 年: 2014 ジャーナル: Acs Chem.Biol. / 年: 2014タイトル: Acetyl-lysine Binding Site of Bromodomain-Containing Protein 4 (BRD4) Interacts with Diverse Kinase Inhibitors. 著者: Ember, S.W. / Zhu, J.Y. / Olesen, S.H. / Martin, M.P. / Becker, A. / Berndt, N. / Georg, G.I. / Schonbrunn, E. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  4o72.cif.gz 4o72.cif.gz | 98.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb4o72.ent.gz pdb4o72.ent.gz | 75.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  4o72.json.gz 4o72.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  4o72_validation.pdf.gz 4o72_validation.pdf.gz | 757.5 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  4o72_full_validation.pdf.gz 4o72_full_validation.pdf.gz | 758.7 KB | 表示 | |
| XML形式データ |  4o72_validation.xml.gz 4o72_validation.xml.gz | 9.9 KB | 表示 | |
| CIF形式データ |  4o72_validation.cif.gz 4o72_validation.cif.gz | 13.9 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/o7/4o72 https://data.pdbj.org/pub/pdb/validation_reports/o7/4o72 ftp://data.pdbj.org/pub/pdb/validation_reports/o7/4o72 ftp://data.pdbj.org/pub/pdb/validation_reports/o7/4o72 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  4o70C  4o71C  4o74C  4o75C 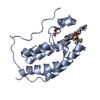 4o76C  4o77C  4o78C  4o7aC  4o7bC  4o7cC  4o7eC  4o7fC  4ps5C  2ossS C: 同じ文献を引用 ( S: 精密化の開始モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 1分子 A
| #1: タンパク質 | 分子量: 15099.380 Da / 分子数: 1 / 断片: UNP residues 44-168 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: BRD4, HUNK1 / プラスミド: PNIC28-BSA4 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: BRD4, HUNK1 / プラスミド: PNIC28-BSA4 / 発現宿主:  |
|---|
-非ポリマー , 5種, 203分子 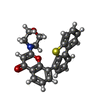








| #2: 化合物 | ChemComp-2R4 / | ||||
|---|---|---|---|---|---|
| #3: 化合物 | ChemComp-PEG / | ||||
| #4: 化合物 | ChemComp-EDO / #5: 化合物 | #6: 水 | ChemComp-HOH / | |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.14 Å3/Da / 溶媒含有率: 42.59 % |
|---|---|
| 結晶化 | 温度: 291 K / 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 7.5 詳細: 12.5 MG/ML BRD4, 5MM HEPES pH 7.5, 50MM SODIUM CHLORIDE, 0.5MM DTT, 50MM TRIS PH8.5, 0.1M AMMONIUM SULFATE, 12.5% PEG 3,350, 10% DMSO, 1 MM NU7441, VAPOR DIFFUSION, HANGING DROP, temperature 291K |
-データ収集
| 回折 | 平均測定温度: 93 K |
|---|---|
| 放射光源 | 由来:  回転陽極 / タイプ: RIGAKU MICROMAX-007 HF / 波長: 1.54178 Å 回転陽極 / タイプ: RIGAKU MICROMAX-007 HF / 波長: 1.54178 Å |
| 検出器 | タイプ: RIGAKU SATURN 944+ / 検出器: CCD / 日付: 2013年11月22日 / 詳細: MIRRORS |
| 放射 | モノクロメーター: MIRRORS / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.54178 Å / 相対比: 1 |
| 反射 | 解像度: 1.4→20 Å / Num. obs: 26039 / % possible obs: 99 % / Observed criterion σ(I): -3 / 冗長度: 3.4 % / Rsym value: 0.03 / Net I/σ(I): 25.4 |
| 反射 シェル | 解像度: 1.4→1.44 Å / 冗長度: 1.8 % / Mean I/σ(I) obs: 4 / Rsym value: 0.166 / % possible all: 92.6 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: PDB entry 2OSS 解像度: 1.4→19.652 Å / SU ML: 0.11 / σ(F): 1.37 / 位相誤差: 13.79 / 立体化学のターゲット値: ML
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å / 溶媒モデル: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.4→19.652 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
|
 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj



