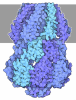
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4m75 | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of Lsm1-7 complex | ||||||
 Components Components | (U6 snRNA-associated Sm-like protein ...) x 7 | ||||||
 Keywords Keywords | RNA BINDING PROTEIN / Sm Like Protein / RNA splicing / STRUCTURAL PROTEIN | ||||||
| Function / homology |  Function and homology information Function and homology informationmRNA decay by 5' to 3' exoribonuclease / Lsm1-7-Pat1 complex / U6 snRNP / deadenylation-dependent decapping of nuclear-transcribed mRNA / U4/U6 snRNP / sno(s)RNA-containing ribonucleoprotein complex / spliceosomal tri-snRNP complex / nuclear-transcribed mRNA catabolic process, deadenylation-dependent decay / P-body assembly / U2-type prespliceosome ...mRNA decay by 5' to 3' exoribonuclease / Lsm1-7-Pat1 complex / U6 snRNP / deadenylation-dependent decapping of nuclear-transcribed mRNA / U4/U6 snRNP / sno(s)RNA-containing ribonucleoprotein complex / spliceosomal tri-snRNP complex / nuclear-transcribed mRNA catabolic process, deadenylation-dependent decay / P-body assembly / U2-type prespliceosome / tRNA processing / precatalytic spliceosome / nuclear-transcribed mRNA catabolic process / spliceosomal snRNP assembly / U6 snRNA binding / U4/U6 x U5 tri-snRNP complex / cellular response to glucose starvation / catalytic step 2 spliceosome / spliceosomal complex / maturation of SSU-rRNA / P-body / mRNA splicing, via spliceosome / mRNA processing / rRNA processing / ribonucleoprotein complex / mRNA binding / chromatin binding / nucleolus / RNA binding / nucleus / cytoplasm Similarity search - Function | ||||||
| Biological species |  | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.95 Å MOLECULAR REPLACEMENT / Resolution: 2.95 Å | ||||||
 Authors Authors | Zhou, L. / Hang, J. / Zhou, Y. / Wan, R. / Lu, G. / Yan, C. / Shi, Y. | ||||||
 Citation Citation |  Journal: Nature / Year: 2014 Journal: Nature / Year: 2014Title: Crystal structures of the Lsm complex bound to the 3' end sequence of U6 small nuclear RNA. Authors: Zhou, L. / Hang, J. / Zhou, Y. / Wan, R. / Lu, G. / Yin, P. / Yan, C. / Shi, Y. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4m75.cif.gz 4m75.cif.gz | 490.2 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4m75.ent.gz pdb4m75.ent.gz | 406 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4m75.json.gz 4m75.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/m7/4m75 https://data.pdbj.org/pub/pdb/validation_reports/m7/4m75 ftp://data.pdbj.org/pub/pdb/validation_reports/m7/4m75 ftp://data.pdbj.org/pub/pdb/validation_reports/m7/4m75 | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  4m77C  4m78C  4m7aC  4m7dC  1i81S C: citing same article ( S: Starting model for refinement |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| Unit cell |
|
- Components
Components
-U6 snRNA-associated Sm-like protein ... , 7 types, 14 molecules AHBICJDKELFMGN
| #1: Protein | Mass: 17473.814 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Strain: ATCC 204508 / S288c / Gene: LSM1, SPB8, YJL124C, J0714 / Production host:  #2: Protein | Mass: 11302.508 Da / Num. of mol.: 2 / Mutation: C45S Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Strain: ATCC 204508 / S288c / Gene: LSM2, SMX5, SNP3, YBL026W, YBL0425 / Production host:  #3: Protein | Mass: 10100.921 Da / Num. of mol.: 2 / Mutation: C37S,C63S Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Strain: ATCC 204508 / S288c / Gene: LSM3, SMX4, USS2, YLR438C-A / Production host:  #4: Protein | Mass: 9547.265 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Strain: ATCC 204508 / S288c / Production host:  #5: Protein | Mass: 10573.641 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Strain: ATCC 204508 / S288c / Gene: LSM5, YER146W / Production host:  #6: Protein | Mass: 13261.521 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Strain: ATCC 204508 / S288c / Production host:  #7: Protein | Mass: 14088.342 Da / Num. of mol.: 2 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Strain: ATCC 204508 / S288c / Production host:  |
|---|
-Non-polymers , 1 types, 2 molecules 
| #8: Chemical |
|---|
-Details
| Has protein modification | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.13 Å3/Da / Density % sol: 42.35 % |
|---|---|
| Crystal grow | Temperature: 291 K / Method: vapor diffusion, hanging drop / pH: 6.5 Details: 100mM MES 6.5, 25% PEG600, 20mM CaCl2, VAPOR DIFFUSION, HANGING DROP, temperature 291K |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SSRF SSRF  / Beamline: BL17U / Wavelength: 0.9795 Å / Beamline: BL17U / Wavelength: 0.9795 Å |
| Detector | Type: ADSC QUANTUM 315r / Detector: CCD / Date: Jan 11, 2012 / Details: mirrors |
| Radiation | Monochromator: Si 111 CHANNEL / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 0.9795 Å / Relative weight: 1 |
| Reflection | Resolution: 2.95→40 Å / % possible obs: 98.5 % / Observed criterion σ(F): 1 / Observed criterion σ(I): 1 |
| Reflection shell | Resolution: 2.95→3.06 Å / % possible all: 98.2 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: PDB ENTRY 1I81 Resolution: 2.95→38.66 Å / SU ML: 0.56 / σ(F): 0.89 / Phase error: 31.7 / Stereochemistry target values: ML
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.98 Å / VDW probe radii: 1.2 Å / Solvent model: FLAT BULK SOLVENT MODEL / Bsol: 52.09 Å2 / ksol: 0.31 e/Å3 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.95→38.66 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller













 PDBj
PDBj