+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4lr2 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Crystal Structure of Human ENPP4 (apo) | |||||||||
 Components Components | Bis(5'-adenosyl)-triphosphatase ENPP4 | |||||||||
 Keywords Keywords | HYDROLASE / NPP4 / ENPP4 / phosphodiesterase | |||||||||
| Function / homology |  Function and homology information Function and homology informationpurine ribonucleoside catabolic process / bis(5'-adenosyl)-triphosphatase / bis(5'-adenosyl)-triphosphatase activity / ficolin-1-rich granule membrane / positive regulation of blood coagulation / blood coagulation / Neutrophil degranulation / extracellular exosome / metal ion binding / membrane / plasma membrane Similarity search - Function | |||||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human) | |||||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 1.5 Å MOLECULAR REPLACEMENT / Resolution: 1.5 Å | |||||||||
 Authors Authors | Albright, R.A. / Braddock, D.T. | |||||||||
 Citation Citation |  Journal: J.Biol.Chem. / Year: 2014 Journal: J.Biol.Chem. / Year: 2014Title: Molecular basis of purinergic signal metabolism by ectonucleotide pyrophosphatase/phosphodiesterases 4 and 1 and implications in stroke. Authors: Albright, R.A. / Ornstein, D.L. / Cao, W. / Chang, W.C. / Robert, D. / Tehan, M. / Hoyer, D. / Liu, L. / Stabach, P. / Yang, G. / De La Cruz, E.M. / Braddock, D.T. #1: Journal: Blood / Year: 2012 Title: NPP4 is a procoagulant enzyme on the surface of vascular endothelium Authors: Albright, R.A. / Chang, W.C. / Robert, D. / Ornstein, D.L. / Cao, W. / Liu, L. / Redick, M.E. / Young, J.I. / De La Cruz, E.M. / Braddock, D.T. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4lr2.cif.gz 4lr2.cif.gz | 186.4 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4lr2.ent.gz pdb4lr2.ent.gz | 143.3 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4lr2.json.gz 4lr2.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Summary document |  4lr2_validation.pdf.gz 4lr2_validation.pdf.gz | 818.2 KB | Display |  wwPDB validaton report wwPDB validaton report |
|---|---|---|---|---|
| Full document |  4lr2_full_validation.pdf.gz 4lr2_full_validation.pdf.gz | 820.1 KB | Display | |
| Data in XML |  4lr2_validation.xml.gz 4lr2_validation.xml.gz | 20.9 KB | Display | |
| Data in CIF |  4lr2_validation.cif.gz 4lr2_validation.cif.gz | 32.9 KB | Display | |
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/lr/4lr2 https://data.pdbj.org/pub/pdb/validation_reports/lr/4lr2 ftp://data.pdbj.org/pub/pdb/validation_reports/lr/4lr2 ftp://data.pdbj.org/pub/pdb/validation_reports/lr/4lr2 | HTTPS FTP |
-Related structure data
| Related structure data |  4lqyC  2gsuS  4lr0  4lr1  4lr5 C: citing same article ( S: Starting model for refinement |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| Unit cell |
| |||||||||
| Components on special symmetry positions |
|
- Components
Components
-Protein , 1 types, 1 molecules A
| #1: Protein | Mass: 46109.957 Da / Num. of mol.: 1 / Fragment: UNP residues 25-402 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Gene: ENPP4, KIAA0879, NPP4 / Plasmid: pFASTBAC1 / Production host: Homo sapiens (human) / Gene: ENPP4, KIAA0879, NPP4 / Plasmid: pFASTBAC1 / Production host:  Trichoplusia ni (cabbage looper) / Strain (production host): HIGH5 Trichoplusia ni (cabbage looper) / Strain (production host): HIGH5References: UniProt: Q9Y6X5, bis(5'-adenosyl)-triphosphatase |
|---|
-Sugars , 2 types, 3 molecules 
| #2: Polysaccharide | 2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose Source method: isolated from a genetically manipulated source |
|---|---|
| #3: Sugar |
-Non-polymers , 3 types, 502 molecules 
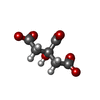



| #4: Chemical | | #5: Chemical | ChemComp-FLC / | #6: Water | ChemComp-HOH / | |
|---|
-Details
| Has protein modification | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.77 Å3/Da / Density % sol: 55.64 % |
|---|
-Data collection
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  CHESS CHESS  / Beamline: A1 / Wavelength: 0.978 Å / Beamline: A1 / Wavelength: 0.978 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Detector | Type: ADSC QUANTUM 210 / Detector: CCD / Date: Jun 3, 2013 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 0.978 Å / Relative weight: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 1.5→50 Å / Num. obs: 71681 / % possible obs: 93.6 % / Redundancy: 6.8 % / Rmerge(I) obs: 0.084 / Χ2: 1.023 / Net I/σ(I): 14.3 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell |
|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: PDB ID 2GSU WITHOUT LIGAND Resolution: 1.5→22.73 Å / Occupancy max: 1 / Occupancy min: 1 / FOM work R set: 0.8631 / SU ML: 0.16 / σ(F): 1.37 / Phase error: 21.21 / Stereochemistry target values: ML
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 70.86 Å2 / Biso mean: 25.7043 Å2 / Biso min: 8.61 Å2 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.5→22.73 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 26
|
 Movie
Movie Controller
Controller













 PDBj
PDBj









