+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4ft3 | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal Structure of the CHK1 | ||||||
 Components Components | Serine/threonine-protein kinase Chk1 | ||||||
 Keywords Keywords | TRANSFERASE/TRANSFERASE inhibitor / TRANSFERASE / TRANSFERASE-TRANSFERASE inhibitor complex | ||||||
| Function / homology |  Function and homology information Function and homology informationnegative regulation of mitotic nuclear division / apoptotic process involved in development / negative regulation of G0 to G1 transition / histone H3T11 kinase activity / regulation of mitotic centrosome separation / mitotic G2/M transition checkpoint / peptidyl-threonine phosphorylation / inner cell mass cell proliferation / regulation of double-strand break repair via homologous recombination / nucleus organization ...negative regulation of mitotic nuclear division / apoptotic process involved in development / negative regulation of G0 to G1 transition / histone H3T11 kinase activity / regulation of mitotic centrosome separation / mitotic G2/M transition checkpoint / peptidyl-threonine phosphorylation / inner cell mass cell proliferation / regulation of double-strand break repair via homologous recombination / nucleus organization / negative regulation of gene expression, epigenetic / mitotic G2 DNA damage checkpoint signaling / Transcriptional Regulation by E2F6 / replicative senescence / Presynaptic phase of homologous DNA pairing and strand exchange / Activation of ATR in response to replication stress / Chk1/Chk2(Cds1) mediated inactivation of Cyclin B:Cdk1 complex / signal transduction in response to DNA damage / positive regulation of cell cycle / DNA damage checkpoint signaling / regulation of signal transduction by p53 class mediator / replication fork / condensed nuclear chromosome / TP53 Regulates Transcription of DNA Repair Genes / cellular response to mechanical stimulus / Signaling by SCF-KIT / G2/M DNA damage checkpoint / Ubiquitin-Mediated Degradation of Phosphorylated Cdc25A / G2/M transition of mitotic cell cycle / regulation of cell population proliferation / Processing of DNA double-strand break ends / Regulation of TP53 Activity through Phosphorylation / protein phosphorylation / protein kinase activity / DNA replication / non-specific serine/threonine protein kinase / chromatin remodeling / protein domain specific binding / protein serine kinase activity / DNA repair / protein serine/threonine kinase activity / apoptotic process / DNA damage response / centrosome / chromatin / protein-containing complex / : / nucleoplasm / ATP binding / nucleus / cytoplasm / cytosol Similarity search - Function | ||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  MOLECULAR REPLACEMENT / Resolution: 2.5 Å MOLECULAR REPLACEMENT / Resolution: 2.5 Å | ||||||
 Authors Authors | Kang, Y.N. / Stuckey, J.A. / Chang, P. / Russell, A.J. | ||||||
 Citation Citation |  Journal: To be Published Journal: To be PublishedTitle: Crystal Structure of the CHK1 Authors: Kang, Y.N. / Stuckey, J.A. / Chang, P. / Russell, A.J. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4ft3.cif.gz 4ft3.cif.gz | 128.7 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4ft3.ent.gz pdb4ft3.ent.gz | 99.5 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4ft3.json.gz 4ft3.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/ft/4ft3 https://data.pdbj.org/pub/pdb/validation_reports/ft/4ft3 ftp://data.pdbj.org/pub/pdb/validation_reports/ft/4ft3 ftp://data.pdbj.org/pub/pdb/validation_reports/ft/4ft3 | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  4fsmC  4fsnC  4fsqC  4fsrC  4fstC  4fsuC  4fswC  4fsyC  4fszC  4ft0C  4ft5C  4ft7C  4ft9C  4ftaC  4ftcC  4ftiC  4ftjC  4ftkC  4ftlC  4ftmC  4ftnC  4ftoC  4ftqC  4ftrC  4fttC  4ftuC  4gh2C  4ft1 C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein , 1 types, 1 molecules A
| #1: Protein | Mass: 32186.049 Da / Num. of mol.: 1 / Fragment: unp residues 2-280 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Strain: human / Gene: CHEK1, CHK1 / Production host: Homo sapiens (human) / Strain: human / Gene: CHEK1, CHK1 / Production host:  HOMO SAPIENS (human) HOMO SAPIENS (human)References: UniProt: O14757, non-specific serine/threonine protein kinase |
|---|
-Non-polymers , 5 types, 193 molecules 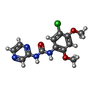







| #2: Chemical | ChemComp-H1K / | ||
|---|---|---|---|
| #3: Chemical | ChemComp-SO4 / | ||
| #4: Chemical | ChemComp-GOL / | ||
| #5: Chemical | ChemComp-IPA / #6: Water | ChemComp-HOH / | |
-Details
| Has protein modification | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.65 Å3/Da / Density % sol: 53.67 % |
|---|---|
| Crystal grow | Temperature: 298 K / Method: vapor diffusion, sitting drop / pH: 7.5 Details: PEG 8000, Isopropanol, HEPES, pH 7.5, VAPOR DIFFUSION, SITTING DROP, temperature 298.0K |
-Data collection
| Diffraction | Mean temperature: 110 K | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  ROTATING ANODE / Type: RIGAKU RU200 / Wavelength: 1.54 Å ROTATING ANODE / Type: RIGAKU RU200 / Wavelength: 1.54 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: MARRESEARCH / Detector: IMAGE PLATE / Details: mirrors | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Monochromator: Osmic Si / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 1.54 Å / Relative weight: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 2.1→20 Å / Num. all: 19845 / Num. obs: 17166 / % possible obs: 86.5 % / Observed criterion σ(I): -3 / Rmerge(I) obs: 0.097 / Χ2: 1.002 / Net I/σ(I): 15 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell |
|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT / Resolution: 2.5→19.95 Å / Cor.coef. Fo:Fc: 0.9392 / Cor.coef. Fo:Fc free: 0.9098 / Occupancy max: 1 / Occupancy min: 0 / SU R Cruickshank DPI: 0.476 / Cross valid method: THROUGHOUT / σ(F): 0 MOLECULAR REPLACEMENT / Resolution: 2.5→19.95 Å / Cor.coef. Fo:Fc: 0.9392 / Cor.coef. Fo:Fc free: 0.9098 / Occupancy max: 1 / Occupancy min: 0 / SU R Cruickshank DPI: 0.476 / Cross valid method: THROUGHOUT / σ(F): 0
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 115.24 Å2 / Biso mean: 29.4545 Å2 / Biso min: 4.14 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.232 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.5→19.95 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 2.5→2.74 Å / Total num. of bins used: 6
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller













 PDBj
PDBj
















