| 登録情報 | データベース: PDB / ID: 3kvm
|
|---|
| タイトル | Crystal structure of human dihydroorotate dehydrogenase (DHODH) with amino-benzoic acid inhibitor 951 at 2.00A resolution |
|---|
 要素 要素 | Dihydroorotate dehydrogenase, mitochondrial |
|---|
 キーワード キーワード | OXIDOREDUCTASE / PROTEIN-ANTIPROLIFERATIVE AGENT COMPLEX / Flavoprotein / FMN / Membrane / Mitochondrion / Mitochondrion inner membrane / Polymorphism / Pyrimidine biosynthesis / Transit peptide / Transmembrane |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
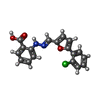
pyrimidine ribonucleotide biosynthetic process / dihydroorotate dehydrogenase (quinone) / dihydroorotate dehydrogenase (quinone) activity / dihydroorotate dehydrogenase activity / dihydroorotase activity / Pyrimidine biosynthesis / UDP biosynthetic process / 'de novo' UMP biosynthetic process / 'de novo' pyrimidine nucleobase biosynthetic process / mitochondrial inner membrane ...pyrimidine ribonucleotide biosynthetic process / dihydroorotate dehydrogenase (quinone) / dihydroorotate dehydrogenase (quinone) activity / dihydroorotate dehydrogenase activity / dihydroorotase activity / Pyrimidine biosynthesis / UDP biosynthetic process / 'de novo' UMP biosynthetic process / 'de novo' pyrimidine nucleobase biosynthetic process / mitochondrial inner membrane / mitochondrion / nucleoplasm / cytosol類似検索 - 分子機能 Dihydroorotate dehydrogenase, class 2 / Dihydroorotate dehydrogenase signature 1. / Dihydroorotate dehydrogenase signature 2. / Dihydroorotate dehydrogenase, conserved site / : / Dihydroorotate dehydrogenase domain / Dihydroorotate dehydrogenase / Aldolase class I / Aldolase-type TIM barrel / TIM Barrel ...Dihydroorotate dehydrogenase, class 2 / Dihydroorotate dehydrogenase signature 1. / Dihydroorotate dehydrogenase signature 2. / Dihydroorotate dehydrogenase, conserved site / : / Dihydroorotate dehydrogenase domain / Dihydroorotate dehydrogenase / Aldolase class I / Aldolase-type TIM barrel / TIM Barrel / Alpha-Beta Barrel / Alpha Beta類似検索 - ドメイン・相同性 Chem-951 / ACETATE ION / UNDECYLAMINE-N,N-DIMETHYL-N-OXIDE / Chem-DOR / FLAVIN MONONUCLEOTIDE / Dihydroorotate dehydrogenase (quinone), mitochondrial類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 2 Å 分子置換 / 解像度: 2 Å |
|---|
 データ登録者 データ登録者 | McLean, L. / Zhang, Y. |
|---|
 引用 引用 |  ジャーナル: Bioorg.Med.Chem.Lett. / 年: 2010 ジャーナル: Bioorg.Med.Chem.Lett. / 年: 2010
タイトル: Discovery of novel inhibitors for DHODH via virtual screening and X-ray crystallographic structures.
著者: McLean, L.R. / Zhang, Y. / Degnen, W. / Peppard, J. / Cabel, D. / Zou, C. / Tsay, J.T. / Subramaniam, A. / Vaz, R.J. / Li, Y. |
|---|
| 履歴 | | 登録 | 2009年11月30日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2010年3月2日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2017年11月1日 | Group: Refinement description / カテゴリ: software |
|---|
| 改定 1.3 | 2023年9月6日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / struct_ref_seq_dif / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  分子置換 / 解像度: 2 Å
分子置換 / 解像度: 2 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Bioorg.Med.Chem.Lett. / 年: 2010
ジャーナル: Bioorg.Med.Chem.Lett. / 年: 2010 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 3kvm.cif.gz
3kvm.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb3kvm.ent.gz
pdb3kvm.ent.gz PDB形式
PDB形式 3kvm.json.gz
3kvm.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/kv/3kvm
https://data.pdbj.org/pub/pdb/validation_reports/kv/3kvm ftp://data.pdbj.org/pub/pdb/validation_reports/kv/3kvm
ftp://data.pdbj.org/pub/pdb/validation_reports/kv/3kvm リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: DHODH / プラスミド: PET19B / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: DHODH / プラスミド: PET19B / 発現宿主: 











 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 回転陽極 / タイプ: RIGAKU RUH3R / 波長: 1.5418 Å
回転陽極 / タイプ: RIGAKU RUH3R / 波長: 1.5418 Å 分子置換
分子置換 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー

















 PDBj
PDBj






