+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 3k2s | ||||||
|---|---|---|---|---|---|---|---|
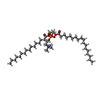
| タイトル | Solution structure of double super helix model | ||||||
 要素 要素 | Apolipoprotein A-I | ||||||
 キーワード キーワード | LIPID BINDING PROTEIN / super double helix / amphipathic / Amyloid / Amyloidosis / Atherosclerosis / Cholesterol metabolism / Disease mutation / Glycation / Glycoprotein / HDL / Lipid metabolism / Lipid transport / Lipoprotein / Neuropathy / Palmitate / Secreted / Steroid metabolism / Transport / HIGH DENSITY LIPOPROTEIN | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Defective ABCA1 causes TGD / high-density lipoprotein particle receptor binding / peptidyl-methionine modification / HDL clearance / spherical high-density lipoprotein particle / Scavenging by Class B Receptors / negative regulation of response to cytokine stimulus / protein oxidation / regulation of intestinal cholesterol absorption / vitamin transport ...Defective ABCA1 causes TGD / high-density lipoprotein particle receptor binding / peptidyl-methionine modification / HDL clearance / spherical high-density lipoprotein particle / Scavenging by Class B Receptors / negative regulation of response to cytokine stimulus / protein oxidation / regulation of intestinal cholesterol absorption / vitamin transport / blood vessel endothelial cell migration / cholesterol import / negative regulation of heterotypic cell-cell adhesion / apolipoprotein A-I receptor binding / ABC transporters in lipid homeostasis / apolipoprotein receptor binding / negative regulation of cell adhesion molecule production / negative regulation of cytokine production involved in immune response / HDL assembly / high-density lipoprotein particle binding / negative regulation of very-low-density lipoprotein particle remodeling / glucocorticoid metabolic process / acylglycerol homeostasis / phosphatidylcholine biosynthetic process / phosphatidylcholine-sterol O-acyltransferase activator activity / positive regulation of phospholipid efflux / Chylomicron remodeling / cellular response to lipoprotein particle stimulus / Chylomicron assembly / high-density lipoprotein particle clearance / phospholipid efflux / chylomicron / high-density lipoprotein particle remodeling / reverse cholesterol transport / positive regulation of cholesterol metabolic process / lipid storage / high-density lipoprotein particle assembly / phospholipid homeostasis / chemorepellent activity / lipoprotein biosynthetic process / cholesterol transfer activity / cholesterol transport / low-density lipoprotein particle / high-density lipoprotein particle / very-low-density lipoprotein particle / endothelial cell proliferation / regulation of Cdc42 protein signal transduction / HDL remodeling / cholesterol efflux / adrenal gland development / Scavenging by Class A Receptors / triglyceride homeostasis / negative regulation of interleukin-1 beta production / negative chemotaxis / cholesterol binding / cholesterol biosynthetic process / amyloid-beta formation / positive regulation of Rho protein signal transduction / positive regulation of cholesterol efflux / endocytic vesicle / negative regulation of tumor necrosis factor-mediated signaling pathway / Scavenging of heme from plasma / Retinoid metabolism and transport / cholesterol metabolic process / positive regulation of stress fiber assembly / heat shock protein binding / endocytic vesicle lumen / positive regulation of substrate adhesion-dependent cell spreading / positive regulation of phagocytosis / cholesterol homeostasis / integrin-mediated signaling pathway / Post-translational protein phosphorylation / Heme signaling / PPARA activates gene expression / phospholipid binding / negative regulation of inflammatory response / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / Platelet degranulation / amyloid-beta binding / extracellular vesicle / cytoplasmic vesicle / secretory granule lumen / blood microparticle / early endosome / protein stabilization / G protein-coupled receptor signaling pathway / endoplasmic reticulum lumen / Amyloid fiber formation / receptor ligand activity / signaling receptor binding / enzyme binding / protein homodimerization activity / : / extracellular exosome / extracellular region / identical protein binding / plasma membrane / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  溶液散乱 / NUCLEAR REACTOR 溶液散乱 / NUCLEAR REACTOR | ||||||
 データ登録者 データ登録者 | Wu, Z. / Gogonea, V. / Lee, X. / Wagner, M.A. / Li, X.-M. / Huang, Y. / Undurti, A. / May, R.P. / Haertlein, M. / Moulin, M. ...Wu, Z. / Gogonea, V. / Lee, X. / Wagner, M.A. / Li, X.-M. / Huang, Y. / Undurti, A. / May, R.P. / Haertlein, M. / Moulin, M. / Gutsche, I. / Zaccai, G. / Didonato, J.A. / Hazen, L.S. | ||||||
 引用 引用 |  ジャーナル: J.Biol.Chem. / 年: 2009 ジャーナル: J.Biol.Chem. / 年: 2009タイトル: Double superhelix model of high density lipoprotein. 著者: Wu, Z. / Gogonea, V. / Lee, X. / Wagner, M.A. / Li, X.M. / Huang, Y. / Undurti, A. / May, R.P. / Haertlein, M. / Moulin, M. / Gutsche, I. / Zaccai, G. / Didonato, J.A. / Hazen, S.L. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3k2s.cif.gz 3k2s.cif.gz | 289.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3k2s.ent.gz pdb3k2s.ent.gz | 293.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3k2s.json.gz 3k2s.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/k2/3k2s https://data.pdbj.org/pub/pdb/validation_reports/k2/3k2s ftp://data.pdbj.org/pub/pdb/validation_reports/k2/3k2s ftp://data.pdbj.org/pub/pdb/validation_reports/k2/3k2s | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 28120.637 Da / 分子数: 2 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 発現宿主: Homo sapiens (ヒト) / 発現宿主:  #2: 化合物 | ChemComp-POV / ( #3: 化合物 | ChemComp-CLR / |
|---|
-実験情報
-実験
| 実験 | 手法:  溶液散乱 / 使用した結晶の数: 1 溶液散乱 / 使用した結晶の数: 1 |
|---|
-データ収集
| 回折 | 平均測定温度: 279 K | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 | 由来: NUCLEAR REACTOR / タイプ: OTHER / 波長: 5 Å | |||||||||||||||
| 検出器 | 検出器: AREA DETECTOR / 日付: 2008年10月15日 | |||||||||||||||
| 放射 | モノクロメーター: GRAPHITE / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray | |||||||||||||||
| 放射波長 | 波長: 5 Å / 相対比: 1 | |||||||||||||||
| 反射 シェル | 最高解像度: 5 Å | |||||||||||||||
| Soln scatter | Conc. range: 2-4 / Data analysis software list: PRIMUS, GNOM, DAMMIN / Data reduction software list: ILL IN-HOUSE PACKAGE / 検出器タイプ: AREA / Num. of time frames: 3 / Sample pH: 7.4 / Source beamline: NEUTRON CAMERA FOR REACTOR SOURCE / Source beamline instrument: D22 (LOQ) / Source class: N / Source type: ILL / 温度: 301 K / タイプ: neutron
|
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化ステップ | サイクル: LAST
| |||||||||||||||||||||||||||||||||||||||
| Soln scatter model | 手法: CONSTRAINED SCATTERING FITTING OF HOMOLOGY MODELS コンフォーマー選択の基準: THE MODELLED SCATTERING CURVES WERE ASSESSED BY CALCULATION OF THE RG IN THE SAME Q RANGES USED IN THE EXPERIMENTAL GUINIER FITS. MODELS WERE THEN RANKED USING A ...コンフォーマー選択の基準: THE MODELLED SCATTERING CURVES WERE ASSESSED BY CALCULATION OF THE RG IN THE SAME Q RANGES USED IN THE EXPERIMENTAL GUINIER FITS. MODELS WERE THEN RANKED USING A GOODNESS-OF-FIT CHI SQUARE-FACTOR DEFINED BY THE DIFFERENCE BETWEEN THE CALCULATED AND EXPERIMENTAL SCATTERING INTENSITIES AND BASED ON THE EXPERIMENTAL CURVES IN THE Q RANGE EXTENDING TO 2.4 NM-1 (PROTEIN) AND 2.1 NM-1 (LIPID). 詳細: AN ALL ATOM COMPUTATIONAL MODEL WAS CONSTRUCTED BY COMBINING MOLELING WITH CONRAST VARIATION SANS, HYDROGEN-DEUTERIUM EXCHANGE (H/D-MS/MS), AND DISTANCE CONSTRAINTS FROM CROSS-LINKING, ...詳細: AN ALL ATOM COMPUTATIONAL MODEL WAS CONSTRUCTED BY COMBINING MOLELING WITH CONRAST VARIATION SANS, HYDROGEN-DEUTERIUM EXCHANGE (H/D-MS/MS), AND DISTANCE CONSTRAINTS FROM CROSS-LINKING, FLUORESCENCE RESONANCE ENERGY TRANSFER AND ELECTRON SPIN RESONANCE. SANS LOW RESOLUTION STRUCTURES (12% AND 42% D2O) WERE USED AS SCAFFOLDS TO BUILD MOLECULAR MODELS FOR PROTEIN AND LIPID COMPONENTS OF NASCENT HDL. 256 MODELS WERE GENERATED AND ASSESSED USING GOODNESS-OF-FIT WITH BOTH SANS AND H/D-MS/MS DATA. THE NEUTRON SCATTERING CURVE I(Q) WAS CALCULATED ASSUMING ALL ATOM STRUCTURE, AND WITH CORRECTIONS FOR WAVELENGTH SPREAD AND BEAM DIVERGENCE. Entry fitting list: THE DOUBLE BELT MODEL (SEGREST JP, JBC 274, 31755 (1999)) Num. of conformers calculated: 256 / Num. of conformers submitted: 1 / 代表コンフォーマー: 1 Software author list: LINDAHL E, SALI A, DELANO WL, MERZEL F, RICHARDS RM, SVERGUN DI Software list: GROMACS, MODELLER, PYMOL, SASSIM, YALE:VOLUME/ACCESS, PRIMUS, GNOM, DAMMIN |
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj