| 登録情報 | データベース: PDB / ID: 3ba6
|
|---|
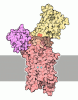
| タイトル | Structure of the Ca2E1P phosphoenzyme intermediate of the SERCA Ca2+-ATPase |
|---|
 要素 要素 | Sarcoplasmic/endoplasmic reticulum calcium ATPase 1 |
|---|
 キーワード キーワード | HYDROLASE / membrane protein / P-type ATPase / phosphoenzyme / aspartyl-phosphoanhydride / Alternative splicing / ATP-binding / Calcium / Calcium transport / Endoplasmic reticulum / Ion transport / Magnesium / Metal-binding / Nucleotide-binding / Phosphorylation / Sarcoplasmic reticulum / Transmembrane / Transport |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
positive regulation of calcium ion import into sarcoplasmic reticulum / positive regulation of ATPase-coupled calcium transmembrane transporter activity / positive regulation of fast-twitch skeletal muscle fiber contraction / H zone / regulation of striated muscle contraction / calcium ion import into sarcoplasmic reticulum / negative regulation of striated muscle contraction / P-type Ca2+ transporter / P-type calcium transporter activity / positive regulation of cardiac muscle cell contraction ...positive regulation of calcium ion import into sarcoplasmic reticulum / positive regulation of ATPase-coupled calcium transmembrane transporter activity / positive regulation of fast-twitch skeletal muscle fiber contraction / H zone / regulation of striated muscle contraction / calcium ion import into sarcoplasmic reticulum / negative regulation of striated muscle contraction / P-type Ca2+ transporter / P-type calcium transporter activity / positive regulation of cardiac muscle cell contraction / I band / endoplasmic reticulum-Golgi intermediate compartment / sarcoplasmic reticulum membrane / sarcoplasmic reticulum / calcium ion transport / calcium ion binding / endoplasmic reticulum membrane / perinuclear region of cytoplasm / endoplasmic reticulum / ATP hydrolysis activity / ATP binding / membrane類似検索 - 分子機能 Calcium-transporting ATPase, transmembrane domain / Calcium-transporting ATPase, transmembrane domain / P-type ATPase, subfamily IIA, SERCA-type / Calcium-transporting ATPase, cytoplasmic transduction domain A / Calcium-transporting ATPase, cytoplasmic transduction domain A / Calcium-transporting ATPase, cytoplasmic domain N / Calcium-transporting ATPase, cytoplasmic domain N / haloacid dehalogenase-like hydrolase / Cation-transporting P-type ATPase, C-terminal / Cation transporting ATPase, C-terminus ...Calcium-transporting ATPase, transmembrane domain / Calcium-transporting ATPase, transmembrane domain / P-type ATPase, subfamily IIA, SERCA-type / Calcium-transporting ATPase, cytoplasmic transduction domain A / Calcium-transporting ATPase, cytoplasmic transduction domain A / Calcium-transporting ATPase, cytoplasmic domain N / Calcium-transporting ATPase, cytoplasmic domain N / haloacid dehalogenase-like hydrolase / Cation-transporting P-type ATPase, C-terminal / Cation transporting ATPase, C-terminus / Cation transporter/ATPase, N-terminus / Cation-transporting P-type ATPase, N-terminal / Cation transporter/ATPase, N-terminus / P-type ATPase, cytoplasmic domain N / HAD superfamily/HAD-like / : / P-type ATPase actuator domain / P-type ATPase, haloacid dehalogenase domain / P-type ATPase, phosphorylation site / P-type ATPase, cytoplasmic domain N / E1-E2 ATPases phosphorylation site. / P-type ATPase, A domain superfamily / P-type ATPase / P-type ATPase, transmembrane domain superfamily / HAD superfamily / HAD-like superfamily / Distorted Sandwich / Up-down Bundle / Rossmann fold / 3-Layer(aba) Sandwich / Mainly Beta / Mainly Alpha / Alpha Beta類似検索 - ドメイン・相同性 AMP PHOSPHORAMIDATE / : / Sarcoplasmic/endoplasmic reticulum calcium ATPase 1類似検索 - 構成要素 |
|---|
| 生物種 |   Oryctolagus cuniculus (ウサギ) Oryctolagus cuniculus (ウサギ) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.8 Å 分子置換 / 解像度: 2.8 Å |
|---|
 データ登録者 データ登録者 | Picard, M. / Winther, A.M.L. / Olesen, C. / Gyrup, C. / Morth, J.P. / Oxvig, C. / Moller, J.V. / Nissen, P. |
|---|
 引用 引用 |  ジャーナル: Nature / 年: 2007 ジャーナル: Nature / 年: 2007
タイトル: The structural basis of calcium transport by the calcium pump.
著者: Olesen, C. / Picard, M. / Winther, A.M. / Gyrup, C. / Morth, J.P. / Oxvig, C. / Moller, J.V. / Nissen, P. |
|---|
| 履歴 | | 登録 | 2007年11月7日 | 登録サイト: RCSB / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2007年12月18日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2017年10月25日 | Group: Refinement description / カテゴリ: software
Item: _software.classification / _software.contact_author ..._software.classification / _software.contact_author / _software.contact_author_email / _software.date / _software.language / _software.location / _software.name / _software.type / _software.version |
|---|
| 改定 1.3 | 2023年11月1日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / pdbx_struct_conn_angle / struct_conn / struct_conn_type / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.conn_type_id / _struct_conn.id / _struct_conn.pdbx_dist_value / _struct_conn.pdbx_leaving_atom_flag / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_conn_type.id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
| 改定 1.4 | 2025年6月4日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature
Item: _pdbx_entry_details.has_protein_modification |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.8 Å
分子置換 / 解像度: 2.8 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Nature / 年: 2007
ジャーナル: Nature / 年: 2007 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 3ba6.cif.gz
3ba6.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb3ba6.ent.gz
pdb3ba6.ent.gz PDB形式
PDB形式 3ba6.json.gz
3ba6.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/ba/3ba6
https://data.pdbj.org/pub/pdb/validation_reports/ba/3ba6 ftp://data.pdbj.org/pub/pdb/validation_reports/ba/3ba6
ftp://data.pdbj.org/pub/pdb/validation_reports/ba/3ba6 リンク
リンク 集合体
集合体
 要素
要素
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  ESRF
ESRF  / ビームライン: ID23-2 / 波長: 1.0723 Å
/ ビームライン: ID23-2 / 波長: 1.0723 Å 分子置換
分子置換 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー

















 PDBj
PDBj