| 登録情報 | データベース: PDB / ID: 2m6o
|
|---|
| タイトル | The actinobacterial transcription factor RbpA binds to the principal sigma subunit of RNA polymerase |
|---|
 要素 要素 | Uncharacterized protein |
|---|
 キーワード キーワード | TRANSCRIPTION / RbpA / RNAP / Sigma factor |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
bacterial-type RNA polymerase holo enzyme binding / bacterial-type RNA polymerase core enzyme binding / response to antibiotic / positive regulation of DNA-templated transcription / zinc ion binding類似検索 - 分子機能 RNA polymerase-binding protein A / RNA polymerase-binding protein RbpA / RbpA superfamily / RNA polymerase-binding protein / Rubrerythrin, domain 2 / Single Sheet / Mainly Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Streptomyces coelicolor (バクテリア) Streptomyces coelicolor (バクテリア) |
|---|
| 手法 | 溶液NMR / simulated annealing, distance geometry |
|---|
| Model details | lowest energy, model1 |
|---|
 データ登録者 データ登録者 | Liu, B. / Tabib-Salazar, A. / Doughty, P. / Lewis, R. / Ghosh, S. / Parsy, M. / Simpson, P. / Matthews, S. / Paget, M. |
|---|
 引用 引用 |  ジャーナル: Nucleic Acids Res. / 年: 2013 ジャーナル: Nucleic Acids Res. / 年: 2013
タイトル: The actinobacterial transcription factor RbpA binds to the principal sigma subunit of RNA polymerase.
著者: Tabib-Salazar, A. / Liu, B. / Doughty, P. / Lewis, R.A. / Ghosh, S. / Parsy, M.L. / Simpson, P.J. / O'Dwyer, K. / Matthews, S.J. / Paget, M.S. |
|---|
| 履歴 | | 登録 | 2013年4月6日 | 登録サイト: BMRB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2013年5月8日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2013年6月26日 | Group: Database references |
|---|
| 改定 1.2 | 2013年7月3日 | Group: Database references |
|---|
| 改定 1.3 | 2018年1月24日 | Group: Structure summary / カテゴリ: audit_author / Item: _audit_author.name |
|---|
| 改定 1.4 | 2024年5月1日 | Group: Data collection / Database references
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_nmr_spectrometer
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_nmr_spectrometer.model |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Streptomyces coelicolor (バクテリア)
Streptomyces coelicolor (バクテリア) データ登録者
データ登録者 引用
引用 ジャーナル: Nucleic Acids Res. / 年: 2013
ジャーナル: Nucleic Acids Res. / 年: 2013 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2m6o.cif.gz
2m6o.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2m6o.ent.gz
pdb2m6o.ent.gz PDB形式
PDB形式 2m6o.json.gz
2m6o.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/m6/2m6o
https://data.pdbj.org/pub/pdb/validation_reports/m6/2m6o ftp://data.pdbj.org/pub/pdb/validation_reports/m6/2m6o
ftp://data.pdbj.org/pub/pdb/validation_reports/m6/2m6o リンク
リンク 集合体
集合体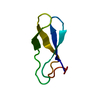
 要素
要素 Streptomyces coelicolor (バクテリア)
Streptomyces coelicolor (バクテリア)
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj HSQC
HSQC