+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 2fk3 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Structure of the Alzheimer's Amyloid Precursor Protein (APP) Copper Binding Domain in 'large unit cell' form | ||||||
 要素 要素 | Amyloid beta A4 protein precursor | ||||||
 キーワード キーワード | METAL BINDING PROTEIN / Alpha-Beta Two-layered Sandwich / Non-Crystallographic Symmetry | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報amyloid-beta complex / growth cone lamellipodium / cellular response to norepinephrine stimulus / growth cone filopodium / microglia development / collateral sprouting in absence of injury / Formyl peptide receptors bind formyl peptides and many other ligands / axo-dendritic transport / regulation of Wnt signaling pathway / regulation of synapse structure or activity ...amyloid-beta complex / growth cone lamellipodium / cellular response to norepinephrine stimulus / growth cone filopodium / microglia development / collateral sprouting in absence of injury / Formyl peptide receptors bind formyl peptides and many other ligands / axo-dendritic transport / regulation of Wnt signaling pathway / regulation of synapse structure or activity / axon midline choice point recognition / astrocyte activation involved in immune response / NMDA selective glutamate receptor signaling pathway / regulation of spontaneous synaptic transmission / mating behavior / growth factor receptor binding / peptidase activator activity / Golgi-associated vesicle / PTB domain binding / positive regulation of amyloid fibril formation / Insertion of tail-anchored proteins into the endoplasmic reticulum membrane / Lysosome Vesicle Biogenesis / astrocyte projection / neuron remodeling / Deregulated CDK5 triggers multiple neurodegenerative pathways in Alzheimer's disease models / nuclear envelope lumen / dendrite development / positive regulation of protein metabolic process / TRAF6 mediated NF-kB activation / signaling receptor activator activity / Advanced glycosylation endproduct receptor signaling / negative regulation of long-term synaptic potentiation / modulation of excitatory postsynaptic potential / The NLRP3 inflammasome / transition metal ion binding / main axon / regulation of multicellular organism growth / intracellular copper ion homeostasis / ECM proteoglycans / regulation of presynapse assembly / positive regulation of T cell migration / neuronal dense core vesicle / Purinergic signaling in leishmaniasis infection / positive regulation of chemokine production / cellular response to manganese ion / Notch signaling pathway / clathrin-coated pit / extracellular matrix organization / neuron projection maintenance / Mitochondrial protein degradation / astrocyte activation / ionotropic glutamate receptor signaling pathway / positive regulation of calcium-mediated signaling / positive regulation of mitotic cell cycle / response to interleukin-1 / axonogenesis / protein serine/threonine kinase binding / cellular response to copper ion / platelet alpha granule lumen / cellular response to cAMP / positive regulation of glycolytic process / central nervous system development / positive regulation of interleukin-1 beta production / adult locomotory behavior / endosome lumen / dendritic shaft / trans-Golgi network membrane / positive regulation of long-term synaptic potentiation / learning / positive regulation of JNK cascade / Post-translational protein phosphorylation / locomotory behavior / microglial cell activation / serine-type endopeptidase inhibitor activity / positive regulation of non-canonical NF-kappaB signal transduction / TAK1-dependent IKK and NF-kappa-B activation / regulation of long-term neuronal synaptic plasticity / synapse organization / cellular response to nerve growth factor stimulus / recycling endosome / visual learning / positive regulation of interleukin-6 production / response to lead ion / Golgi lumen / cognition / Regulation of Insulin-like Growth Factor (IGF) transport and uptake by Insulin-like Growth Factor Binding Proteins (IGFBPs) / endocytosis / cellular response to amyloid-beta / positive regulation of inflammatory response / neuron projection development / positive regulation of tumor necrosis factor production / Platelet degranulation / heparin binding / regulation of translation / regulation of gene expression / early endosome membrane / perikaryon / G alpha (i) signalling events / G alpha (q) signalling events / dendritic spine 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  単波長異常分散 / 解像度: 2.4 Å 単波長異常分散 / 解像度: 2.4 Å | ||||||
 データ登録者 データ登録者 | Kong, G.K.-W. / Parker, M.W. | ||||||
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 2007 ジャーナル: J.Mol.Biol. / 年: 2007タイトル: Structural Studies of the Alzheimer's Amyloid Precursor Protein Copper-binding Domain Reveal How it Binds Copper Ions 著者: Kong, G.K. / Adams, J.J. / Harris, H.H. / Boas, J.F. / Curtain, C.C. / Galatis, D. / Masters, C.L. / Barnham, K.J. / McKinstry, W.J. / Cappai, R. / Parker, M.W. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  2fk3.cif.gz 2fk3.cif.gz | 110.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb2fk3.ent.gz pdb2fk3.ent.gz | 86 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  2fk3.json.gz 2fk3.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  2fk3_validation.pdf.gz 2fk3_validation.pdf.gz | 482 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  2fk3_full_validation.pdf.gz 2fk3_full_validation.pdf.gz | 490.1 KB | 表示 | |
| XML形式データ |  2fk3_validation.xml.gz 2fk3_validation.xml.gz | 20.6 KB | 表示 | |
| CIF形式データ |  2fk3_validation.cif.gz 2fk3_validation.cif.gz | 29.8 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/fk/2fk3 https://data.pdbj.org/pub/pdb/validation_reports/fk/2fk3 ftp://data.pdbj.org/pub/pdb/validation_reports/fk/2fk3 ftp://data.pdbj.org/pub/pdb/validation_reports/fk/2fk3 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 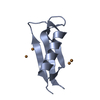
| ||||||||
| 2 | 
| ||||||||
| 3 | 
| ||||||||
| 4 | 
| ||||||||
| 5 | 
| ||||||||
| 6 | 
| ||||||||
| 7 | 
| ||||||||
| 8 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 6848.926 Da / 分子数: 8 / 断片: Residues 133 to 189 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: APP / プラスミド: pPIC-9 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: APP / プラスミド: pPIC-9 / 発現宿主:  Pichia pastoris (菌類) / 株 (発現宿主): GS115 / 参照: UniProt: P05067 Pichia pastoris (菌類) / 株 (発現宿主): GS115 / 参照: UniProt: P05067#2: 化合物 | ChemComp-CU / #3: 水 | ChemComp-HOH / | Has protein modification | Y | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.34 Å3/Da / 溶媒含有率: 47.46 % |
|---|---|
| 結晶化 | 温度: 295 K / 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 5.4 詳細: 0.1 M MES pH 5.4 - 5.6, 0.4 M NaCOOH, 10 - 15 % (w/v) PEG 4000, VAPOR DIFFUSION, HANGING DROP, temperature 295K |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  APS APS  / ビームライン: 14-ID-B / 波長: 1.3786 Å / ビームライン: 14-ID-B / 波長: 1.3786 Å |
| 検出器 | タイプ: MARRESEARCH / 検出器: CCD / 日付: 2003年11月13日 / 詳細: Bent cylindrical Si-mirror (Rh coated) |
| 放射 | モノクロメーター: Diamond (111) double-crystal monochromator プロトコル: MAD / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.3786 Å / 相対比: 1 |
| 反射 | 解像度: 2.4→20 Å / Num. all: 20578 / Num. obs: 20981 / % possible obs: 98.5 % / Observed criterion σ(I): 1 / 冗長度: 11.4 % / Biso Wilson estimate: 34.1 Å2 / Rsym value: 0.072 / Net I/σ(I): 30.8 |
| 反射 シェル | 解像度: 2.4→2.49 Å / 冗長度: 6 % / Mean I/σ(I) obs: 9.3 / Rsym value: 0.143 / % possible all: 86.3 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  単波長異常分散 / 解像度: 2.4→19.88 Å / Rfactor Rfree error: 0.008 / Data cutoff high absF: 1444276.07 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0 / 立体化学のターゲット値: Engh & Huber 単波長異常分散 / 解像度: 2.4→19.88 Å / Rfactor Rfree error: 0.008 / Data cutoff high absF: 1444276.07 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0 / 立体化学のターゲット値: Engh & Huber
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 溶媒モデル: FLAT MODEL / Bsol: 39.6865 Å2 / ksol: 0.369541 e/Å3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 24.7 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.4→19.88 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.4→2.55 Å / Rfactor Rfree error: 0.023 / Total num. of bins used: 6
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Xplor file |
|
 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj