Entry Database : PDB / ID : 2bvmTitle Crystal structure of the catalytic domain of toxin B from Clostridium difficile in complex with UDP, Glc and manganese ion TOXIN B Keywords / Function / homology Function Domain/homology Component
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / Biological species CLOSTRIDIUM DIFFICILE (bacteria)Method / / / Resolution : 2.55 Å Authors Reinert, D.J. / Jank, T. / Aktories, K. / Schulz, G.E. Journal : J.Mol.Biol. / Year : 2005Title : Structural Basis for the Function of Clostridium Difficile Toxin B.Authors : Reinert, D.J. / Jank, T. / Aktories, K. / Schulz, G.E. History Deposition Jun 30, 2005 Deposition site / Processing site Revision 1.0 Aug 3, 2005 Provider / Type Revision 1.1 Jul 13, 2011 Group / Version format complianceRevision 1.2 Jul 29, 2020 Group Data collection / Derived calculations ... Data collection / Derived calculations / Other / Structure summary Category chem_comp / entity ... chem_comp / entity / pdbx_chem_comp_identifier / pdbx_database_status / pdbx_entity_nonpoly / pdbx_struct_conn_angle / struct_conn / struct_site / struct_site_gen Item _chem_comp.name / _chem_comp.type ... _chem_comp.name / _chem_comp.type / _entity.pdbx_description / _pdbx_database_status.status_code_sf / _pdbx_entity_nonpoly.name / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id Description / Provider / Type Revision 1.3 Dec 13, 2023 Group Data collection / Database references ... Data collection / Database references / Refinement description / Structure summary Category chem_comp / chem_comp_atom ... chem_comp / chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model Item / _database_2.pdbx_DOI / _database_2.pdbx_database_accession
Show all Show less
 Yorodumi
Yorodumi Open data
Open data Basic information
Basic information Components
Components Keywords
Keywords Function and homology information
Function and homology information CLOSTRIDIUM DIFFICILE (bacteria)
CLOSTRIDIUM DIFFICILE (bacteria) X-RAY DIFFRACTION /
X-RAY DIFFRACTION /  SYNCHROTRON /
SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.55 Å
MOLECULAR REPLACEMENT / Resolution: 2.55 Å  Authors
Authors Citation
Citation Journal: J.Mol.Biol. / Year: 2005
Journal: J.Mol.Biol. / Year: 2005 Structure visualization
Structure visualization Molmil
Molmil Jmol/JSmol
Jmol/JSmol Downloads & links
Downloads & links Download
Download 2bvm.cif.gz
2bvm.cif.gz PDBx/mmCIF format
PDBx/mmCIF format pdb2bvm.ent.gz
pdb2bvm.ent.gz PDB format
PDB format 2bvm.json.gz
2bvm.json.gz PDBx/mmJSON format
PDBx/mmJSON format Other downloads
Other downloads https://data.pdbj.org/pub/pdb/validation_reports/bv/2bvm
https://data.pdbj.org/pub/pdb/validation_reports/bv/2bvm ftp://data.pdbj.org/pub/pdb/validation_reports/bv/2bvm
ftp://data.pdbj.org/pub/pdb/validation_reports/bv/2bvm

 Links
Links Assembly
Assembly
 Components
Components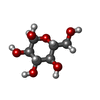

 CLOSTRIDIUM DIFFICILE (bacteria) / Strain: VPI 10463 / Production host:
CLOSTRIDIUM DIFFICILE (bacteria) / Strain: VPI 10463 / Production host: 

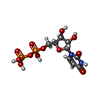





 X-RAY DIFFRACTION / Number of used crystals: 1
X-RAY DIFFRACTION / Number of used crystals: 1  Sample preparation
Sample preparation SYNCHROTRON / Site:
SYNCHROTRON / Site:  SLS
SLS  / Beamline: X06SA / Wavelength: 0.82
/ Beamline: X06SA / Wavelength: 0.82  Processing
Processing MOLECULAR REPLACEMENT
MOLECULAR REPLACEMENT Movie
Movie Controller
Controller












 PDBj
PDBj








