+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1yn1 | ||||||
|---|---|---|---|---|---|---|---|
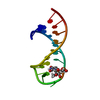
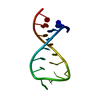
| タイトル | Solution structure of the VS ribozyme stem-loop V in the presence of MgCl2 | ||||||
 要素 要素 | VS RIBOZYME STEM-LOOP V | ||||||
 キーワード キーワード | RNA / U-turn / hairpin / magnesium ions | ||||||
| 機能・相同性 | RNA / RNA (> 10) 機能・相同性情報 機能・相同性情報 | ||||||
| 手法 | 溶液NMR / SIMULATED ANNEALING; MOLECULAR DYNAMICS | ||||||
| Model type details | minimized average | ||||||
 データ登録者 データ登録者 | Campbell, D.O. / Legault, P. | ||||||
 引用 引用 |  ジャーナル: Biochemistry / 年: 2006 ジャーナル: Biochemistry / 年: 2006タイトル: NMR structure of varkud satellite ribozyme stem-loop v in the presence of magnesium ions and localization of metal-binding sites 著者: Campbell, D.O. / Bouchard, P. / Desjardins, G. / Legault, P. #1:  ジャーナル: To be Published / 年: 2005 ジャーナル: To be Published / 年: 2005タイトル: NMR Structure of the VS Ribozyme Stem-Loop V RNA and Magnesium-Ion Binding from Chemical-Shift Mapping 著者: Campbell, D.O. / Legault, P. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1yn1.cif.gz 1yn1.cif.gz | 122.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1yn1.ent.gz pdb1yn1.ent.gz | 100.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1yn1.json.gz 1yn1.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/yn/1yn1 https://data.pdbj.org/pub/pdb/validation_reports/yn/1yn1 ftp://data.pdbj.org/pub/pdb/validation_reports/yn/1yn1 ftp://data.pdbj.org/pub/pdb/validation_reports/yn/1yn1 | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: RNA鎖 | 分子量: 5419.261 Da / 分子数: 1 / 断片: SL5 / 由来タイプ: 合成 詳細: THIS SEQUENCE IS DERIVED FROM THE NEUROSPORA VARKUD SATELLITE RIBOZYME |
|---|
-実験情報
-実験
| 実験 | 手法: 溶液NMR | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
|
- 試料調製
試料調製
| 詳細 | 内容: 0.8 mM to 2.0 mM of unlabeled, 15N, or 13C/15N SL5 溶媒系: [10 mM d11-Tris pH 7.0, 50 mM NaCl, 0.05 mM NaN3, 40 mM MgCl2] or [ 10 mM d11-Tris pH 7.0, 0.05 mM NaN3, 20 mM MgCl2]; 90% H2O, 10% D2O or 100% D2O; |
|---|---|
| 試料状態 | イオン強度: variable (see sample details) / pH: 7 / 圧: ambient / 温度: 298 K |
-NMR測定
| NMRスペクトロメーター | タイプ: Varian INOVA / 製造業者: Varian / モデル: INOVA / 磁場強度: 600 MHz |
|---|
- 解析
解析
| NMR software |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: SIMULATED ANNEALING; MOLECULAR DYNAMICS / ソフトェア番号: 1 詳細: Conformer 1 represents the minimized average structure, the 10 following structures represent the ensemble of low-energy structures | ||||||||||||||||||||||||
| 代表構造 | 選択基準: minimized average structure | ||||||||||||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: structures with the lowest energy 計算したコンフォーマーの数: 69 / 登録したコンフォーマーの数: 11 |
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj





























 X-PLOR
X-PLOR