| 登録情報 | データベース: PDB / ID: 1w4u
|
|---|
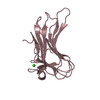
| タイトル | NMR solution structure of the ubiquitin conjugating enzyme UbcH5B |
|---|
 要素 要素 | UBIQUITIN-CONJUGATING ENZYME E2-17 KDA 2 |
|---|
 キーワード キーワード | LIGASE / UBIQUITINATION / E2 ENZYME / BL CONJUGATION PATHWAY |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
Synthesis of active ubiquitin: roles of E1 and E2 enzymes / E3 ubiquitin ligases ubiquitinate target proteins / Inactivation of CSF3 (G-CSF) signaling / IKK complex recruitment mediated by RIP1 / Oxygen-dependent proline hydroxylation of Hypoxia-inducible Factor Alpha / FCERI mediated NF-kB activation / CLEC7A (Dectin-1) signaling / Downstream TCR signaling / Peroxisomal protein import / Neddylation ...Synthesis of active ubiquitin: roles of E1 and E2 enzymes / E3 ubiquitin ligases ubiquitinate target proteins / Inactivation of CSF3 (G-CSF) signaling / IKK complex recruitment mediated by RIP1 / Oxygen-dependent proline hydroxylation of Hypoxia-inducible Factor Alpha / FCERI mediated NF-kB activation / CLEC7A (Dectin-1) signaling / Downstream TCR signaling / Peroxisomal protein import / Neddylation / (E3-independent) E2 ubiquitin-conjugating enzyme / Antigen processing: Ubiquitination & Proteasome degradation / E2 ubiquitin-conjugating enzyme / ubiquitin conjugating enzyme activity / ubiquitin ligase complex / protein autoubiquitination / protein K48-linked ubiquitination / protein modification process / Synthesis of active ubiquitin: roles of E1 and E2 enzymes / TICAM1, RIP1-mediated IKK complex recruitment / IKK complex recruitment mediated by RIP1 / PINK1-PRKN Mediated Mitophagy / Negative regulators of DDX58/IFIH1 signaling / Peroxisomal protein import / Regulation of TNFR1 signaling / Inactivation of CSF3 (G-CSF) signaling / Oxygen-dependent proline hydroxylation of Hypoxia-inducible Factor Alpha / CLEC7A (Dectin-1) signaling / FCERI mediated NF-kB activation / protein polyubiquitination / ubiquitin-protein transferase activity / ubiquitin protein ligase activity / Downstream TCR signaling / Antigen processing: Ubiquitination & Proteasome degradation / E3 ubiquitin ligases ubiquitinate target proteins / Neddylation / ubiquitin-dependent protein catabolic process / protein ubiquitination / protein-containing complex / extracellular exosome / nucleoplasm / ATP binding / nucleus / cytosol類似検索 - 分子機能 Ubiquitin Conjugating Enzyme / Ubiquitin Conjugating Enzyme / Ubiquitin-conjugating enzyme, active site / Ubiquitin-conjugating (UBC) active site signature. / Ubiquitin-conjugating enzyme E2 / Ubiquitin-conjugating enzyme / Ubiquitin-conjugating (UBC) core domain profile. / Ubiquitin-conjugating enzyme E2, catalytic domain homologues / Ubiquitin-conjugating enzyme/RWD-like / Roll / Alpha Beta類似検索 - ドメイン・相同性 Ubiquitin-conjugating enzyme E2 D2 / Ubiquitin-conjugating enzyme E2 D2類似検索 - 構成要素 |
|---|
| 生物種 |  HOMO SAPIENS (ヒト) HOMO SAPIENS (ヒト) |
|---|
| 手法 | 溶液NMR / ARIA |
|---|
 データ登録者 データ登録者 | Houben, K. / Dominguez, C. / Van Schaik, F.M.A. / Timmers, H.T.M. / Bonvin, A.M.J.J. / Boelens, R. |
|---|
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 2004 ジャーナル: J.Mol.Biol. / 年: 2004
タイトル: Solution Structure of the Ubiquitin-Conjugating Enzyme Ubch5B
著者: Houben, K. / Dominguez, C. / Van Schaik, F.M.A. / Timmers, H.T.M. / Bonvin, A.M.J.J. / Boelens, R. |
|---|
| 履歴 | | 登録 | 2004年7月29日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2004年11月10日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2017年4月19日 | Group: Atomic model / Other |
|---|
| 改定 1.2 | 2024年5月15日 | Group: Data collection / Database references / Other
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_database_status / pdbx_nmr_spectrometer
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_mr / _pdbx_nmr_spectrometer.model |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 HOMO SAPIENS (ヒト)
HOMO SAPIENS (ヒト) データ登録者
データ登録者 引用
引用 ジャーナル: J.Mol.Biol. / 年: 2004
ジャーナル: J.Mol.Biol. / 年: 2004 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1w4u.cif.gz
1w4u.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1w4u.ent.gz
pdb1w4u.ent.gz PDB形式
PDB形式 1w4u.json.gz
1w4u.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/w4/1w4u
https://data.pdbj.org/pub/pdb/validation_reports/w4/1w4u ftp://data.pdbj.org/pub/pdb/validation_reports/w4/1w4u
ftp://data.pdbj.org/pub/pdb/validation_reports/w4/1w4u リンク
リンク 集合体
集合体
 要素
要素 HOMO SAPIENS (ヒト) / 発現宿主:
HOMO SAPIENS (ヒト) / 発現宿主: 
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj









