| 登録情報 | データベース: PDB / ID: 1txq
|
|---|
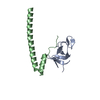
| タイトル | Crystal structure of the EB1 C-terminal domain complexed with the CAP-Gly domain of p150Glued |
|---|
 要素 要素 | - Dynactin 1
- Microtubule-associated protein RP/EB family member 1
|
|---|
 キーワード キーワード | STRUCTURAL PROTEIN/PROTEIN BINDING / PROTEIN COMPLEX / STRUCTURAL PROTEIN-PROTEIN BINDING COMPLEX |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
cell cortex region / protein localization to astral microtubule / centriolar subdistal appendage / protein localization to mitotic spindle / cortical microtubule cytoskeleton / positive regulation of neuromuscular junction development / centriole-centriole cohesion / mitotic spindle astral microtubule end / microtubule anchoring at centrosome / maintenance of synapse structure ...cell cortex region / protein localization to astral microtubule / centriolar subdistal appendage / protein localization to mitotic spindle / cortical microtubule cytoskeleton / positive regulation of neuromuscular junction development / centriole-centriole cohesion / mitotic spindle astral microtubule end / microtubule anchoring at centrosome / maintenance of synapse structure / ventral spinal cord development / protein localization to microtubule / microtubule plus-end / nuclear membrane disassembly / mitotic spindle microtubule / cell projection membrane / positive regulation of microtubule nucleation / XBP1(S) activates chaperone genes / melanosome transport / attachment of mitotic spindle microtubules to kinetochore / microtubule bundle formation / non-motile cilium assembly / microtubule plus-end binding / dynein complex / retrograde transport, endosome to Golgi / COPI-independent Golgi-to-ER retrograde traffic / protein localization to centrosome / microtubule associated complex / motor behavior / neuromuscular process / nuclear migration / negative regulation of microtubule polymerization / neuromuscular junction development / mitotic spindle pole / cell leading edge / microtubule organizing center / microtubule polymerization / establishment of mitotic spindle orientation / regulation of microtubule polymerization or depolymerization / spindle midzone / intercellular bridge / spindle assembly / cytoplasmic microtubule / COPI-mediated anterograde transport / Amplification of signal from unattached kinetochores via a MAD2 inhibitory signal / positive regulation of microtubule polymerization / Mitotic Prometaphase / centriole / neuron projection maintenance / EML4 and NUDC in mitotic spindle formation / Loss of Nlp from mitotic centrosomes / Loss of proteins required for interphase microtubule organization from the centrosome / Recruitment of mitotic centrosome proteins and complexes / tubulin binding / MHC class II antigen presentation / Recruitment of NuMA to mitotic centrosomes / regulation of mitotic spindle organization / Anchoring of the basal body to the plasma membrane / Resolution of Sister Chromatid Cohesion / HSP90 chaperone cycle for steroid hormone receptors (SHR) in the presence of ligand / AURKA Activation by TPX2 / RHO GTPases Activate Formins / kinetochore / tau protein binding / spindle / neuron cellular homeostasis / spindle pole / mitotic spindle / The role of GTSE1 in G2/M progression after G2 checkpoint / Separation of Sister Chromatids / Signaling by ALK fusions and activated point mutants / Regulation of PLK1 Activity at G2/M Transition / intracellular protein localization / nuclear envelope / cell migration / nervous system development / mitotic cell cycle / microtubule cytoskeleton / cell cortex / microtubule binding / microtubule / neuron projection / ciliary basal body / cilium / cadherin binding / axon / cell division / focal adhesion / neuronal cell body / centrosome / protein kinase binding / Golgi apparatus / RNA binding / identical protein binding / membrane / cytosol / cytoplasm類似検索 - 分子機能 Single alpha-helices involved in coiled-coils or other helix-helix interfaces - #1430 / Dynein associated protein / Dynein associated protein / CAP Gly-rich-like domain / EB1, C-terminal / Microtubule-associated protein RP/EB / EB1, C-terminal domain superfamily / EB1-C terminal (EB1-C) domain profile. / EB1-like C-terminal motif / CAP-Gly domain signature. ...Single alpha-helices involved in coiled-coils or other helix-helix interfaces - #1430 / Dynein associated protein / Dynein associated protein / CAP Gly-rich-like domain / EB1, C-terminal / Microtubule-associated protein RP/EB / EB1, C-terminal domain superfamily / EB1-C terminal (EB1-C) domain profile. / EB1-like C-terminal motif / CAP-Gly domain signature. / CAP Gly-rich domain / CAP Gly-rich domain superfamily / CAP-Gly domain / CAP-Gly domain profile. / CAP_GLY / Calponin homology (CH) domain / Calponin homology domain / CH domain superfamily / Calponin homology (CH) domain profile. / Single alpha-helices involved in coiled-coils or other helix-helix interfaces / SH3 type barrels. / Roll / Up-down Bundle / Mainly Beta / Mainly Alpha類似検索 - ドメイン・相同性 Dynactin subunit 1 / Microtubule-associated protein RP/EB family member 1類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  多波長異常分散 / 解像度: 1.8 Å 多波長異常分散 / 解像度: 1.8 Å |
|---|
 データ登録者 データ登録者 | Hayashi, I. / Ikura, M. |
|---|
 引用 引用 |  ジャーナル: Mol.Cell / 年: 2005 ジャーナル: Mol.Cell / 年: 2005
タイトル: Structural Basis for the Activation of Microtubule Assembly by the EB1 and p150(Glued) Complex
著者: Hayashi, I. / Wilde, A. / Mal, T.K. / Ikura, M. |
|---|
| 履歴 | | 登録 | 2004年7月6日 | 登録サイト: RCSB / 処理サイト: PDBJ |
|---|
| 改定 1.0 | 2005年9月13日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年4月30日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.3 | 2024年3月13日 | Group: Data collection / Database references / カテゴリ: chem_comp_atom / chem_comp_bond / database_2
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  多波長異常分散 / 解像度: 1.8 Å
多波長異常分散 / 解像度: 1.8 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Mol.Cell / 年: 2005
ジャーナル: Mol.Cell / 年: 2005 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 1txq.cif.gz
1txq.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb1txq.ent.gz
pdb1txq.ent.gz PDB形式
PDB形式 1txq.json.gz
1txq.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 1txq_validation.pdf.gz
1txq_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 1txq_full_validation.pdf.gz
1txq_full_validation.pdf.gz 1txq_validation.xml.gz
1txq_validation.xml.gz 1txq_validation.cif.gz
1txq_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/tx/1txq
https://data.pdbj.org/pub/pdb/validation_reports/tx/1txq ftp://data.pdbj.org/pub/pdb/validation_reports/tx/1txq
ftp://data.pdbj.org/pub/pdb/validation_reports/tx/1txq リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: p150Glued / プラスミド: pET15b / 生物種 (発現宿主): Escherichia coli / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: p150Glued / プラスミド: pET15b / 生物種 (発現宿主): Escherichia coli / 発現宿主: 
 Homo sapiens (ヒト) / 遺伝子: EB1 / プラスミド: pGEX4T-1 / 生物種 (発現宿主): Escherichia coli / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: EB1 / プラスミド: pGEX4T-1 / 生物種 (発現宿主): Escherichia coli / 発現宿主: 
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 19-BM / 波長: 0.9513 Å
/ ビームライン: 19-BM / 波長: 0.9513 Å 解析
解析 多波長異常分散 / 解像度: 1.8→17.93 Å / Rfactor Rfree error: 0.007 / Data cutoff high absF: 769082.92 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0 / 立体化学のターゲット値: Engh & Huber
多波長異常分散 / 解像度: 1.8→17.93 Å / Rfactor Rfree error: 0.007 / Data cutoff high absF: 769082.92 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0 / 立体化学のターゲット値: Engh & Huber ムービー
ムービー コントローラー
コントローラー









 PDBj
PDBj


















