[English] 日本語
 Yorodumi
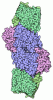
Yorodumi- PDB-1qh8: NITROGENASE MOFE PROTEIN FROM KLEBSIELLA PNEUMONIAE, AS-CRYSTALLI... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 1qh8 | ||||||
|---|---|---|---|---|---|---|---|
| Title | NITROGENASE MOFE PROTEIN FROM KLEBSIELLA PNEUMONIAE, AS-CRYSTALLIZED (MIXED OXIDATION) STATE | ||||||
 Components Components | (PROTEIN (NITROGENASE MOLYBDENUM IRON ...) x 2 | ||||||
 Keywords Keywords | OXIDOREDUCTASE / BIOLOGICAL NITROGEN FIXATION / NITROGEN METABOLISM / MOLYBDOENZYMES / ELECTRON TRANSFER | ||||||
| Function / homology |  Function and homology information Function and homology informationmolybdenum-iron nitrogenase complex / nitrogenase / nitrogenase activity / iron-sulfur cluster binding / ATP binding / metal ion binding Similarity search - Function | ||||||
| Biological species |  Klebsiella pneumoniae (bacteria) Klebsiella pneumoniae (bacteria) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 1.6 Å MOLECULAR REPLACEMENT / Resolution: 1.6 Å | ||||||
 Authors Authors | Mayer, S.M. / Lawson, D.M. / Gormal, C.A. / Roe, S.M. / Smith, B.E. | ||||||
 Citation Citation |  Journal: J.Mol.Biol. / Year: 1999 Journal: J.Mol.Biol. / Year: 1999Title: New insights into structure-function relationships in nitrogenase: A 1.6 A resolution X-ray crystallographic study of Klebsiella pneumoniae MoFe-protein. Authors: Mayer, S.M. / Lawson, D.M. / Gormal, C.A. / Roe, S.M. / Smith, B.E. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  1qh8.cif.gz 1qh8.cif.gz | 473.4 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb1qh8.ent.gz pdb1qh8.ent.gz | 373.9 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  1qh8.json.gz 1qh8.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/qh/1qh8 https://data.pdbj.org/pub/pdb/validation_reports/qh/1qh8 ftp://data.pdbj.org/pub/pdb/validation_reports/qh/1qh8 ftp://data.pdbj.org/pub/pdb/validation_reports/qh/1qh8 | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  1qguC  1qh1C  1min C: citing same article ( S: Starting model for refinement |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||||||
| Unit cell |
| ||||||||||||
| Noncrystallographic symmetry (NCS) | NCS oper:
|
- Components
Components
-PROTEIN (NITROGENASE MOLYBDENUM IRON ... , 2 types, 4 molecules ACBD
| #1: Protein | Mass: 53632.051 Da / Num. of mol.: 2 / Source method: isolated from a natural source / Details: ALSO KNOWN AS KLEBSIELLA PNEUMONIAE OXYTOCA. / Source: (natural)  Klebsiella pneumoniae (bacteria) / Cellular location: CYTOPLASM / Variant: WILD-TYPE / Strain: M5A1 / References: UniProt: P00466, nitrogenase Klebsiella pneumoniae (bacteria) / Cellular location: CYTOPLASM / Variant: WILD-TYPE / Strain: M5A1 / References: UniProt: P00466, nitrogenase#2: Protein | Mass: 58338.180 Da / Num. of mol.: 2 / Source method: isolated from a natural source / Details: ALSO KNOWN AS KLEBSIELLA PNEUMONIAE OXYTOCA. / Source: (natural)  Klebsiella pneumoniae (bacteria) / Cellular location: CYTOPLASM / Variant: WILD-TYPE / Strain: M5A1 / References: UniProt: P09772, nitrogenase Klebsiella pneumoniae (bacteria) / Cellular location: CYTOPLASM / Variant: WILD-TYPE / Strain: M5A1 / References: UniProt: P09772, nitrogenase |
|---|
-Non-polymers , 7 types, 2872 molecules 




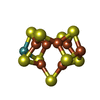
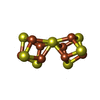



| #3: Chemical | ChemComp-MG / #4: Chemical | #5: Chemical | #6: Chemical | #7: Chemical | ChemComp-EDO / #8: Chemical | #9: Water | ChemComp-HOH / | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.31 Å3/Da / Density % sol: 46 % | ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Crystal grow | pH: 8 Details: CRYSTALLIZED ANAEROBICALLY USING LIQUID-LIQUID DIFFUSION TECHNIQUE. FINAL CONCENTRATIONS AFTER EQUILIBRATION WERE: 7% (W/V) PEG 6000, 0.4 - 0.6 M MGCL2, 50 MM TRIS-HCL PH 8, 3.3 MG/ML ...Details: CRYSTALLIZED ANAEROBICALLY USING LIQUID-LIQUID DIFFUSION TECHNIQUE. FINAL CONCENTRATIONS AFTER EQUILIBRATION WERE: 7% (W/V) PEG 6000, 0.4 - 0.6 M MGCL2, 50 MM TRIS-HCL PH 8, 3.3 MG/ML PROTEIN., pH 8.0, temperature 100K PRIOR TO DATA COLLECTION THE CRYSTAL WAS TRANSIENTLY SOAKED IN CRYOPROTECTANT (MOTHER LIQUOR WITH 25% ETHYLENE GLYCOL) CONTAINING 2 MM SODIUM DITHIONITE (A REDUCTANT). | ||||||||||||||||||||||||||||||
| Crystal | *PLUS | ||||||||||||||||||||||||||||||
| Crystal grow | *PLUS Temperature: 17 ℃ / pH: 8 / Method: liquid diffusion | ||||||||||||||||||||||||||||||
| Components of the solutions | *PLUS
|
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  EMBL/DESY, HAMBURG EMBL/DESY, HAMBURG  / Beamline: X11 / Wavelength: 0.91 / Beamline: X11 / Wavelength: 0.91 |
| Detector | Type: MARRESEARCH / Detector: IMAGE PLATE / Date: Jul 1, 1997 / Details: MIRRORS |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 0.91 Å / Relative weight: 1 |
| Reflection | Resolution: 1.6→50 Å / Num. obs: 265023 / % possible obs: 98 % / Observed criterion σ(I): -3 / Redundancy: 3.3 % / Biso Wilson estimate: 14.83 Å2 / Rmerge(I) obs: 0.044 / Net I/σ(I): 22.4 |
| Reflection shell | Resolution: 1.6→1.63 Å / Rmerge(I) obs: 0.227 / Mean I/σ(I) obs: 3.82 / % possible all: 84.7 |
| Reflection shell | *PLUS % possible obs: 84.7 % |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: 1MIN  1min Resolution: 1.6→50 Å / Cross valid method: THROUGHOUT / σ(F): 0 Details: TOWARDS THE END OF REFINEMENT ALL RESTRAINTS WITHIN THE HETEROGENS HCA, CFM, AND CLF WERE EXPLICITLY TURNED OFF. IN ADDITION, THE BONDS BETWEEN THESE HETEROGENS AND THE PROTEIN (SEE ...Details: TOWARDS THE END OF REFINEMENT ALL RESTRAINTS WITHIN THE HETEROGENS HCA, CFM, AND CLF WERE EXPLICITLY TURNED OFF. IN ADDITION, THE BONDS BETWEEN THESE HETEROGENS AND THE PROTEIN (SEE CONNECTIVITY SECTION) WERE NOT RESTRAINED.
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 17.71 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.6→50 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Software | *PLUS Name: REFMAC / Classification: refinement | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement | *PLUS σ(F): 0 / % reflection Rfree: 5 % / Rfactor obs: 0.155 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | *PLUS |
 Movie
Movie Controller
Controller
















 PDBj
PDBj