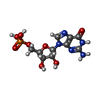
Entry Database : PDB / ID : 1jxmTitle CRYSTAL STRUCTURE OF THE GMP BOUND SH3-HOOK-GK FRAGMENT OF PSD-95 POSTSYNAPTIC DENSITY PROTEIN Keywords / / / / Function / homology Function Domain/homology Component
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / Biological species Rattus norvegicus (Norway rat)Method / / / Resolution : 2 Å Authors Tavares, G.A. / Panepucci, E.H. / Brunger, A.T. Journal : Mol.Cell / Year : 2001Title : Structural characterization of the intramolecular interaction between the SH3 and guanylate kinase domains of PSD-95.Authors : Tavares, G.A. / Panepucci, E.H. / Brunger, A.T. History Deposition Sep 7, 2001 Deposition site / Processing site Revision 1.0 Jan 16, 2002 Provider / Type Revision 1.1 Apr 27, 2008 Group Revision 1.2 Jul 13, 2011 Group Revision 1.3 Nov 29, 2023 Group / Database references / Derived calculationsCategory chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / database_2 / pdbx_database_related / struct_ref_seq_dif / struct_site Item _database_2.pdbx_DOI / _database_2.pdbx_database_accession ... _database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_related.db_name / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id
Show all Show less
 Yorodumi
Yorodumi Open data
Open data Basic information
Basic information Components
Components Keywords
Keywords Function and homology information
Function and homology information
 X-RAY DIFFRACTION /
X-RAY DIFFRACTION /  SYNCHROTRON /
SYNCHROTRON /  MAD / Resolution: 2 Å
MAD / Resolution: 2 Å  Authors
Authors Citation
Citation Journal: Mol.Cell / Year: 2001
Journal: Mol.Cell / Year: 2001 Structure visualization
Structure visualization Molmil
Molmil Jmol/JSmol
Jmol/JSmol Downloads & links
Downloads & links Download
Download 1jxm.cif.gz
1jxm.cif.gz PDBx/mmCIF format
PDBx/mmCIF format pdb1jxm.ent.gz
pdb1jxm.ent.gz PDB format
PDB format 1jxm.json.gz
1jxm.json.gz PDBx/mmJSON format
PDBx/mmJSON format Other downloads
Other downloads 1jxm_validation.pdf.gz
1jxm_validation.pdf.gz wwPDB validaton report
wwPDB validaton report 1jxm_full_validation.pdf.gz
1jxm_full_validation.pdf.gz 1jxm_validation.xml.gz
1jxm_validation.xml.gz 1jxm_validation.cif.gz
1jxm_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/jx/1jxm
https://data.pdbj.org/pub/pdb/validation_reports/jx/1jxm ftp://data.pdbj.org/pub/pdb/validation_reports/jx/1jxm
ftp://data.pdbj.org/pub/pdb/validation_reports/jx/1jxm Links
Links Assembly
Assembly
 Components
Components

 X-RAY DIFFRACTION / Number of used crystals: 2
X-RAY DIFFRACTION / Number of used crystals: 2  Sample preparation
Sample preparation Processing
Processing MAD / Resolution: 2→22.72 Å / Rfactor Rfree error: 0.004 / Data cutoff high absF: 2161953.84 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / Cross valid method: THROUGHOUT / σ(F): 1 / Stereochemistry target values: Engh & Huber
MAD / Resolution: 2→22.72 Å / Rfactor Rfree error: 0.004 / Data cutoff high absF: 2161953.84 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / Cross valid method: THROUGHOUT / σ(F): 1 / Stereochemistry target values: Engh & Huber Movie
Movie Controller
Controller













 PDBj
PDBj