+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1hry | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | THE 3D STRUCTURE OF THE HUMAN SRY-DNA COMPLEX SOLVED BY MULTID-DIMENSIONAL HETERONUCLEAR-EDITED AND-FILTERED NMR | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | DNA BINDING PROTEIN/DNA / DNA / SRY / DNA-BINDING PROTEIN / DNA BINDING PROTEIN-DNA COMPLEX | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of male gonad development / Transcriptional regulation of testis differentiation / sex differentiation / male sex determination / Deactivation of the beta-catenin transactivating complex / DNA-binding transcription activator activity, RNA polymerase II-specific / DNA-binding transcription factor binding / DNA-binding transcription factor activity, RNA polymerase II-specific / cell differentiation / calmodulin binding ...positive regulation of male gonad development / Transcriptional regulation of testis differentiation / sex differentiation / male sex determination / Deactivation of the beta-catenin transactivating complex / DNA-binding transcription activator activity, RNA polymerase II-specific / DNA-binding transcription factor binding / DNA-binding transcription factor activity, RNA polymerase II-specific / cell differentiation / calmodulin binding / nuclear speck / RNA polymerase II cis-regulatory region sequence-specific DNA binding / positive regulation of gene expression / chromatin / positive regulation of DNA-templated transcription / positive regulation of transcription by RNA polymerase II / DNA binding / nucleoplasm / nucleus / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 | 溶液NMR / simulated annealing | ||||||
 データ登録者 データ登録者 | Clore, G.M. / Werner, M.H. / Huth, J.R. / Gronenborn, A.M. | ||||||
 引用 引用 |  ジャーナル: Cell(Cambridge,Mass.) / 年: 1995 ジャーナル: Cell(Cambridge,Mass.) / 年: 1995タイトル: Molecular basis of human 46X,Y sex reversal revealed from the three-dimensional solution structure of the human SRY-DNA complex. 著者: Werner, M.H. / Huth, J.R. / Gronenborn, A.M. / Clore, G.M. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1hry.cif.gz 1hry.cif.gz | 54.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1hry.ent.gz pdb1hry.ent.gz | 37.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1hry.json.gz 1hry.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1hry_validation.pdf.gz 1hry_validation.pdf.gz | 248.3 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1hry_full_validation.pdf.gz 1hry_full_validation.pdf.gz | 247.9 KB | 表示 | |
| XML形式データ |  1hry_validation.xml.gz 1hry_validation.xml.gz | 3.9 KB | 表示 | |
| CIF形式データ |  1hry_validation.cif.gz 1hry_validation.cif.gz | 5 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/hr/1hry https://data.pdbj.org/pub/pdb/validation_reports/hr/1hry ftp://data.pdbj.org/pub/pdb/validation_reports/hr/1hry ftp://data.pdbj.org/pub/pdb/validation_reports/hr/1hry | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 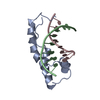
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: DNA鎖 | 分子量: 2404.621 Da / 分子数: 1 / 由来タイプ: 合成 / 詳細: chemically synthesized /  キーワード: DEOXYRIBONUCLEIC ACID キーワード: DEOXYRIBONUCLEIC ACID |
|---|---|
| #2: DNA鎖 | 分子量: 2448.613 Da / 分子数: 1 / 由来タイプ: 合成 / 詳細: chemically synthesized /  キーワード: DEOXYRIBONUCLEIC ACID キーワード: DEOXYRIBONUCLEIC ACID |
| #3: タンパク質 | 分子量: 9508.031 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) / Homo sapiens (ヒト) /  キーワード: POLYPEPTIDE / 参照: UniProt: Q05066 キーワード: POLYPEPTIDE / 参照: UniProt: Q05066 |
-実験情報
-実験
| 実験 | 手法: 溶液NMR |
|---|---|
| NMR実験の詳細 | Text: THE 3D STRUCTURE OF THE HUMAN SRY-DNA COMPLEX SOLVED BY MULTI-DIMENSIONAL HETERONUCLEAR-EDITED AND -FILTERED NMR IS BASED ON 1805 EXPERIMENTAL RESTRAINTS: (A) INTRA-PROTEIN: 290 SEQUENTIAL (|I- ...Text: THE 3D STRUCTURE OF THE HUMAN SRY-DNA COMPLEX SOLVED BY MULTI-DIMENSIONAL HETERONUCLEAR-EDITED AND -FILTERED NMR IS BASED ON 1805 EXPERIMENTAL RESTRAINTS: (A) INTRA-PROTEIN: 290 SEQUENTIAL (|I-J|=1), 221 MEDIUM RANGE (1 < |I-J| >=5) AND 107 LONG RANGE (|I-J| >5) INTERRESIDUES. 238 INTRARESIDUE APPROXIMATE INTERPROTON DISTANCE RESTRAINTS; 70 DISTANCE RESTRAINTS FOR 35 HYDROGEN BONDS; 153 TORSION ANGLE (71 PHI, 10 PSI, 56 CHI1 AND 16 CHI2) RESTRAINTS; 56 THREE-BOND HN-HA COUPLING CONSTANT RESTRAINTS; 145 (73 CALPHA AND 72 CBETA) 13C SHIFT RESTRAINTS. (B) INTRA-DNA: 206 INTRARESIDUE, 96 SEQUENTIAL INTRASTRAND, 36 INTERSTRAND INTERPROTON DISTANCE RESTRAINTS; 40 H-BOND RESTRAINTS; 72 TORSION ANGLE RESTRAINTS (FOR ALPHA, BETA, GAMMA, EPSILON AND ZETA BACKBONE TORSION ANGLES. (C) INTERMOLECULAR: 75 INTERPROTON DISTANCE RESTRAINTS |
- 試料調製
試料調製
| 結晶化 | *PLUS 手法: other / 詳細: NMR |
|---|
- 解析
解析
| ソフトウェア |
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR software | 名称:  X-PLOR / 開発者: BRUNGER / 分類: 精密化 X-PLOR / 開発者: BRUNGER / 分類: 精密化 | ||||||||||||
| 精密化 | 手法: simulated annealing / ソフトェア番号: 1 詳細: NUMBER OF ATOMS USED IN REFINEMENT. NUMBER OF PROTEIN ATOMS 644 NUMBER OF NUCLEIC ACID ATOMS 322 NUMBER OF HETEROGEN ATOMS 0 NUMBER OF SOLVENT ATOMS 0 THE STRUCTURES WERE CALCULATED USING THE ...詳細: NUMBER OF ATOMS USED IN REFINEMENT. NUMBER OF PROTEIN ATOMS 644 NUMBER OF NUCLEIC ACID ATOMS 322 NUMBER OF HETEROGEN ATOMS 0 NUMBER OF SOLVENT ATOMS 0 THE STRUCTURES WERE CALCULATED USING THE SIMULATED ANNEALING PROTOCOL OF NILGES ET AL. (1988) FEBS LETT. 229, 129 - 136 USING THE PROGRAM X-PLOR 3.1 (BRUNGER) MODIFIED TO INCORPORATE COUPLING CONSTANT (GARRETT ET AL. (1984) J. MAGN. RESON. SERIES B 104, 99 - 103) AND CARBON CHEMICAL SHIFT RESTRAINTS (KUSZEWSKI ET AL. (1995) MAGN. RESON. SERIES B 106, 92 - 96). THE 3D STRUCTURE OF THE HUMAN SRY-DNA COMPLEX SOLVED BY MULTI-DIMENSIONAL HETERONUCLEAR-EDITED AND -FILTERED NMR IS BASED ON 1805 EXPERIMENTAL RESTRAINTS: (A) INTRA-PROTEIN: 290 SEQUENTIAL (|I-J|=1), 221 MEDIUM RANGE (1 < |I-J| >=5) AND 107 LONG RANGE (|I-J| >5) INTERRESIDUES. 238 INTRARESIDUE APPROXIMATE INTERPROTON DISTANCE RESTRAINTS; 70 DISTANCE RESTRAINTS FOR 35 HYDROGEN BONDS; 153 TORSION ANGLE (71 PHI, 10 PSI, 56 CHI1 AND 16 CHI2) RESTRAINTS; 56 THREE-BOND HN-HA COUPLING CONSTANT RESTRAINTS; 145 (73 CALPHA AND 72 CBETA) 13C SHIFT RESTRAINTS. (B) INTRA-DNA: 206 INTRARESIDUE, 96 SEQUENTIAL INTRASTRAND, 36 INTERSTRAND INTERPROTON DISTANCE RESTRAINTS; 40 H-BOND RESTRAINTS; 72 TORSION ANGLE RESTRAINTS (FOR ALPHA, BETA, GAMMA, EPSILON AND ZETA BACKBONE TORSION ANGLES. (C) INTERMOLECULAR: 75 INTERPROTON DISTANCE RESTRAINTS THE STRUCTURE IN THIS ENTRY IS THE RESTRAINED REGULARIZED MEAN STRUCTURE. THE LAST COLUMN REPRESENTS THE RMS OF THE 35 INDIVIDUAL SIMULATED ANNEALING STRUCTURES ABOUT THE MEAN COORDINATE POSITIONS. THE 35 INDIVIDUAL STRUCTURES CAN BE FOUND IN PDB ENTRY 1HRZ. THE LAST COLUMN IN THE INDIVIDUAL SA STRUCTURES HAS NO MEANING. | ||||||||||||
| NMR constraints | NA other-angle constraints total count: 72 / NOE constraints total: 1805 / NOE intraresidue total count: 444 / NOE long range total count: 107 / NOE medium range total count: 221 / NOE sequential total count: 386 / Hydrogen bond constraints total count: 40 / Protein chi angle constraints total count: 72 / Protein other angle constraints total count: 271 / Protein phi angle constraints total count: 71 / Protein psi angle constraints total count: 10 | ||||||||||||
| NMRアンサンブル | 登録したコンフォーマーの数: 1 |
 ムービー
ムービー コントローラー
コントローラー










 PDBj
PDBj


