+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-7173 | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Single-Molecule 3D Image of DNA Origami Bennett Linkage by Individual Particle Electron Tomography (No. 042) | |||||||||||||||
 マップデータ マップデータ | Single-Molecule 3D Image of DNA Origami Bennett Linkage by Individual Particle Electron Tomography (No. 042) | |||||||||||||||
 試料 試料 |
| |||||||||||||||
| 生物種 |  Escherichia virus M13 (ウイルス) / synthetic construct (人工物) Escherichia virus M13 (ウイルス) / synthetic construct (人工物) | |||||||||||||||
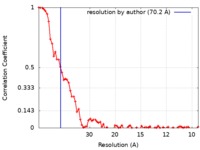
| 手法 | 電子線トモグラフィー法 / クライオ電子顕微鏡法 / ネガティブ染色法 / 解像度: 70.2 Å | |||||||||||||||
 データ登録者 データ登録者 | Lei D / Marras A / Liu J / Huang C / Zhou L / Castro C / Su H / Ren G | |||||||||||||||
| 資金援助 |  米国, 4件 米国, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2018 ジャーナル: Nat Commun / 年: 2018タイトル: Three-dimensional structural dynamics of DNA origami Bennett linkages using individual-particle electron tomography. 著者: Dongsheng Lei / Alexander E Marras / Jianfang Liu / Chao-Min Huang / Lifeng Zhou / Carlos E Castro / Hai-Jun Su / Gang Ren /  要旨: Scaffolded DNA origami has proven to be a powerful and efficient technique to fabricate functional nanomachines by programming the folding of a single-stranded DNA template strand into three- ...Scaffolded DNA origami has proven to be a powerful and efficient technique to fabricate functional nanomachines by programming the folding of a single-stranded DNA template strand into three-dimensional (3D) nanostructures, designed to be precisely motion-controlled. Although two-dimensional (2D) imaging of DNA nanomachines using transmission electron microscopy and atomic force microscopy suggested these nanomachines are dynamic in 3D, geometric analysis based on 2D imaging was insufficient to uncover the exact motion in 3D. Here we use the individual-particle electron tomography method and reconstruct 129 density maps from 129 individual DNA origami Bennett linkage mechanisms at ~ 6-14 nm resolution. The statistical analyses of these conformations lead to understanding the 3D structural dynamics of Bennett linkage mechanisms. Moreover, our effort provides experimental verification of a theoretical kinematics model of DNA origami, which can be used as feedback to improve the design and control of motion via optimized DNA sequences and routing. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_7173.map.gz emd_7173.map.gz | 24.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-7173-v30.xml emd-7173-v30.xml emd-7173.xml emd-7173.xml | 11.8 KB 11.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_7173_fsc.xml emd_7173_fsc.xml | 6.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_7173.png emd_7173.png | 25.7 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-7173 http://ftp.pdbj.org/pub/emdb/structures/EMD-7173 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7173 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7173 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_7173_validation.pdf.gz emd_7173_validation.pdf.gz | 78.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_7173_full_validation.pdf.gz emd_7173_full_validation.pdf.gz | 77.3 KB | 表示 | |
| XML形式データ |  emd_7173_validation.xml.gz emd_7173_validation.xml.gz | 494 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7173 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7173 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7173 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7173 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7155C  7156C  7157C  7158C  7159C  7160C  7161C  7162C  7163C  7164C  7165C  7166C  7167C  7168C  7169C  7170C  7171C  7172C  7174C  7175C  7176C  7177C  7178C  7179C  7180C  7181C  7182C  7183C  7184C  7185C  7186C  7187C  7188C  7189C  7190C  7191C  7192C  7193C  7194C  7195C  7196C  7197C  7198C  7199C  7200C  7201C  7202C  7203C  7204C  7205C  7206C  7207C  7208C  7209C  7210C  7211C  7212C  7213C  7214C  7215C  7216C  7217C  7218C  7219C  7220C  7221C  7222C  7223C  7224C  7225C  7226C  7227C  7228C  7229C  7230C  7231C  7232C  7233C  7234C  7235C  7236C  7237C  7238C  7239C  7240C  7241C  7242C  7243C  7244C  7245C  7246C  7247C  7248C  7249C  7250C  7251C  7252C  7253C  7254C  7255C  7256C  7257C  7258C  7259C  7260C  7261C  7262C  7263C  7264C  7265C  7266C  7267C  7268C  7269C  7270C  7271C  7272C  7273C  7274C  7275C  7276C  7277C  7278C  7279C  7280C  7281C  7282C  7283C  7284C  7285C C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_7173.map.gz / 形式: CCP4 / 大きさ: 27 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_7173.map.gz / 形式: CCP4 / 大きさ: 27 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Single-Molecule 3D Image of DNA Origami Bennett Linkage by Individual Particle Electron Tomography (No. 042) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 4.8 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : DNA origami Bennett linkage
| 全体 | 名称: DNA origami Bennett linkage |
|---|---|
| 要素 |
|
-超分子 #1: DNA origami Bennett linkage
| 超分子 | 名称: DNA origami Bennett linkage / タイプ: complex / ID: 1 / 親要素: 0 |
|---|
-超分子 #2: M13 phage genome segment
| 超分子 | 名称: M13 phage genome segment / タイプ: complex / ID: 2 / 親要素: 1 |
|---|---|
| 由来(天然) | 生物種:  Escherichia virus M13 (ウイルス) Escherichia virus M13 (ウイルス) |
| 組換発現 | 生物種:  |
-超分子 #3: Synthetic DNA oligonucleotides
| 超分子 | 名称: Synthetic DNA oligonucleotides / タイプ: complex / ID: 3 / 親要素: 1 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 組換発現 | 生物種:  |
-実験情報
-構造解析
| 手法 | ネガティブ染色法, クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 電子線トモグラフィー法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 詳細: Tris-Borate-EDTA (TBE) buffer containing 11 mM MgCl2 |
|---|---|
| 染色 | タイプ: NEGATIVE / 材質: Uranyl Formate 詳細: The grid was washed twice by 1% (w/v) uranyl formate |
| グリッド | 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: LACEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 0.039 kPa |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / チャンバー内温度: 277 K / 装置: LEICA EM GP |
| 詳細 | DNA origami Bennett linkage was diluted to ~2 nM with Tris-Borate-EDTA (TBE) buffer containing 11 mM MgCl2 |
| 切片作成 | その他: NO SECTIONING |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | ZEISS LIBRA120PLUS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: In-column Omega Filter |
| 撮影 | フィルム・検出器のモデル: GATAN ULTRASCAN 4000 (4k x 4k) デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 平均電子線量: 1.92 e/Å2 |
| 電子線 | 加速電圧: 120 kV / 電子線源: LAB6 |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.2 mm / 倍率(公称値): 50000 |
| 試料ステージ | 試料ホルダーモデル: GATAN CT3500 SINGLE TILT LIQUID NITROGEN CRYO TRANSFER HOLDER ホルダー冷却材: NITROGEN |
 ムービー
ムービー コントローラー
コントローラー



 UCSF Chimera
UCSF Chimera

 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)