+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Helical structure of KomBC in complex with dITP | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | KomBc / dITP / Sir2 / CELL INVASION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報nucleoside triphosphate catabolic process / nucleoside triphosphate diphosphatase activity / nucleotide metabolic process / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Archangium gephyra (バクテリア) Archangium gephyra (バクテリア) | |||||||||
| 手法 | らせん対称体再構成法 / クライオ電子顕微鏡法 / 解像度: 3.04 Å | |||||||||
 データ登録者 データ登録者 | Li Y / Zheng Q / Li S | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2026 ジャーナル: Mol Cell / 年: 2026タイトル: Filament-driven activation of the Kongming antiviral system by deoxyinosine triphosphate. 著者: Xiangkai Zhen / Yu Li / Zihe Liu / Yang Huang / Xurong Wang / Shuying Xu / Yuchen Jiang / Fan Li / Jinfu Su / Qi Lai / Shaowei Li / Ningshao Xia / Qingbing Zheng / Songying Ouyang /  要旨: Nucleotide-derived second messengers are frequently deployed by bacteria to activate effector proteins to mediate the immunity. The Kongming system uses deoxyinosine triphosphate (dITP) to trigger ...Nucleotide-derived second messengers are frequently deployed by bacteria to activate effector proteins to mediate the immunity. The Kongming system uses deoxyinosine triphosphate (dITP) to trigger nicotinamide adenine dinucleotide (NAD) depletion via the Sir2-domain protein KomC. We reveal that dITP binding to the KomB-KomC (KomBC) complex stabilizes KomB dimerization, initiating hierarchical allosteric changes. This drives KomBC filament assembly, which is essential for activating the NADase activity of KomC. Cryo-EM structures of apo-, dITP-bound, NAD-bound and postcatalytic KomBC filaments show the structural landscape of how dITP-induced remodeling reshapes the catalytic pocket of KomC, enabling NAD hydrolysis. Mutagenesis confirms that filament assembly and allostery are critical for catalysis. These findings elucidate the structural basis for the recognition of the nucleotide derivative signaling molecule, the assembly and the filament-mediated allosteric activation mechanism in prokaryotic immunity and a distinct variation of Sir2 NADase activation. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_64788.map.gz emd_64788.map.gz | 169.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-64788-v30.xml emd-64788-v30.xml emd-64788.xml emd-64788.xml | 25.3 KB 25.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_64788.png emd_64788.png | 102.6 KB | ||
| Filedesc metadata |  emd-64788.cif.gz emd-64788.cif.gz | 6.3 KB | ||
| その他 |  emd_64788_additional_1.map.gz emd_64788_additional_1.map.gz emd_64788_additional_2.map.gz emd_64788_additional_2.map.gz emd_64788_half_map_1.map.gz emd_64788_half_map_1.map.gz emd_64788_half_map_2.map.gz emd_64788_half_map_2.map.gz | 168.7 MB 165.7 MB 318.5 MB 318.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-64788 http://ftp.pdbj.org/pub/emdb/structures/EMD-64788 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-64788 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-64788 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9v57MC  9v0gC  9v0yC  9v0zC  9v12C  9v2kC  9v2mC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_64788.map.gz / 形式: CCP4 / 大きさ: 343 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_64788.map.gz / 形式: CCP4 / 大きさ: 343 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.778 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: #1
| ファイル | emd_64788_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: #2
| ファイル | emd_64788_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_64788_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_64788_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : KomBC filament with dITP
| 全体 | 名称: KomBC filament with dITP |
|---|---|
| 要素 |
|
-超分子 #1: KomBC filament with dITP
| 超分子 | 名称: KomBC filament with dITP / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Archangium gephyra (バクテリア) Archangium gephyra (バクテリア) |
-分子 #1: Xanthosine/inosine triphosphate pyrophosphatase
| 分子 | 名称: Xanthosine/inosine triphosphate pyrophosphatase / タイプ: protein_or_peptide / ID: 1 / コピー数: 8 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Archangium gephyra (バクテリア) Archangium gephyra (バクテリア) |
| 分子量 | 理論値: 20.012025 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MAPTWFYNTT NSEKLRELQH VLGGSAKLGY LTAKVTEILD VDLETVIRAK AIAAYRAVRV PVIVEHGALC IDALNGLPGA LVKPFWESL DTRLCEVIPA GQRTARARGA LCYCDGRERH VLIEETEGEI APSARGTGGF HWDPIFIPKG QTRTFAEMSL D EKLSFSPL GRLHTRLRTE LGL UniProtKB: XTP/dITP diphosphohydrolase |
-分子 #2: NAD-dependent protein deacetylase
| 分子 | 名称: NAD-dependent protein deacetylase / タイプ: protein_or_peptide / ID: 2 / コピー数: 8 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Archangium gephyra (バクテリア) Archangium gephyra (バクテリア) |
| 分子量 | 理論値: 31.370715 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MTTLTLSEAA PLLKKEFREG RLIPFLGAGF SKPLKLPDGS QLIASLAKTL GFEPELFDMH GRFEQLAEFF AISAPNRLQR LVYEMSLSF DSAEAEALRE KSPMHRALAA LDWRTIYTTN YDKHVEGALR DAGKQAAVLA SFADFQGPRA RDVCEVIKFH G TLDQPDTI ...文字列: MTTLTLSEAA PLLKKEFREG RLIPFLGAGF SKPLKLPDGS QLIASLAKTL GFEPELFDMH GRFEQLAEFF AISAPNRLQR LVYEMSLSF DSAEAEALRE KSPMHRALAA LDWRTIYTTN YDKHVEGALR DAGKQAAVLA SFADFQGPRA RDVCEVIKFH G TLDQPDTI VLTESSYFQR MALDAPPDQR LRADLLANSF LFIGYSFSDT NIRYIWYRMN QLREQSQLGV KHSQARRCFF AT HGAGLVQ PDILQQWNID VIQLDPTDKS ASVARLLESI A UniProtKB: NAD-dependent protein deacetylase |
-分子 #3: 2'-deoxyinosine 5'-triphosphate
| 分子 | 名称: 2'-deoxyinosine 5'-triphosphate / タイプ: ligand / ID: 3 / コピー数: 8 / 式: Y43 |
|---|---|
| 分子量 | 理論値: 492.166 Da |
| Chemical component information | 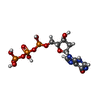 ChemComp-Y43: |
-分子 #4: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 4 / コピー数: 8 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F30 |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Tecnai F30 / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 想定した対称性 - らせんパラメータ - Δz: 49.25 Å 想定した対称性 - らせんパラメータ - ΔΦ: 83.37 ° 想定した対称性 - らせんパラメータ - 軸対称性: C2 (2回回転対称) 解像度のタイプ: BY AUTHOR / 解像度: 3.04 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 1574792 |
|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION |
| 初期モデル | モデルのタイプ: OTHER |
| 最終 角度割当 | タイプ: NOT APPLICABLE |
 ムービー
ムービー コントローラー
コントローラー












 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)




















































