[日本語] English
 万見
万見- EMDB-61947: Cryo-EM structure of UTP-bound P2Y purinoceptor 4-miniGq-Nb35 complex -
+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of UTP-bound P2Y purinoceptor 4-miniGq-Nb35 complex | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | G protein-coupled receptors / G-protein signaling / Nucleotide receptors / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報G protein-coupled UTP receptor activity / P2Y receptors / G protein-coupled purinergic nucleotide receptor activity / transepithelial chloride transport / regulation of presynaptic cytosolic calcium ion concentration / cellular response to ATP / regulation of synaptic vesicle exocytosis / PKA activation in glucagon signalling / hair follicle placode formation / developmental growth ...G protein-coupled UTP receptor activity / P2Y receptors / G protein-coupled purinergic nucleotide receptor activity / transepithelial chloride transport / regulation of presynaptic cytosolic calcium ion concentration / cellular response to ATP / regulation of synaptic vesicle exocytosis / PKA activation in glucagon signalling / hair follicle placode formation / developmental growth / D1 dopamine receptor binding / intracellular transport / vascular endothelial cell response to laminar fluid shear stress / renal water homeostasis / Hedgehog 'off' state / adenylate cyclase-activating adrenergic receptor signaling pathway / activation of adenylate cyclase activity / presynaptic active zone membrane / regulation of insulin secretion / cellular response to glucagon stimulus / adenylate cyclase activator activity / trans-Golgi network membrane / negative regulation of inflammatory response to antigenic stimulus / bone development / G-protein beta/gamma-subunit complex binding / platelet aggregation / cognition / Olfactory Signaling Pathway / Activation of the phototransduction cascade / G beta:gamma signalling through PLC beta / Presynaptic function of Kainate receptors / Thromboxane signalling through TP receptor / G protein-coupled acetylcholine receptor signaling pathway / adenylate cyclase-activating G protein-coupled receptor signaling pathway / G-protein activation / Activation of G protein gated Potassium channels / Inhibition of voltage gated Ca2+ channels via Gbeta/gamma subunits / Prostacyclin signalling through prostacyclin receptor / G beta:gamma signalling through CDC42 / Glucagon signaling in metabolic regulation / G beta:gamma signalling through BTK / Synthesis, secretion, and inactivation of Glucagon-like Peptide-1 (GLP-1) / ADP signalling through P2Y purinoceptor 12 / Sensory perception of sweet, bitter, and umami (glutamate) taste / photoreceptor disc membrane / Glucagon-type ligand receptors / Adrenaline,noradrenaline inhibits insulin secretion / Vasopressin regulates renal water homeostasis via Aquaporins / G alpha (z) signalling events / Glucagon-like Peptide-1 (GLP1) regulates insulin secretion / cellular response to catecholamine stimulus / ADORA2B mediated anti-inflammatory cytokines production / ADP signalling through P2Y purinoceptor 1 / G beta:gamma signalling through PI3Kgamma / Cooperation of PDCL (PhLP1) and TRiC/CCT in G-protein beta folding / adenylate cyclase-activating dopamine receptor signaling pathway / sensory perception of smell / GPER1 signaling / Inactivation, recovery and regulation of the phototransduction cascade / cellular response to prostaglandin E stimulus / G-protein beta-subunit binding / heterotrimeric G-protein complex / G alpha (12/13) signalling events / sensory perception of taste / extracellular vesicle / signaling receptor complex adaptor activity / Thrombin signalling through proteinase activated receptors (PARs) / positive regulation of cold-induced thermogenesis / G protein activity / positive regulation of cytosolic calcium ion concentration / GTPase binding / retina development in camera-type eye / Ca2+ pathway / High laminar flow shear stress activates signaling by PIEZO1 and PECAM1:CDH5:KDR in endothelial cells / fibroblast proliferation / G alpha (i) signalling events / basolateral plasma membrane / 加水分解酵素; 酸無水物に作用; GTPに作用・細胞または細胞小器官の運動に関与 / G alpha (s) signalling events / phospholipase C-activating G protein-coupled receptor signaling pathway / G alpha (q) signalling events / Ras protein signal transduction / Extra-nuclear estrogen signaling / cell population proliferation / G protein-coupled receptor signaling pathway / apical plasma membrane / lysosomal membrane / GTPase activity / synapse / protein-containing complex binding / GTP binding / glutamatergic synapse / signal transduction / extracellular exosome / ATP binding / metal ion binding / membrane / plasma membrane / cytosol / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / Homo sapiens (ヒト) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.14 Å | |||||||||
 データ登録者 データ登録者 | Lan B / Zhang S / Liu X / Lin B | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell Discov / 年: 2025 ジャーナル: Cell Discov / 年: 2025タイトル: Structural insight into the self-activation and G-protein coupling of P2Y2 receptor. 著者: Baoliang Lan / Shuhao Zhang / Kai Chen / Shengjie Dai / Jiaqi Fei / Kaixuan Gao / Xiaoou Sun / Bin Lin / Xiangyu Liu /  要旨: Purinergic P2Y2 receptor (P2Y2R) represents a typically extracellular ATP and UTP sensor for mediating purinergic signaling. Despite its importance as a pharmacological target, the molecular ...Purinergic P2Y2 receptor (P2Y2R) represents a typically extracellular ATP and UTP sensor for mediating purinergic signaling. Despite its importance as a pharmacological target, the molecular mechanisms underlying ligand recognition and G-protein coupling have remained elusive due to lack of structural information. In this study, we determined the cryo-electron microscopy (cryo-EM) structures of the apo P2Y2R in complex with G, ATP-bound P2Y2R in complex with G or G, and UTP-bound P2Y4R in complex with G. These structures reveal the similarities and distinctions of ligand recognition within the P2Y receptor family. Furthermore, a comprehensive analysis of G-protein coupling reveals that P2Y2R exhibits promiscuity in coupling with both G and G proteins. Combining molecular dynamics simulations and signaling assays, we elucidate the molecular mechanisms by which P2Y2R differentiates pathway-specific G or G coupling through distinct structural components on the intracellular side. Strikingly, we identify a helix-like segment within the N-terminus that occupies the orthosteric ligand-binding pocket of P2Y2R, accounting for its self-activation. Taken together, these findings provide a molecular framework for understanding the activation mechanism of P2Y2R, encompassing ligand recognition, G-protein coupling, and a novel N-terminus-mediated self-activation mechanism. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_61947.map.gz emd_61947.map.gz | 42.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-61947-v30.xml emd-61947-v30.xml emd-61947.xml emd-61947.xml | 19.4 KB 19.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_61947.png emd_61947.png | 75.8 KB | ||
| Filedesc metadata |  emd-61947.cif.gz emd-61947.cif.gz | 6.5 KB | ||
| その他 |  emd_61947_half_map_1.map.gz emd_61947_half_map_1.map.gz emd_61947_half_map_2.map.gz emd_61947_half_map_2.map.gz | 41.9 MB 41.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-61947 http://ftp.pdbj.org/pub/emdb/structures/EMD-61947 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-61947 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-61947 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_61947.map.gz / 形式: CCP4 / 大きさ: 45.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_61947.map.gz / 形式: CCP4 / 大きさ: 45.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.0825 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_61947_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_61947_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Cryo-EM structure of UTP-bound P2Y purinoceptor 4-miniGq-Nb35 complex
| 全体 | 名称: Cryo-EM structure of UTP-bound P2Y purinoceptor 4-miniGq-Nb35 complex |
|---|---|
| 要素 |
|
-超分子 #1: Cryo-EM structure of UTP-bound P2Y purinoceptor 4-miniGq-Nb35 complex
| 超分子 | 名称: Cryo-EM structure of UTP-bound P2Y purinoceptor 4-miniGq-Nb35 complex タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#5 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Guanine nucleotide-binding protein G(s) subunit alpha isoforms short
| 分子 | 名称: Guanine nucleotide-binding protein G(s) subunit alpha isoforms short タイプ: protein_or_peptide / ID: 1 詳細: The N-terminal sequence of Gi1 is incorporated into the mini-G protein;Certain residues mutated to match Guanine nucleotide-binding protein G(q) subunit コピー数: 1 / 光学異性体: LEVO EC番号: 加水分解酵素; 酸無水物に作用; GTPに作用・細胞または細胞小器官の運動に関与 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 28.01476 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: TLSAEDKAAV ERSKMIEKQL QKDKQVYRAT HRLLLLGADN SGKSTIVKQM RILHGGSGGS GGTSGIFETK FQVDKVNFHM FDVGGQRDE RRKWIQCFND VTAIIFVVDS SDYNRLQEAL NDFKSIWNNR WLRTISVILF LNKQDLLAEK VLAGKSKIED Y FPEFARYT ...文字列: TLSAEDKAAV ERSKMIEKQL QKDKQVYRAT HRLLLLGADN SGKSTIVKQM RILHGGSGGS GGTSGIFETK FQVDKVNFHM FDVGGQRDE RRKWIQCFND VTAIIFVVDS SDYNRLQEAL NDFKSIWNNR WLRTISVILF LNKQDLLAEK VLAGKSKIED Y FPEFARYT TPEDATPEPG EDPRVTRAKY FIRDEFLRIS TASGDGRHYC YPHFTCAVDT ENARRIFNDC KDIILQMNLR EY NLV UniProtKB: Guanine nucleotide-binding protein G(s) subunit alpha isoforms short, Guanine nucleotide-binding protein G(s) subunit alpha isoforms short |
-分子 #2: Guanine nucleotide-binding protein G(I)/G(S)/G(T) subunit beta-1
| 分子 | 名称: Guanine nucleotide-binding protein G(I)/G(S)/G(T) subunit beta-1 タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 39.418086 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MHHHHHHLEV LFQGPGSSGS ELDQLRQEAE QLKNQIRDAR KACADATLSQ ITNNIDPVGR IQMRTRRTLR GHLAKIYAMH WGTDSRLLV SASQDGKLII WDSYTTNKVH AIPLRSSWVM TCAYAPSGNY VACGGLDNIC SIYNLKTREG NVRVSRELAG H TGYLSCCR ...文字列: MHHHHHHLEV LFQGPGSSGS ELDQLRQEAE QLKNQIRDAR KACADATLSQ ITNNIDPVGR IQMRTRRTLR GHLAKIYAMH WGTDSRLLV SASQDGKLII WDSYTTNKVH AIPLRSSWVM TCAYAPSGNY VACGGLDNIC SIYNLKTREG NVRVSRELAG H TGYLSCCR FLDDNQIVTS SGDTTCALWD IETGQQTTTF TGHTGDVMSL SLAPDTRLFV SGACDASAKL WDVREGMCRQ TF TGHESDI NAICFFPNGN AFATGSDDAT CRLFDLRADQ ELMTYSHDNI ICGITSVSFS KSGRLLLAGY DDFNCNVWDA LKA DRAGVL AGHDNRVSCL GVTDDGMAVA TGSWDSFLKI WN UniProtKB: Guanine nucleotide-binding protein G(I)/G(S)/G(T) subunit beta-1 |
-分子 #3: Guanine nucleotide-binding protein G(I)/G(S)/G(O) subunit gamma-2
| 分子 | 名称: Guanine nucleotide-binding protein G(I)/G(S)/G(O) subunit gamma-2 タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 7.861143 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MASNNTASIA QARKLVEQLK MEANIDRIKV SKAAADLMAY CEAHAKEDPL LTPVPASENP FREKKFFCAI L UniProtKB: Guanine nucleotide-binding protein G(I)/G(S)/G(O) subunit gamma-2 |
-分子 #4: Nanobody 35
| 分子 | 名称: Nanobody 35 / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 14.686328 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: QVQLQESGGG LVQPGGSLRL SCAASGFTFS NYKMNWVRQA PGKGLEWVSD ISQSGASISY TGSVKGRFTI SRDNAKNTLY LQMNSLKPE DTAVYYCARC PAPFTPFCFD VTSTTYAYRG QGTQVTVSSH HHHHH |
-分子 #5: P2Y purinoceptor 4
| 分子 | 名称: P2Y purinoceptor 4 / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 45.787227 KDa |
| 組換発現 | 生物種:  Homo (哺乳類) Homo (哺乳類) |
| 配列 | 文字列: MKTIIALSYI FCLVFADYKD DDDAMASTES SLLRSLGLSP GPGSSEVELD CWFDEDFKFI LLPVSYAVVF VLGLGLNAPT LWLFIFRLR PWDATATYMF HLALSDTLYV LSLPTLIYYY AAHNHWPFGT EICKFVRFLF YWNLYCSVLF LTCISVHRYL G ICHPLRAL ...文字列: MKTIIALSYI FCLVFADYKD DDDAMASTES SLLRSLGLSP GPGSSEVELD CWFDEDFKFI LLPVSYAVVF VLGLGLNAPT LWLFIFRLR PWDATATYMF HLALSDTLYV LSLPTLIYYY AAHNHWPFGT EICKFVRFLF YWNLYCSVLF LTCISVHRYL G ICHPLRAL RWGRPRLAGL LCLAVWLVVA GCLVPNLFFV TTSNKGTTVL CHDTTRPEEF DHYVHFSSAV MGLLFGVPCL VT LVCYGLM ARRLYQPLPG SAQSSSRLRS LRTIAVVLTV FAVCFVPFHI TRTIYYLARL LEADCRVLNI VNVVYKVTRP LAS ANSCLD PVLYLLTGDK YRRQLRQLCG GGKPQPRTAA SSLALVSLPE DSSCRWAATP QDSSCSTPRA DRLHHHHHHG GSGG LEVLF QGP UniProtKB: P2Y purinoceptor 4 |
-分子 #6: URIDINE 5'-TRIPHOSPHATE
| 分子 | 名称: URIDINE 5'-TRIPHOSPHATE / タイプ: ligand / ID: 6 / コピー数: 1 / 式: UTP |
|---|---|
| 分子量 | 理論値: 484.141 Da |
| Chemical component information | 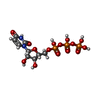 ChemComp-UTP: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.6 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー
































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)




































