+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | cryo-EM structure of a tmFAP | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | de novo protein design / transmembrane protein / ligand binding / fluorogenic / membrane / fluorescent protein. / MEMBRANE PROTEIN/IMMUNE SYSTEM / MEMBRANE PROTEIN-IMMUNE SYSTEM complex | |||||||||
| 生物種 | artificial sequences (その他) /  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.74 Å | |||||||||
 データ登録者 データ登録者 | Sun K / Zhu JY / Liang MF / Lu PL | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2025 ジャーナル: Nature / 年: 2025タイトル: De novo design of transmembrane fluorescence-activating proteins. 著者: Jingyi Zhu / Mingfu Liang / Ke Sun / Yu Wei / Ruiying Guo / Lijing Zhang / Junhui Shi / Dan Ma / Qi Hu / Gaoxingyu Huang / Peilong Lu /  要旨: The recognition of ligands by transmembrane proteins is essential for the exchange of materials, energy and information across biological membranes. Progress has been made in the de novo design of ...The recognition of ligands by transmembrane proteins is essential for the exchange of materials, energy and information across biological membranes. Progress has been made in the de novo design of transmembrane proteins, as well as in designing water-soluble proteins to bind small molecules, but de novo design of transmembrane proteins that tightly and specifically bind to small molecules remains an outstanding challenge. Here we present the accurate design of ligand-binding transmembrane proteins by integrating deep learning and energy-based methods. We designed pre-organized ligand-binding pockets in high-quality four-helix backbones for a fluorogenic ligand, and generated a transmembrane span using gradient-guided hallucination. The designer transmembrane proteins specifically activated fluorescence of the target fluorophore with mid-nanomolar affinity, exhibiting higher brightness and quantum yield compared to those of enhanced green fluorescent protein. These proteins were highly active in the membrane fraction of live bacterial and eukaryotic cells following expression. The crystal and cryogenic electron microscopy structures of the designer protein-ligand complexes were very close to the structures of the design models. We showed that the interactions between ligands and transmembrane proteins within the membrane can be accurately designed. Our work paves the way for the creation of new functional transmembrane proteins, with a wide range of applications including imaging, ligand sensing and membrane transport. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_60929.map.gz emd_60929.map.gz | 25.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-60929-v30.xml emd-60929-v30.xml emd-60929.xml emd-60929.xml | 21.7 KB 21.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_60929.png emd_60929.png | 76.2 KB | ||
| Filedesc metadata |  emd-60929.cif.gz emd-60929.cif.gz | 6.6 KB | ||
| その他 |  emd_60929_half_map_1.map.gz emd_60929_half_map_1.map.gz emd_60929_half_map_2.map.gz emd_60929_half_map_2.map.gz | 25.1 MB 25.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-60929 http://ftp.pdbj.org/pub/emdb/structures/EMD-60929 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-60929 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-60929 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_60929_validation.pdf.gz emd_60929_validation.pdf.gz | 721.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_60929_full_validation.pdf.gz emd_60929_full_validation.pdf.gz | 721.3 KB | 表示 | |
| XML形式データ |  emd_60929_validation.xml.gz emd_60929_validation.xml.gz | 10.6 KB | 表示 | |
| CIF形式データ |  emd_60929_validation.cif.gz emd_60929_validation.cif.gz | 12.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-60929 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-60929 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-60929 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-60929 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_60929.map.gz / 形式: CCP4 / 大きさ: 27 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_60929.map.gz / 形式: CCP4 / 大きさ: 27 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.14 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : De novo design of HBC599 membrane protein binder
| 全体 | 名称: De novo design of HBC599 membrane protein binder |
|---|---|
| 要素 |
|
-超分子 #1: De novo design of HBC599 membrane protein binder
| 超分子 | 名称: De novo design of HBC599 membrane protein binder / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種: artificial sequences (その他) |
-分子 #1: HBC599 membrane protein binder
| 分子 | 名称: HBC599 membrane protein binder / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: artificial sequences (その他) |
| 分子量 | 理論値: 33.037648 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: DEERLKEILF FLLLIIIFVV FLLIVDYKFL EEFKEKNVTD KEEFNEVIKI DEAVMLISAF LLAIAAALLK ELEELIRKRF EEWEKEEET LKKLEDNWET LNDNLKVIEK ADNAAQVKDA LTKMRAAALD AQKATPPKLE DKSPDSPEMK DFRHGFDILV G QIDDALKL ...文字列: DEERLKEILF FLLLIIIFVV FLLIVDYKFL EEFKEKNVTD KEEFNEVIKI DEAVMLISAF LLAIAAALLK ELEELIRKRF EEWEKEEET LKKLEDNWET LNDNLKVIEK ADNAAQVKDA LTKMRAAALD AQKATPPKLE DKSPDSPEMK DFRHGFDILV G QIDDALKL ANEGKVKEAQ AAAEQLKTTR NAYIQKYLEK AKETMEKRKE IRRELEKILG VLAGLYVGAA FLMVIAKFLT KK IKEENTT DKEKLNEWYE FVYVLLIFAF FIILAIAVVL LKLLEILG |
-分子 #2: Heavy chain, Fab fragment
| 分子 | 名称: Heavy chain, Fab fragment / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 24.321084 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: EISEVQLVES GGGLVQPGGS LRLSCAASGF NVVDFSLHWV RQAPGKGLEW VAYISSSSGS TSYADSVKGR FTISADTSKN TAYLQMNSL RAEDTAVYYC ARWGYWPGEP WWKAFDYWGQ GTLVTVSSAS TKGPSVFPLA PSSKSTSGGT AALGCLVKDY F PEPVTVSW ...文字列: EISEVQLVES GGGLVQPGGS LRLSCAASGF NVVDFSLHWV RQAPGKGLEW VAYISSSSGS TSYADSVKGR FTISADTSKN TAYLQMNSL RAEDTAVYYC ARWGYWPGEP WWKAFDYWGQ GTLVTVSSAS TKGPSVFPLA PSSKSTSGGT AALGCLVKDY F PEPVTVSW NSGALTSGVH TFPAVLQSSG LYSLSSVVTV PSSSLGTQTY ICNVNHKPSN TKVDKKVEPK S |
-分子 #3: Light Chain, Fab fragment
| 分子 | 名称: Light Chain, Fab fragment / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.353947 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: SDIQMTQSPS SLSASVGDRV TITCRASQSV SSAVAWYQQK PGKAPKLLIY SASSLYSGVP SRFSGSRSGT DFTLTISSLQ PEDFATYYC QQYLYYSLVT FGQGTKVEIK RTVAAPSVFI FPPSDSQLKS GTASVVCLLN NFYPREAKVQ WKVDNALQSG N SQESVTEQ ...文字列: SDIQMTQSPS SLSASVGDRV TITCRASQSV SSAVAWYQQK PGKAPKLLIY SASSLYSGVP SRFSGSRSGT DFTLTISSLQ PEDFATYYC QQYLYYSLVT FGQGTKVEIK RTVAAPSVFI FPPSDSQLKS GTASVVCLLN NFYPREAKVQ WKVDNALQSG N SQESVTEQ DSKDSTYSLS STLTLSKADY EKHKVYACEV THQGLSSPVT KSFNRG |
-分子 #4: 4-[(Z)-1-cyano-2-{6-[(2-hydroxyethyl)(methyl)amino]-1-benzothioph...
| 分子 | 名称: 4-[(Z)-1-cyano-2-{6-[(2-hydroxyethyl)(methyl)amino]-1-benzothiophen-2-yl}ethenyl]benzonitrile タイプ: ligand / ID: 4 / コピー数: 1 / 式: KY6 |
|---|---|
| 分子量 | 理論値: 359.444 Da |
| Chemical component information | 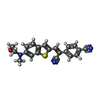 ChemComp-KY6: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 7.6 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 |
| 凍結 | 凍結剤: ETHANE-PROPANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.0 µm 最小 デフォーカス(公称値): 1.4000000000000001 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.74 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 453223 |
| 初期 角度割当 | タイプ: ANGULAR RECONSTITUTION |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー






