+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the light-driven sodium pump ErNaR in the pentameric form | |||||||||
 マップデータ マップデータ | Sharpened consensus map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | rhodopsin / ErNaR / sodium pump / phototransduction / MEMBRANE PROTEIN | |||||||||
| 生物種 |  Erythrobacter (バクテリア) Erythrobacter (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.1 Å | |||||||||
 データ登録者 データ登録者 | Haubner M / Williams HM / Hruby J / Straub MS / Guskov A / Kovalev K / Drabbels M / Lorenz UJ | |||||||||
| 資金援助 |  スイス, 1件 スイス, 1件
| |||||||||
 引用 引用 |  ジャーナル: bioRxiv / 年: 2025 ジャーナル: bioRxiv / 年: 2025タイトル: Microsecond Time-Resolved Cryo-EM Based on Jet Vitrification. 著者: Michal Haubner / Harry M Williams / Jakub Hruby / Monique S Straub / Albert Guskov / Kirill Kovalev / Marcel Drabbels / Ulrich J Lorenz /    要旨: Understanding and ultimately predicting the function of proteins is one of the frontiers in structural biology. This will only be possible if it becomes feasible to routinely observe proteins on the ...Understanding and ultimately predicting the function of proteins is one of the frontiers in structural biology. This will only be possible if it becomes feasible to routinely observe proteins on the fast timescales on which they perform their tasks. Recently, laser flash melting and revitrification experiments have improved the time resolution of cryo-electron microscopy (cryo-EM) to microseconds, rendering it fast enough to observe the domain motions of proteins that are frequently linked to function. However, observations have been limited to a time window of just a few hundred microseconds. Here, we introduce time-resolved cryo-EM experiments based on jet vitrification that combine microsecond resolution with an observation window of up to seconds. We use a short laser pulse to initiate protein dynamics, and as they unfold, vitrify the sample with a jet of a liquid cryogen to arrest the dynamics at that point in time. We demonstrate that our approach affords near-atomic spatial resolution and a time resolution of 21 µs. This allows us to observe the photoinduced dynamics of the light-driven sodium pump NaR on the microsecond to millisecond timescale. Our experiments significantly expand the ability of cryo-EM to observe protein dynamics across multiple timescales. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_55765.map.gz emd_55765.map.gz | 778.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-55765-v30.xml emd-55765-v30.xml emd-55765.xml emd-55765.xml | 22.4 KB 22.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_55765.png emd_55765.png | 67.5 KB | ||
| マスクデータ |  emd_55765_msk_1.map emd_55765_msk_1.map | 824 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-55765.cif.gz emd-55765.cif.gz | 6.5 KB | ||
| その他 |  emd_55765_half_map_1.map.gz emd_55765_half_map_1.map.gz emd_55765_half_map_2.map.gz emd_55765_half_map_2.map.gz | 765.6 MB 765.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-55765 http://ftp.pdbj.org/pub/emdb/structures/EMD-55765 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-55765 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-55765 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_55765.map.gz / 形式: CCP4 / 大きさ: 824 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_55765.map.gz / 形式: CCP4 / 大きさ: 824 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened consensus map | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.726 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_55765_msk_1.map emd_55765_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map A
| ファイル | emd_55765_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map B
| ファイル | emd_55765_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : ErNaR light-driven sodium pump
| 全体 | 名称: ErNaR light-driven sodium pump |
|---|---|
| 要素 |
|
-超分子 #1: ErNaR light-driven sodium pump
| 超分子 | 名称: ErNaR light-driven sodium pump / タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Erythrobacter (バクテリア) Erythrobacter (バクテリア) |
-分子 #1: Bacteriorhodopsin-like protein
| 分子 | 名称: Bacteriorhodopsin-like protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 5 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Erythrobacter (バクテリア) Erythrobacter (バクテリア) |
| 分子量 | 理論値: 30.560346 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: (FME)PSIENFLAY DFWQYDVIRH LFAFSTAVFL AGLVYFAMTA RTTAPNYRLS ANISAVVMVS AALELGQLWL LWNESF QWA ELQGSFVPVA GERFSNGYRY MNWLIDVPML ATQLVVVCGF VGTELRNRWA KLTIAGVLMI LTGYVGQYFE PAVAGVP GY ...文字列: (FME)PSIENFLAY DFWQYDVIRH LFAFSTAVFL AGLVYFAMTA RTTAPNYRLS ANISAVVMVS AALELGQLWL LWNESF QWA ELQGSFVPVA GERFSNGYRY MNWLIDVPML ATQLVVVCGF VGTELRNRWA KLTIAGVLMI LTGYVGQYFE PAVAGVP GY EGAEQFWIWG IISTAFFVWM LLILANAVRN PQGAPSDEVR SRLKFCFWFL LATWSIYPFA YAMPLFAPTA DGVVVRQV I YTVADVSSKL VFGVILSQVA LRRSAEEGFE PARVA |
-分子 #2: EICOSANE
| 分子 | 名称: EICOSANE / タイプ: ligand / ID: 2 / コピー数: 46 / 式: LFA |
|---|---|
| 分子量 | 理論値: 282.547 Da |
| Chemical component information |  ChemComp-LFA: |
-分子 #3: DODECYL-BETA-D-MALTOSIDE
| 分子 | 名称: DODECYL-BETA-D-MALTOSIDE / タイプ: ligand / ID: 3 / コピー数: 10 / 式: LMT |
|---|---|
| 分子量 | 理論値: 510.615 Da |
| Chemical component information |  ChemComp-LMT: |
-分子 #4: RETINAL
| 分子 | 名称: RETINAL / タイプ: ligand / ID: 4 / コピー数: 5 / 式: RET |
|---|---|
| 分子量 | 理論値: 284.436 Da |
| Chemical component information | 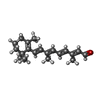 ChemComp-RET: |
-分子 #5: water
| 分子 | 名称: water / タイプ: ligand / ID: 5 / コピー数: 428 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 4.5 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
詳細: 10 mM HEPES pH 7.5, 150 mM NaCl | ||||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 200 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 90 sec. / 前処理 - 雰囲気: AIR 詳細: Grid was sputter coated with 40 nm thick layer of silver beforehand using a Quorum Q300T device. | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV 詳細: Vitrification carried out using a modified Vitrobot Mark IV, as outlined in the paper reporting this entry.. | ||||||||||||
| 詳細 | This sample was monodisperse. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 165000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)












































