+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Human DNA polymerase epsilon bound to DNA and PCNA (closed conformation) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | DNA / polymerase / epsilon / PCNA / leading strand / human / replication / replisome / proofreading | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報DNA replication initiation / epsilon DNA polymerase complex / positive regulation of deoxyribonuclease activity / dinucleotide insertion or deletion binding / PCNA-p21 complex / mitotic telomere maintenance via semi-conservative replication / purine-specific mismatch base pair DNA N-glycosylase activity / nucleotide-excision repair, DNA gap filling / nuclear lamina / positive regulation of DNA-directed DNA polymerase activity ...DNA replication initiation / epsilon DNA polymerase complex / positive regulation of deoxyribonuclease activity / dinucleotide insertion or deletion binding / PCNA-p21 complex / mitotic telomere maintenance via semi-conservative replication / purine-specific mismatch base pair DNA N-glycosylase activity / nucleotide-excision repair, DNA gap filling / nuclear lamina / positive regulation of DNA-directed DNA polymerase activity / Polymerase switching / MutLalpha complex binding / Telomere C-strand (Lagging Strand) Synthesis / Processive synthesis on the lagging strand / DNA replication proofreading / PCNA complex / single-stranded DNA 3'-5' DNA exonuclease activity / Removal of the Flap Intermediate / Processive synthesis on the C-strand of the telomere / Polymerase switching on the C-strand of the telomere / Mismatch repair (MMR) directed by MSH2:MSH3 (MutSbeta) / Mismatch repair (MMR) directed by MSH2:MSH6 (MutSalpha) / Removal of the Flap Intermediate from the C-strand / Transcription of E2F targets under negative control by DREAM complex / replisome / response to L-glutamate / 加水分解酵素; エステル加水分解酵素; 5'-リン酸モノエステル産生エンドデオキシリボヌクレアーゼ / response to dexamethasone / DNA synthesis involved in DNA repair / histone acetyltransferase binding / DNA polymerase processivity factor activity / leading strand elongation / G1/S-Specific Transcription / nuclear replication fork / replication fork processing / SUMOylation of DNA replication proteins / PCNA-Dependent Long Patch Base Excision Repair / Activation of the pre-replicative complex / embryonic organ development / response to cadmium ion / translesion synthesis / mismatch repair / estrous cycle / cyclin-dependent protein kinase holoenzyme complex / Translesion synthesis by REV1 / Translesion synthesis by POLK / base-excision repair, gap-filling / DNA polymerase binding / Translesion synthesis by POLI / Gap-filling DNA repair synthesis and ligation in GG-NER / epithelial cell differentiation / liver regeneration / positive regulation of DNA repair / TP53 Regulates Transcription of Genes Involved in G2 Cell Cycle Arrest / Termination of translesion DNA synthesis / positive regulation of DNA replication / replication fork / Recognition of DNA damage by PCNA-containing replication complex / nuclear estrogen receptor binding / Translesion Synthesis by POLH / male germ cell nucleus / HDR through Homologous Recombination (HRR) / Dual Incision in GG-NER / G1/S transition of mitotic cell cycle / receptor tyrosine kinase binding / Dual incision in TC-NER / Gap-filling DNA repair synthesis and ligation in TC-NER / DNA-templated DNA replication / cellular response to hydrogen peroxide / cellular response to xenobiotic stimulus / cellular response to UV / E3 ubiquitin ligases ubiquitinate target proteins / response to estradiol / mitotic cell cycle / heart development / chromatin organization / 4 iron, 4 sulfur cluster binding / damaged DNA binding / DNA-directed DNA polymerase / DNA-directed DNA polymerase activity / chromosome, telomeric region / DNA replication / nuclear body / nucleotide binding / centrosome / chromatin binding / chromatin / protein-containing complex binding / enzyme binding / negative regulation of transcription by RNA polymerase II / DNA binding / extracellular exosome / zinc ion binding / nucleoplasm / identical protein binding / nucleus / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / synthetic construct (人工物) Homo sapiens (ヒト) / synthetic construct (人工物) | |||||||||
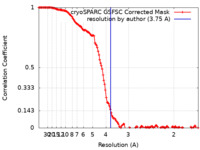
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.75 Å | |||||||||
 データ登録者 データ登録者 | Roske JJ / Yeeles JTP | |||||||||
| 資金援助 |  英国, 1件 英国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2024 ジャーナル: Nat Struct Mol Biol / 年: 2024タイトル: Structural basis for processive daughter-strand synthesis and proofreading by the human leading-strand DNA polymerase Pol ε. 著者: Johann J Roske / Joseph T P Yeeles /  要旨: During chromosome replication, the nascent leading strand is synthesized by DNA polymerase epsilon (Pol ε), which associates with the sliding clamp processivity factor proliferating cell nuclear ...During chromosome replication, the nascent leading strand is synthesized by DNA polymerase epsilon (Pol ε), which associates with the sliding clamp processivity factor proliferating cell nuclear antigen (PCNA) to form a processive holoenzyme. For high-fidelity DNA synthesis, Pol ε relies on nucleotide selectivity and its proofreading ability to detect and excise a misincorporated nucleotide. Here, we present cryo-electron microscopy (cryo-EM) structures of human Pol ε in complex with PCNA, DNA and an incoming nucleotide, revealing how Pol ε associates with PCNA through its PCNA-interacting peptide box and additional unique features of its catalytic domain. Furthermore, by solving a series of cryo-EM structures of Pol ε at a mismatch-containing DNA, we elucidate how Pol ε senses and edits a misincorporated nucleotide. Our structures delineate steps along an intramolecular switching mechanism between polymerase and exonuclease activities, providing the basis for a proofreading mechanism in B-family replicative polymerases. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_50224.map.gz emd_50224.map.gz | 223.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-50224-v30.xml emd-50224-v30.xml emd-50224.xml emd-50224.xml | 19.9 KB 19.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_50224_fsc.xml emd_50224_fsc.xml | 14.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_50224.png emd_50224.png | 144.2 KB | ||
| マスクデータ |  emd_50224_msk_1.map emd_50224_msk_1.map | 236.9 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-50224.cif.gz emd-50224.cif.gz | 6.9 KB | ||
| その他 |  emd_50224_additional_1.map.gz emd_50224_additional_1.map.gz emd_50224_half_map_1.map.gz emd_50224_half_map_1.map.gz emd_50224_half_map_2.map.gz emd_50224_half_map_2.map.gz | 2.3 MB 219.9 MB 219.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-50224 http://ftp.pdbj.org/pub/emdb/structures/EMD-50224 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-50224 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-50224 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_50224_validation.pdf.gz emd_50224_validation.pdf.gz | 1020.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_50224_full_validation.pdf.gz emd_50224_full_validation.pdf.gz | 1019.8 KB | 表示 | |
| XML形式データ |  emd_50224_validation.xml.gz emd_50224_validation.xml.gz | 21.4 KB | 表示 | |
| CIF形式データ |  emd_50224_validation.cif.gz emd_50224_validation.cif.gz | 26.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-50224 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-50224 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-50224 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-50224 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9f6fMC  9f6dC  9f6eC  9f6iC  9f6jC  9f6kC  9f6lC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_50224.map.gz / 形式: CCP4 / 大きさ: 236.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_50224.map.gz / 形式: CCP4 / 大きさ: 236.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.84065 Å | ||||||||||||||||||||||||||||||||||||
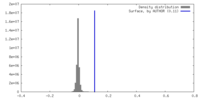
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_50224_msk_1.map emd_50224_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
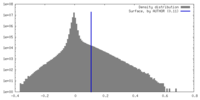
| 密度ヒストグラム |
-追加マップ: #1
| ファイル | emd_50224_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
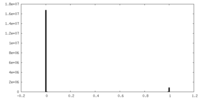
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_50224_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
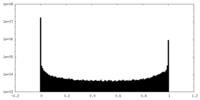
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_50224_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Quaternary Complex of human leading strand polymerase epsilon, Pr...
| 全体 | 名称: Quaternary Complex of human leading strand polymerase epsilon, Proliferating cell nuclear antigen (PCNA), substrate DNA and incoming nucleotide. |
|---|---|
| 要素 |
|
-超分子 #1: Quaternary Complex of human leading strand polymerase epsilon, Pr...
| 超分子 | 名称: Quaternary Complex of human leading strand polymerase epsilon, Proliferating cell nuclear antigen (PCNA), substrate DNA and incoming nucleotide. タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: DNA polymerase epsilon catalytic subunit A
| 分子 | 名称: DNA polymerase epsilon catalytic subunit A / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: DNA-directed DNA polymerase |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 138.137562 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MSLRSGGRRR ADPGADGEAS RDDGATSSVS ALKRLERSQW TDKMDLRFGF ERLKEPGEKT GWLINMHPTE ILDEDKRLGS AVDYYFIQD DGSRFKVALP YKPYFYIATR KGCEREVSSF LSKKFQGKIA KVETVPKEDL DLPNHLVGLK RNYIRLSFHT V EDLVKVRK ...文字列: MSLRSGGRRR ADPGADGEAS RDDGATSSVS ALKRLERSQW TDKMDLRFGF ERLKEPGEKT GWLINMHPTE ILDEDKRLGS AVDYYFIQD DGSRFKVALP YKPYFYIATR KGCEREVSSF LSKKFQGKIA KVETVPKEDL DLPNHLVGLK RNYIRLSFHT V EDLVKVRK EISPAVKKNR EQDHASDAYT ALLSSVLQRG GVITDEEETS KKIADQLDNI VDMREYDVPY HIRLSIDLKI HV AHWYNVR YRGNAFPVEI TRRDDLVERP DPVVLAFAIA TTKLPLKFPD AETDQIMMIS YMIDGQGYLI TNREIVSEDI EDF EFTPKP EYEGPFCVFN EPDEAHLIQR WFEHVQETKP TIMVTYNGDF FDWPFVEARA AVHGLSMQQE IGFQKDSQGE YKAP QCIHM DCLRWVKRDS YLPVGSHNLK AAAKAKLGYD PVELDPEDMC RMATEQPQTL ATYSVSDAVA TYYLYMKYVH PFIFA LCTI IPMEPDEVLR KGSGTLCEAL LMVQAFHANI IFPNKQEQEF NKLTDDGHVL DSETYVGGHV EALESGVFRS DIPCRF RMN PAAFDFLLQR VEKTLRHALE EEEKVPVEQV TNFEEVCDEI KSKLASLKDV PSRIECPLIY HLDVGAMYPN IILTNRL QP SAMVDEATCA ACDFNKPGAN CQRKMAWQWR GEFMPASRSE YHRIQHQLES EKFPPLFPEG PARAFHELSR EEQAKYEK R RLADYCRKAY KKIHITKVEE RLTTICQREN SFYVDTVRAF RDRRYEFKGL HKVWKKKLSA AVEVGDAAEV KRCKNMEVL YDSLQLAHKC ILNSFYGYVM RKGARWYSME MAGIVCFTGA NIITQARELI EQIGRPLELD TDGIWCVLPN SFPENFVFKT TNVKKPKVT ISYPGAMLNI MVKEGFTNDQ YQELAEPSSL TYVTRSENSI FFEVDGPYLA MILPASKEEG KKLKKRYAVF N EDGSLAEL KGFEVKRRGE LQLIKIFQSS VFEAFLKGST LEEVYGSVAK VADYWLDVLY SKAANMPDSE LFELISENRS MS RKLEDYG EQKSTSISTA KRLAEFLGDQ MVKDAGLSCR YIISRKPEGS PVTERAIPLA IFQAEPTVRK HFLRKWLKSS SLQ DFDIRA ILDWDYYIER LGSAIQKIIT IPAALQQVKN PVPRVKHPDW LHKKLLEKND VYKQKKISEL FTLEGRRQVT MAEA UniProtKB: DNA polymerase epsilon catalytic subunit A |
-分子 #2: Proliferating cell nuclear antigen
| 分子 | 名称: Proliferating cell nuclear antigen / タイプ: protein_or_peptide / ID: 2 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 28.795752 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MFEARLVQGS ILKKVLEALK DLINEACWDI SSSGVNLQSM DSSHVSLVQL TLRSEGFDTY RCDRNLAMGV NLTSMSKILK CAGNEDIIT LRAEDNADTL ALVFEAPNQE KVSDYEMKLM DLDVEQLGIP EQEYSCVVKM PSGEFARICR DLSHIGDAVV I SCAKDGVK ...文字列: MFEARLVQGS ILKKVLEALK DLINEACWDI SSSGVNLQSM DSSHVSLVQL TLRSEGFDTY RCDRNLAMGV NLTSMSKILK CAGNEDIIT LRAEDNADTL ALVFEAPNQE KVSDYEMKLM DLDVEQLGIP EQEYSCVVKM PSGEFARICR DLSHIGDAVV I SCAKDGVK FSASGELGNG NIKLSQTSNV DKEEEAVTIE MNEPVQLTFA LRYLNFFTKA TPLSSTVTLS MSADVPLVVE YK IADMGHL KYYLAPKIED EEGS UniProtKB: Proliferating cell nuclear antigen |
-分子 #3: DNA nascent strand
| 分子 | 名称: DNA nascent strand / タイプ: dna / ID: 3 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 7.074585 KDa |
| 配列 | 文字列: (DC)(DC)(DT)(DT)(DC)(DC)(DA)(DC)(DT)(DT) (DC)(DC)(DC)(DA)(DA)(DC)(DC)(DC)(DT)(DC) (DA)(DC)(DC)(2DA) |
-分子 #4: DNA template strand
| 分子 | 名称: DNA template strand / タイプ: dna / ID: 4 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 12.033732 KDa |
| 配列 | 文字列: (DA)(DA)(DG)(DG)(DC)(DT)(DG)(DA)(DA)(DC) (DG)(DA)(DA)(DT)(DT)(DG)(DG)(DT)(DG)(DA) (DG)(DG)(DG)(DT)(DT)(DG)(DG)(DG)(DA) (DA)(DG)(DT)(DG)(DG)(DA)(DA)(DG)(DG) |
-分子 #5: IRON/SULFUR CLUSTER
| 分子 | 名称: IRON/SULFUR CLUSTER / タイプ: ligand / ID: 5 / コピー数: 1 / 式: SF4 |
|---|---|
| 分子量 | 理論値: 351.64 Da |
| Chemical component information | 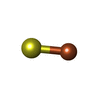 ChemComp-FS1: |
-分子 #6: 2',3'-dideoxyadenosine triphosphate
| 分子 | 名称: 2',3'-dideoxyadenosine triphosphate / タイプ: ligand / ID: 6 / コピー数: 1 / 式: DDS |
|---|---|
| 分子量 | 理論値: 475.182 Da |
| Chemical component information |  ChemComp-DDS: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 40.08 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)