+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structural basis of specific lysine transport by Pseudomonas aeruginosa permease LysP | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Complex / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 | Amino acid permease, conserved site / : / Amino acid permeases signature. / Amino acid permease/ SLC12A domain / Amino acid permease / amino acid transmembrane transport / amino acid transmembrane transporter activity / membrane / Lysine-specific permease 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Pseudomonas aeruginosa PAO1 (緑膿菌) / Pseudomonas aeruginosa PAO1 (緑膿菌) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.68 Å | |||||||||
 データ登録者 データ登録者 | Nji E / Matsuoka R | |||||||||
| 資金援助 |  英国, 1件 英国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2025 ジャーナル: Nat Commun / 年: 2025タイトル: Structural basis of specific lysine transport by Pseudomonas aeruginosa permease LysP. 著者: Deniz Bicer / Rei Matsuoka / Aurélien F A Moumbock / Preethi Sukumar / Albert Suades / Harish Cheruvara / Andrew Quigley / David Drew / Els Pardon / Jan Steyaert / Peter J F Henderson / ...著者: Deniz Bicer / Rei Matsuoka / Aurélien F A Moumbock / Preethi Sukumar / Albert Suades / Harish Cheruvara / Andrew Quigley / David Drew / Els Pardon / Jan Steyaert / Peter J F Henderson / Martin Caffrey / Julia J Griese / Emmanuel Nji /         要旨: Under conditions of extreme acidity, the lysine-specific permease, LysP, not only mediates the import of L-lysine it also interacts with the transcriptional regulator, CadC, to activate expression of ...Under conditions of extreme acidity, the lysine-specific permease, LysP, not only mediates the import of L-lysine it also interacts with the transcriptional regulator, CadC, to activate expression of the cadAB operon. This operon encodes the lysine decarboxylase, CadA, which converts lysine to cadaverine while consuming a cytoplasmic proton, and the antiporter, CadB, which exports protonated cadaverine in exchange for extracellular lysine. Together, these processes contribute to cytoplasmic pH homeostasis and support bacterial acid resistance - a mechanism essential for the survival of pathogenic bacteria in acidic host environments. Here, we present the cryo-EM structure of LysP from Pseudomonas aeruginosa in an inward-occluded conformation (3.2-5.3 Å resolution), bound to L-lysine and a nanobody. L-Lysine is coordinated by hydrophobic contacts, cation-π interactions, and by hydrogen bonding mostly with polar uncharged residues. Reconstitution of LysP into proteoliposomes confirms specific L-lysine transport, which is competitively inhibited by L-4-thialysine. These findings provide a structural framework for understanding selective lysine recognition and inhibition, with implications for antibacterial drug design. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_50053.map.gz emd_50053.map.gz | 15.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-50053-v30.xml emd-50053-v30.xml emd-50053.xml emd-50053.xml | 23 KB 23 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_50053.png emd_50053.png | 67.7 KB | ||
| マスクデータ |  emd_50053_msk_1.map emd_50053_msk_1.map | 30.5 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-50053.cif.gz emd-50053.cif.gz | 6.7 KB | ||
| その他 |  emd_50053_additional_1.map.gz emd_50053_additional_1.map.gz emd_50053_half_map_1.map.gz emd_50053_half_map_1.map.gz emd_50053_half_map_2.map.gz emd_50053_half_map_2.map.gz | 28.7 MB 28.4 MB 28.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-50053 http://ftp.pdbj.org/pub/emdb/structures/EMD-50053 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-50053 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-50053 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9eydMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_50053.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_50053.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.008 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_50053_msk_1.map emd_50053_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: sharpening map
| ファイル | emd_50053_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | sharpening map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_50053_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_50053_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : PaLysP-NbCA5755 complex
| 全体 | 名称: PaLysP-NbCA5755 complex |
|---|---|
| 要素 |
|
-超分子 #1: PaLysP-NbCA5755 complex
| 超分子 | 名称: PaLysP-NbCA5755 complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Pseudomonas aeruginosa PAO1 (緑膿菌) Pseudomonas aeruginosa PAO1 (緑膿菌) |
-分子 #1: Lysine-specific permease
| 分子 | 名称: Lysine-specific permease / タイプ: protein_or_peptide / ID: 1 / 詳細: K1001 is a substrate / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Pseudomonas aeruginosa PAO1 (緑膿菌) Pseudomonas aeruginosa PAO1 (緑膿菌) |
| 分子量 | 理論値: 51.816453 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: RRVLKPRHLN MIAIGGSIGT GLFVASGATV ATAGPGGALL SYALIGLMVY FLMTSLGEMA AYMPVSGSFC TYGSRFVEDG FGFALGWNY WYNWAVTIAA ELVAAQLVMS FWFPEVPGIY WSAIFLGIMF GLNVISARGF GESEFWFALI KVVTVVIFIG V GLATIFGI ...文字列: RRVLKPRHLN MIAIGGSIGT GLFVASGATV ATAGPGGALL SYALIGLMVY FLMTSLGEMA AYMPVSGSFC TYGSRFVEDG FGFALGWNY WYNWAVTIAA ELVAAQLVMS FWFPEVPGIY WSAIFLGIMF GLNVISARGF GESEFWFALI KVVTVVIFIG V GLATIFGI MHGVESPGFS NFTMGDAPFV GGFQAMVGVA MIAGFSFQGT ELIGIAAGES ENPRKNIPIA IRQVFWRILM FY ILAIFVI GMLIPYTDPN LLKNDASDIS VSPFTLLFER AGFAAAAGVM NAVILSAILS AGNSGMYAST RMLYNLALEG KAP RLFSRV SRSGVPRNAL YATTLVGALC FLTSAFGDST VYTWLLNTSG MCGFIAWLGI AISHYRFRKG YLAQGGRLED LPYR AKLFP FGPLFAFALC MVITLGQNYQ ALVGERIDWI GLLATYISLP LFLAIWLGYR WKKRARFVRY HEMDVSPTNT UniProtKB: Lysine-specific permease |
-分子 #2: Nanobody CA5755
| 分子 | 名称: Nanobody CA5755 / タイプ: protein_or_peptide / ID: 2 / 詳細: Nanobody CA5755 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 14.443981 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: QVQLQESGGG LVQGGSLRLS CAASGRTFSI YGMAWVRQAS GKEREFVAAM PRGGGTTNYA DSVKGRFSIS RDNAKNTVDL QMNSLKPED TAVYYCVADR GFTLRLGIQH DYWGQGTQVT VSSHHHHHHE PEA |
-分子 #3: LYSINE
| 分子 | 名称: LYSINE / タイプ: ligand / ID: 3 / コピー数: 1 / 式: LYS |
|---|---|
| 分子量 | 理論値: 147.195 Da |
| Chemical component information | 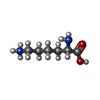 ChemComp-LYS: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 検出モード: COUNTING / 平均電子線量: 80.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)




















































