+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Tetrahymena Ribozyme scaffolded Fluoride riboswitch | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Ribozyme / xrRNA / Scaffold / RNA | |||||||||
| 生物種 |  Tetrahymena (真核生物) / Tetrahymena (真核生物) /   Thermotoga petrophila (バクテリア) Thermotoga petrophila (バクテリア) | |||||||||
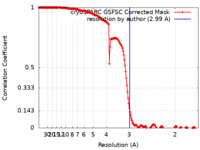
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.99 Å | |||||||||
 データ登録者 データ登録者 | Langeberg CJ / Kieft JS | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2023 ジャーナル: Nucleic Acids Res / 年: 2023タイトル: A generalizable scaffold-based approach for structure determination of RNAs by cryo-EM. 著者: Conner J Langeberg / Jeffrey S Kieft /  要旨: Single-particle cryo-electron microscopy (cryo-EM) can reveal the structures of large and often dynamic molecules, but smaller biomolecules (≤50 kDa) remain challenging targets due to their ...Single-particle cryo-electron microscopy (cryo-EM) can reveal the structures of large and often dynamic molecules, but smaller biomolecules (≤50 kDa) remain challenging targets due to their intrinsic low signal to noise ratio. Methods to help resolve small proteins have been applied but development of similar approaches to aid in structural determination of small, structured RNA elements have lagged. Here, we present a scaffold-based approach that we used to recover maps of sub-25 kDa RNA domains to 4.5-5.0 Å. While lacking the detail of true high-resolution maps, these maps are suitable for model building and preliminary structure determination. We demonstrate this method helped faithfully recover the structure of several RNA elements of known structure, and that it promises to be generalized to other RNAs without disturbing their native fold. This approach may streamline the sample preparation process and reduce the optimization required for data collection. This first-generation scaffold approach provides a robust system to aid in RNA structure determination by cryo-EM and lays the groundwork for further scaffold optimization to achieve higher resolution. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_41312.map.gz emd_41312.map.gz | 256.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-41312-v30.xml emd-41312-v30.xml emd-41312.xml emd-41312.xml | 14.8 KB 14.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_41312_fsc.xml emd_41312_fsc.xml | 16.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_41312.png emd_41312.png | 55.4 KB | ||
| Filedesc metadata |  emd-41312.cif.gz emd-41312.cif.gz | 5.2 KB | ||
| その他 |  emd_41312_half_map_1.map.gz emd_41312_half_map_1.map.gz emd_41312_half_map_2.map.gz emd_41312_half_map_2.map.gz | 474.5 MB 474.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-41312 http://ftp.pdbj.org/pub/emdb/structures/EMD-41312 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41312 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41312 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_41312_validation.pdf.gz emd_41312_validation.pdf.gz | 772.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_41312_full_validation.pdf.gz emd_41312_full_validation.pdf.gz | 771.8 KB | 表示 | |
| XML形式データ |  emd_41312_validation.xml.gz emd_41312_validation.xml.gz | 26.1 KB | 表示 | |
| CIF形式データ |  emd_41312_validation.cif.gz emd_41312_validation.cif.gz | 34.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41312 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41312 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41312 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41312 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_41312.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_41312.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.8464 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_41312_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_41312_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Tetrahymena Ribozyme scaffolded Fluoride riboswitch
| 全体 | 名称: Tetrahymena Ribozyme scaffolded Fluoride riboswitch |
|---|---|
| 要素 |
|
-超分子 #1: Tetrahymena Ribozyme scaffolded Fluoride riboswitch
| 超分子 | 名称: Tetrahymena Ribozyme scaffolded Fluoride riboswitch / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Tetrahymena (真核生物) Tetrahymena (真核生物) |
-分子 #1: RNA (417-MER)
| 分子 | 名称: RNA (417-MER) / タイプ: rna / ID: 1 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:   Thermotoga petrophila (バクテリア) Thermotoga petrophila (バクテリア) |
| 分子量 | 理論値: 134.830641 KDa |
| 配列 | 文字列: GGGCGAUGAG GCCCGCCCAA ACUGCCCUAU AUGGAUGCAG UUCACAGACU AAAUGUCGGU CGGGGAAGAU GUAUUCUUCU CAUAAGAUA UAGUCGGACC UCUCCUUAAU GGGAGCUAGC GGAUGAAGUG AUGCAACACU GGAGCCGCUG GGAACUAAUU U GUAUGCGA ...文字列: GGGCGAUGAG GCCCGCCCAA ACUGCCCUAU AUGGAUGCAG UUCACAGACU AAAUGUCGGU CGGGGAAGAU GUAUUCUUCU CAUAAGAUA UAGUCGGACC UCUCCUUAAU GGGAGCUAGC GGAUGAAGUG AUGCAACACU GGAGCCGCUG GGAACUAAUU U GUAUGCGA AAGUAUAUUG AUUAGUUUUG GAGGAGGGAA AAGUUAUCAG GCAUGCACCU GGUAGCUAGU CUUUAAACCA AU AGAUUGC AUCGGUUUAA AAGGCAAGAC CGUCAAAUUG CGGGAAAGGG GUCAACAGCC GUUCAGUACC AAGUCUCAGG GGA AACUUU GAGAUGGCCU UGCAAAGGGU AUGGUAAUAA GCUGACGGAC AUGGUCCUAA CCACGCAGCC AAGUCCUAAG UAGG GCUGA UGGCCUCUAC UG |
-分子 #2: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 2 / コピー数: 30 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #3: FLUORIDE ION
| 分子 | 名称: FLUORIDE ION / タイプ: ligand / ID: 3 / コピー数: 1 / 式: F |
|---|---|
| 分子量 | 理論値: 18.998 Da |
| Chemical component information |  ChemComp-F: |
-分子 #4: POTASSIUM ION
| 分子 | 名称: POTASSIUM ION / タイプ: ligand / ID: 4 / コピー数: 1 / 式: K |
|---|---|
| 分子量 | 理論値: 39.098 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 構成要素:
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / メッシュ: 50 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 6 sec. / 前処理 - 雰囲気: OTHER | |||||||||
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)