+ Open data
Open data
- Basic information
Basic information
| Entry |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | CryoEM structure of ZIKV rsNS1 | |||||||||
 Map data Map data | ||||||||||
 Sample Sample |
| |||||||||
 Keywords Keywords | Flavivirus / ZIKA / NS1 / VIRAL PROTEIN | |||||||||
| Function / homology |  Function and homology information Function and homology informationsymbiont-mediated suppression of host interferon-mediated signaling pathway / flavivirin / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of host TYK2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT1 activity / viral capsid / nucleoside-triphosphate phosphatase / double-stranded RNA binding / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of TBK1 activity / clathrin-dependent endocytosis of virus by host cell ...symbiont-mediated suppression of host interferon-mediated signaling pathway / flavivirin / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of host TYK2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT2 activity / symbiont-mediated suppression of host JAK-STAT cascade via inhibition of STAT1 activity / viral capsid / nucleoside-triphosphate phosphatase / double-stranded RNA binding / symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of TBK1 activity / clathrin-dependent endocytosis of virus by host cell / symbiont-mediated suppression of host toll-like receptor signaling pathway / mRNA (guanine-N7)-methyltransferase / methyltransferase cap1 / host cell cytoplasm / protein-macromolecule adaptor activity / methyltransferase cap1 activity / mRNA 5'-cap (guanine-N7-)-methyltransferase activity / RNA helicase activity / protein dimerization activity / host cell perinuclear region of cytoplasm / host cell endoplasmic reticulum membrane / RNA helicase / symbiont-mediated suppression of host type I interferon-mediated signaling pathway / serine-type endopeptidase activity / symbiont-mediated activation of host autophagy / RNA-directed RNA polymerase / viral RNA genome replication / RNA-directed RNA polymerase activity / fusion of virus membrane with host endosome membrane / viral envelope / lipid binding / virion attachment to host cell / GTP binding / host cell nucleus / virion membrane / structural molecule activity / ATP hydrolysis activity / proteolysis / extracellular region / ATP binding / metal ion binding Similarity search - Function | |||||||||
| Biological species |   Zika virus Zika virus | |||||||||
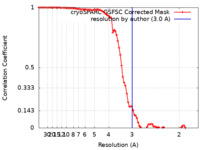
| Method | single particle reconstruction / cryo EM / Resolution: 3.0 Å | |||||||||
 Authors Authors | Chew BLA / Luo D | |||||||||
| Funding support |  Singapore, 1 items Singapore, 1 items
| |||||||||
 Citation Citation |  Journal: Npj Viruses / Year: 2024 Journal: Npj Viruses / Year: 2024Title: Structural basis of Zika virus NS1 multimerization and human antibody recognition. Authors: Bing Liang Alvin Chew / An Qi Ngoh / Wint Wint Phoo / Mei Jie Grace Weng / Ho Jun Sheng / Kitti Wing Ki Chan / Eddie Yong Jun Tan / Terri Gelbart / Chenrui Xu / Gene S Tan / Subhash G Vasudevan / Dahai Luo /    Abstract: Zika virus (ZIKV) belongs to the Flavivirus genus of the Flaviviridae family along with the four serotypes of dengue virus (DENV1-4). The recent global outbreaks of contemporary ZIKV strains ...Zika virus (ZIKV) belongs to the Flavivirus genus of the Flaviviridae family along with the four serotypes of dengue virus (DENV1-4). The recent global outbreaks of contemporary ZIKV strains demonstrated that infection can lead to neurological sequelae in adults and severe abnormalities in newborns that were previously unreported with ancestral strains. As such, there remains an unmet need for efficacious vaccines and antiviral agents against ZIKV. The non-structural protein 1 (NS1) is secreted from the infected cell and is thought to be associated with disease severity besides its proven usefulness for differential diagnoses. However, its physiologically relevant structure and pathogenesis mechanisms remain unclear. Here, we present high-resolution cryoEM structures of ZIKV recombinant secreted NS1 (rsNS1) and its complexes with three human monoclonal antibodies (AA12, EB9, GB5), as well as evidence for ZIKV infection-derived secreted NS1 (isNS1) binding to High Density Lipoprotein (HDL). We show that ZIKV rsNS1 forms tetramers and filamentous repeats of tetramers. We also observed that antibody binding did not disrupt the ZIKV NS1 tetramers as they bound to the wing and connector subdomain of the β-ladder. Our study reveals new insights into NS1 multimerization, highlights the need to distinguish the polymorphic nature of rsNS1 and isNS1, and expands the mechanistic basis of the protection conferred by antibodies targeting NS1. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Supplemental images |
|---|
- Downloads & links
Downloads & links
-EMDB archive
| Map data |  emd_37663.map.gz emd_37663.map.gz | 33 MB |  EMDB map data format EMDB map data format | |
|---|---|---|---|---|
| Header (meta data) |  emd-37663-v30.xml emd-37663-v30.xml emd-37663.xml emd-37663.xml | 16.1 KB 16.1 KB | Display Display |  EMDB header EMDB header |
| FSC (resolution estimation) |  emd_37663_fsc.xml emd_37663_fsc.xml | 8.4 KB | Display |  FSC data file FSC data file |
| Images |  emd_37663.png emd_37663.png | 104.4 KB | ||
| Filedesc metadata |  emd-37663.cif.gz emd-37663.cif.gz | 5.8 KB | ||
| Others |  emd_37663_half_map_1.map.gz emd_37663_half_map_1.map.gz emd_37663_half_map_2.map.gz emd_37663_half_map_2.map.gz | 59.5 MB 59.5 MB | ||
| Archive directory |  http://ftp.pdbj.org/pub/emdb/structures/EMD-37663 http://ftp.pdbj.org/pub/emdb/structures/EMD-37663 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-37663 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-37663 | HTTPS FTP |
-Related structure data
| Related structure data |  8wn8MC  8wnpC  8wnuC  8wo0C  8wo4C M: atomic model generated by this map C: citing same article ( |
|---|---|
| Similar structure data | Similarity search - Function & homology  F&H Search F&H Search |
- Links
Links
| EMDB pages |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| Related items in Molecule of the Month |
- Map
Map
| File |  Download / File: emd_37663.map.gz / Format: CCP4 / Size: 64 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) Download / File: emd_37663.map.gz / Format: CCP4 / Size: 64 MB / Type: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & slices | Image control
Images are generated by Spider. | ||||||||||||||||||||||||||||||||||||
| Voxel size | X=Y=Z: 0.86 Å | ||||||||||||||||||||||||||||||||||||
| Density |
| ||||||||||||||||||||||||||||||||||||
| Symmetry | Space group: 1 | ||||||||||||||||||||||||||||||||||||
| Details | EMDB XML:
|
-Supplemental data
-Half map: #2
| File | emd_37663_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & Slices |
| ||||||||||||
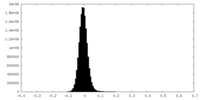
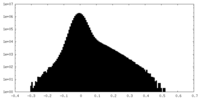
| Density Histograms |
-Half map: #1
| File | emd_37663_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Projections & Slices |
| ||||||||||||
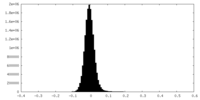
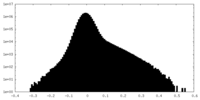
| Density Histograms |
- Sample components
Sample components
-Entire : Zika virus
| Entire | Name:   Zika virus Zika virus |
|---|---|
| Components |
|
-Supramolecule #1: Zika virus
| Supramolecule | Name: Zika virus / type: virus / ID: 1 / Parent: 0 / Macromolecule list: #1 / Details: NS1 / NCBI-ID: 64320 / Sci species name: Zika virus / Sci species strain: MR766 / Virus type: VIRION / Virus isolate: STRAIN / Virus enveloped: Yes / Virus empty: No |
|---|---|
| Host (natural) | Organism:  Homo sapiens (human) Homo sapiens (human) |
-Macromolecule #1: Non-structural protein 1
| Macromolecule | Name: Non-structural protein 1 / type: protein_or_peptide / ID: 1 / Number of copies: 4 / Enantiomer: LEVO |
|---|---|
| Source (natural) | Organism:   Zika virus Zika virus |
| Molecular weight | Theoretical: 41.251578 KDa |
| Recombinant expression | Organism:  Homo sapiens (human) Homo sapiens (human) |
| Sequence | String: DVGCSVDFSK KETRCGTGVF IYNDVEAWRD RYKYHPDSPR RLAAAVKQAW EEGICGISSV SRMENIMWKS VEGELNAILE ENGVQLTVV VGSVKNPMWR GPQRLPVPVN ELPHGWKAWG KSYFVRAAKT NNSFVVDGDT LKECPLEHRA WNSFLVEDHG F GVFHTSVW ...String: DVGCSVDFSK KETRCGTGVF IYNDVEAWRD RYKYHPDSPR RLAAAVKQAW EEGICGISSV SRMENIMWKS VEGELNAILE ENGVQLTVV VGSVKNPMWR GPQRLPVPVN ELPHGWKAWG KSYFVRAAKT NNSFVVDGDT LKECPLEHRA WNSFLVEDHG F GVFHTSVW LKVREDYSLE CDPAVIGTAV KGREAAHSDL GYWIESEKND TWRLKRAHLI EMKTCEWPKS HTLWTDGVEE SD LIIPKSL AGPLSHHNTR EGYRTQVKGP WHSEELEIRF EECPGTKVYV EETCGTRGPS LRSTTASGRV IEEWCCRECT MPP LSFRAK DGCWYGMEIR PRKEPESNLV RSMVTAGTKH HHHHH UniProtKB: Genome polyprotein |
-Macromolecule #2: 2-acetamido-2-deoxy-beta-D-glucopyranose
| Macromolecule | Name: 2-acetamido-2-deoxy-beta-D-glucopyranose / type: ligand / ID: 2 / Number of copies: 2 / Formula: NAG |
|---|---|
| Molecular weight | Theoretical: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-Experimental details
-Structure determination
| Method | cryo EM |
|---|---|
 Processing Processing | single particle reconstruction |
| Aggregation state | particle |
- Sample preparation
Sample preparation
| Buffer | pH: 8 |
|---|---|
| Vitrification | Cryogen name: ETHANE |
- Electron microscopy
Electron microscopy
| Microscope | FEI TITAN KRIOS |
|---|---|
| Image recording | Film or detector model: GATAN K2 SUMMIT (4k x 4k) / Average electron dose: 48.0 e/Å2 |
| Electron beam | Acceleration voltage: 300 kV / Electron source:  FIELD EMISSION GUN FIELD EMISSION GUN |
| Electron optics | Illumination mode: OTHER / Imaging mode: OTHER / Nominal defocus max: 2.0 µm / Nominal defocus min: 0.5 µm |
| Experimental equipment |  Model: Titan Krios / Image courtesy: FEI Company |
+ Image processing
Image processing
-Atomic model buiding 1
| Refinement | Protocol: RIGID BODY FIT |
|---|---|
| Output model |  PDB-8wn8: |
 Movie
Movie Controller
Controller











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)