+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Rpd3S histone deacetylase complex | |||||||||||||||||||||||||||
 マップデータ マップデータ | ||||||||||||||||||||||||||||
 試料 試料 |
| |||||||||||||||||||||||||||
 キーワード キーワード | Rpd3S / HDAC / Hho1 / cryptic transcription / TRANSCRIPTION | |||||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報TINTIN complex / Snt2C complex / negative regulation of silent mating-type cassette heterochromatin formation / negative regulation of antisense RNA transcription / Rpd3L complex / protein localization to nucleolar rDNA repeats / negative regulation of reciprocal meiotic recombination / negative regulation of rDNA heterochromatin formation / Rpd3L-Expanded complex / Rpd3S complex ...TINTIN complex / Snt2C complex / negative regulation of silent mating-type cassette heterochromatin formation / negative regulation of antisense RNA transcription / Rpd3L complex / protein localization to nucleolar rDNA repeats / negative regulation of reciprocal meiotic recombination / negative regulation of rDNA heterochromatin formation / Rpd3L-Expanded complex / Rpd3S complex / rDNA chromatin condensation / histone H3K36me3 reader activity / nucleophagy / regulation of RNA stability / HDACs deacetylate histones / histone deacetylase activity, hydrolytic mechanism / DNA replication-dependent chromatin assembly / histone deacetylase / nucleosome disassembly / histone deacetylase activity / cellular response to nitrogen starvation / SUMOylation of chromatin organization proteins / negative regulation of transcription by RNA polymerase I / regulation of DNA-templated DNA replication initiation / Sin3-type complex / histone deacetylase complex / NuA4 histone acetyltransferase complex / Estrogen-dependent gene expression / positive regulation of macroautophagy / histone acetyltransferase complex / histone reader activity / nuclear periphery / meiotic cell cycle / transcription elongation by RNA polymerase II / positive regulation of transcription elongation by RNA polymerase II / G1/S transition of mitotic cell cycle / double-strand break repair via nonhomologous end joining / G2/M transition of mitotic cell cycle / transcription corepressor activity / heterochromatin formation / nucleosome assembly / cellular response to heat / response to oxidative stress / transcription coactivator activity / cell division / DNA repair / negative regulation of DNA-templated transcription / regulation of DNA-templated transcription / regulation of transcription by RNA polymerase II / DNA-templated transcription / chromatin / negative regulation of transcription by RNA polymerase II / positive regulation of transcription by RNA polymerase II / zinc ion binding / identical protein binding / nucleus / cytoplasm 類似検索 - 分子機能 | |||||||||||||||||||||||||||
| 生物種 |  | |||||||||||||||||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.46 Å | |||||||||||||||||||||||||||
 データ登録者 データ登録者 | Dong S / Li H / Wang M / Rasheed N / Zou B / Gao X / Guan J / Li W / Zhang J / Wang C ...Dong S / Li H / Wang M / Rasheed N / Zou B / Gao X / Guan J / Li W / Zhang J / Wang C / Zhou N / Shi X / Li M / Zhou M / Huang J / Zhang Y / Wong KH / Zhang X / Chao WCH / Jun H | |||||||||||||||||||||||||||
| 資金援助 |  中国, 8件 中国, 8件
| |||||||||||||||||||||||||||
 引用 引用 |  ジャーナル: Cell Res / 年: 2023 ジャーナル: Cell Res / 年: 2023タイトル: Structural basis of nucleosome deacetylation and DNA linker tightening by Rpd3S histone deacetylase complex. 著者: Shuqi Dong / Huadong Li / Meilin Wang / Nadia Rasheed / Binqian Zou / Xijie Gao / Jiali Guan / Weijie Li / Jiale Zhang / Chi Wang / Ningkun Zhou / Xue Shi / Mei Li / Min Zhou / Junfeng Huang ...著者: Shuqi Dong / Huadong Li / Meilin Wang / Nadia Rasheed / Binqian Zou / Xijie Gao / Jiali Guan / Weijie Li / Jiale Zhang / Chi Wang / Ningkun Zhou / Xue Shi / Mei Li / Min Zhou / Junfeng Huang / He Li / Ying Zhang / Koon Ho Wong / Xiaofei Zhang / William Chong Hang Chao / Jun He /  要旨: In Saccharomyces cerevisiae, cryptic transcription at the coding region is prevented by the activity of Sin3 histone deacetylase (HDAC) complex Rpd3S, which is carried by the transcribing RNA ...In Saccharomyces cerevisiae, cryptic transcription at the coding region is prevented by the activity of Sin3 histone deacetylase (HDAC) complex Rpd3S, which is carried by the transcribing RNA polymerase II (RNAPII) to deacetylate and stabilize chromatin. Despite its fundamental importance, the mechanisms by which Rpd3S deacetylates nucleosomes and regulates chromatin dynamics remain elusive. Here, we determined several cryo-EM structures of Rpd3S in complex with nucleosome core particles (NCPs), including the H3/H4 deacetylation states, the alternative deacetylation state, the linker tightening state, and a state in which Rpd3S co-exists with the Hho1 linker histone on NCP. These structures suggest that Rpd3S utilizes a conserved Sin3 basic surface to navigate through the nucleosomal DNA, guided by its interactions with H3K36 methylation and the extra-nucleosomal DNA linkers, to target acetylated H3K9 and sample other histone tails. Furthermore, our structures illustrate that Rpd3S reconfigures the DNA linkers and acts in concert with Hho1 to engage the NCP, potentially unraveling how Rpd3S and Hho1 work in tandem for gene silencing. | |||||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_37096.map.gz emd_37096.map.gz | 68 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-37096-v30.xml emd-37096-v30.xml emd-37096.xml emd-37096.xml | 25.2 KB 25.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_37096.png emd_37096.png | 28.5 KB | ||
| マスクデータ |  emd_37096_msk_1.map emd_37096_msk_1.map | 137.1 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-37096.cif.gz emd-37096.cif.gz | 8.4 KB | ||
| その他 |  emd_37096_half_map_1.map.gz emd_37096_half_map_1.map.gz emd_37096_half_map_2.map.gz emd_37096_half_map_2.map.gz | 127.4 MB 127.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-37096 http://ftp.pdbj.org/pub/emdb/structures/EMD-37096 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-37096 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-37096 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8kc7MC  8kd2C  8kd3C  8kd4C  8kd5C  8kd6C  8kd7C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_37096.map.gz / 形式: CCP4 / 大きさ: 137.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_37096.map.gz / 形式: CCP4 / 大きさ: 137.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.88 Å | ||||||||||||||||||||||||||||||||||||
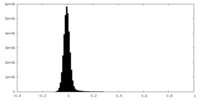
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_37096_msk_1.map emd_37096_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
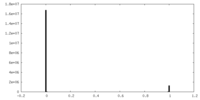
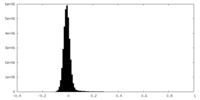
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_37096_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
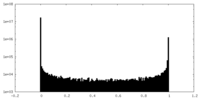
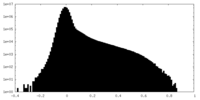
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_37096_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
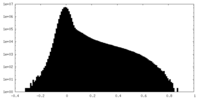
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Histone deacetylase complex Rpd3S in its apo form
| 全体 | 名称: Histone deacetylase complex Rpd3S in its apo form |
|---|---|
| 要素 |
|
-超分子 #1: Histone deacetylase complex Rpd3S in its apo form
| 超分子 | 名称: Histone deacetylase complex Rpd3S in its apo form / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 527.7 KDa |
-分子 #1: Histone deacetylase RPD3
| 分子 | 名称: Histone deacetylase RPD3 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: histone deacetylase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 48.961957 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MVYEATPFDP ITVKPSDKRR VAYFYDADVG NYAYGAGHPM KPHRIRMAHS LIMNYGLYKK MEIYRAKPAT KQEMCQFHTD EYIDFLSRV TPDNLEMFKR ESVKFNVGDD CPVFDGLYEY CSISGGGSME GAARLNRGKC DVAVNYAGGL HHAKKSEASG F CYLNDIVL ...文字列: MVYEATPFDP ITVKPSDKRR VAYFYDADVG NYAYGAGHPM KPHRIRMAHS LIMNYGLYKK MEIYRAKPAT KQEMCQFHTD EYIDFLSRV TPDNLEMFKR ESVKFNVGDD CPVFDGLYEY CSISGGGSME GAARLNRGKC DVAVNYAGGL HHAKKSEASG F CYLNDIVL GIIELLRYHP RVLYIDIDVH HGDGVEEAFY TTDRVMTCSF HKYGEFFPGT GELRDIGVGA GKNYAVNVPL RD GIDDATY RSVFEPVIKK IMEWYQPSAV VLQCGGDSLS GDRLGCFNLS MEGHANCVNY VKSFGIPMMV VGGGGYTMRN VAR TWCFET GLLNNVVLDK DLPYNEYYEY YGPDYKLSVR PSNMFNVNTP EYLDKVMTNI FANLENTKYA PSVQLNHTPR DAED LGDVE EDSAEAKDTK GGSQYARDLH VEHDNEFY UniProtKB: Histone deacetylase RPD3 |
-分子 #2: Transcriptional regulatory protein SIN3
| 分子 | 名称: Transcriptional regulatory protein SIN3 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 157.586844 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MHHHHHHHHP QLAMWSHPQF EKGGGSGGGS GGGSWSHPQF EKENLYFQSD YRPLNVKDAL SYLEQVKFQF SSRPDIYNLF LDIMKDFKS QAIDTPGVIE RVSTLFRGYP ILIQGFNTFL PQGYRIECSS NPDDPIRVTT PMGTTTVNNN ISPSGRGTTD A QELGSFPE ...文字列: MHHHHHHHHP QLAMWSHPQF EKGGGSGGGS GGGSWSHPQF EKENLYFQSD YRPLNVKDAL SYLEQVKFQF SSRPDIYNLF LDIMKDFKS QAIDTPGVIE RVSTLFRGYP ILIQGFNTFL PQGYRIECSS NPDDPIRVTT PMGTTTVNNN ISPSGRGTTD A QELGSFPE SDGNGVQQPS NVPMVPSSVY QSEQNQDQQQ SLPLLATSSG LPSIQQPEMP AHRQIPQSQS LVPQEDAKKN VD VEFSQAI SYVNKIKTRF ADQPDIYKHF LEILQTYQRE QKPINEVYAQ VTHLFQNAPD LLEDFKKFLP DSSASANQQV QHA QQHAQQ QHEAQMHAQA QAQAQAQAQV EQQKQQQQFL YPASGYYGHP SNRGIPQQNL PPIGSFSPPT NGSTVHEAYQ DQQH MQPPH FMPLPSIVQH GPNMVHQGIA NENPPLSDLR TSLTEQYAPS SIQHQQQHPQ SISPIANTQY GDIPVRPEID LDPSI VPVV PEPTEPIENN ISLNEEVTFF EKAKRYIGNK HLYTEFLKIL NLYSQDILDL DDLVEKVDFY LGSNKELFTW FKNFVG YQE KTKCIENIVH EKHRLDLDLC EAFGPSYKRL PKSDTFMPCS GRDDMCWEVL NDEWVGHPVW ASEDSGFIAH RKNQYEE TL FKIEEERHEY DFYIESNLRT IQCLETIVNK IENMTENEKA NFKLPPGLGH TSMTIYKKVI RKVYDKERGF EIIDALHE H PAVTAPVVLK RLKQKDEEWR RAQREWNKVW RELEQKVFFK SLDHLGLTFK QADKKLLTTK QLISEISSIK VDQTNKKIH WLTPKPKSQL DFDFPDKNIF YDILCLADTF ITHTTAYSNP DKERLKDLLK YFISLFFSIS FEKIEESLYS HKQNVSESSG SDDGSSIAS RKRPYQQEMS LLDILHRSRY QKLKRSNDED GKVPQLSEPP EEEPNTIEEE ELIDEEAKNP WLTGNLVEEA N SQGIIQNR SIFNLFANTN IYIFFRHWTT IYERLLEIKQ MNERVTKEIN TRSTVTFAKD LDLLSSQLSE MGLDFVGEDA YK QVLRLSR RLINGDLEHQ WFEESLRQAY NNKAFKLYTI DKVTQSLVKH AHTLMTDAKT AEIMALFVKD RNASTTSAKD QII YRLQVR SHMSNTENMF RIEFDKRTLH VSIQYIALDD LTLKEPKADE DKWKYYVTSY ALPHPTEGIP HEKLKIPFLE RLIE FGQDI DGTEVDEEFS PEGISVSTLK IKIQPITYQL HIENGSYDVF TRKATNKYPT IANDNTQKGM VSQKKELISK FLDCA VGLR NNLDEAQKLS MQKKWENLKD SIAKTSAGNQ GIESETEKGK ITKQEQSDNL DSSTASVLPA SITTVPQDDN IETTGN TES SDKGAKIQ UniProtKB: Transcriptional regulatory protein SIN3 |
-分子 #3: Chromatin modification-related protein EAF3
| 分子 | 名称: Chromatin modification-related protein EAF3 / タイプ: protein_or_peptide / ID: 3 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 45.266406 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MVDLEQEFAL GGRCLAFHGP LMYEAKILKI WDPSSKMYTS IPNDKPGGSS QATKEIKPQK LGEDESIPEE IINGKCFFIH YQGWKSSWD EWVGYDRIRA YNEENIAMKK RLANEAKEAK KSLLEQQKKK KLSTSLGGPS NGGKRKGDSR SNASISKSTS Q SFLTSSVS ...文字列: MVDLEQEFAL GGRCLAFHGP LMYEAKILKI WDPSSKMYTS IPNDKPGGSS QATKEIKPQK LGEDESIPEE IINGKCFFIH YQGWKSSWD EWVGYDRIRA YNEENIAMKK RLANEAKEAK KSLLEQQKKK KLSTSLGGPS NGGKRKGDSR SNASISKSTS Q SFLTSSVS GRKSGRSSAN SLHPGSSLRS SSDQNGNDDR RRSSSLSPNM LHHIAGYPTP KISLQIPIKL KSVLVDDWEY VT KDKKICR LPADVTVEMV LNKYEHEVSQ ELESPGSQSQ LSEYCAGLKL YFDKCLGNML LYRLERLQYD ELLKKSSKDQ KPL VPIRIY GAIHLLRLIS VLPELISSTT MDLQSCQLLI KQTEDFLVWL LMHVDEYFND KDPNRSDDAL YVNTSSQYEG VALG M UniProtKB: Chromatin modification-related protein EAF3 |
-分子 #4: Transcriptional regulatory protein RCO1
| 分子 | 名称: Transcriptional regulatory protein RCO1 / タイプ: protein_or_peptide / ID: 4 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 84.469328 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MDTSKKDTTR SPSHSNSSSP SSSSLSSSSS KEKKRPKRLS SQNVNYDLKR RKIITSEGIE RSFKNEHSNL AVEDNIPEEE PKELLEKDS KGNIIKLNEP STISEDSKVS VTGLPLNKGP SEKIKRESLW NYRKNLGGQS NNSEMTLVPS KRFTQVPKNF Q DLNRNDLK ...文字列: MDTSKKDTTR SPSHSNSSSP SSSSLSSSSS KEKKRPKRLS SQNVNYDLKR RKIITSEGIE RSFKNEHSNL AVEDNIPEEE PKELLEKDS KGNIIKLNEP STISEDSKVS VTGLPLNKGP SEKIKRESLW NYRKNLGGQS NNSEMTLVPS KRFTQVPKNF Q DLNRNDLK TFLTENMTEE SNIRSTIGWN GDIINRTRDR EPESDRDNKK LSNIRTKIIL STNATYDSKS KLFGQNSIKS TS NASEKIF RDKNNSTIDF ENEDFCSACN QSGSFLCCDT CPKSFHFLCL DPPIDPNNLP KGDWHCNECK FKIFINNSMA TLK KIESNF IKQNNNVKIF AKLLFNIDSH NPKQFQLPNY IKETFPAVKT GSRGQYSDEN DKIPLTDRQL FNTSYGQSIT KLDS YNPDT HIDSNSGKFL ICYKCNQTRL GSWSHPENSR LIMTCDYCQT PWHLDCVPRA SFKNLGSKWK CPLHSPTKVY KKIHH CQED NSVNYKVWKK QRLINKKNQL YYEPLQKIGY QNNGNIQIIP TTSHTDYDFN QDFKITQIDE NSIKYDFFDK IYKSKM VQK RKLFQFQESL IDKLVSNGSQ NGNSEDNMVK DIASLIYFQV SNNDKSSNNK SASKSNNLRK LWDLKELTNV VVPNELD SI QFNDFSSDEI KHLLYLKKII ESKPKEELLK FLNIENPENQ SEMHHHHHHH HPQLAMWSHP QFEKGGGSGG GSGGGSWS H PQFEKENLYF QS UniProtKB: Transcriptional regulatory protein RCO1 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | 3D array |
- 試料調製
試料調製
| 濃度 | 0.7 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー













 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)