[日本語] English
 万見
万見- EMDB-36854: Cryo-EM structure of 30S ribosome with cleaved AP-mRNA bound complex I -
+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of 30S ribosome with cleaved AP-mRNA bound complex I | ||||||||||||
 マップデータ マップデータ | |||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | Ribosome / AP-mRNA | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報ornithine decarboxylase inhibitor activity / transcription antitermination factor activity, RNA binding / misfolded RNA binding / Group I intron splicing / RNA folding / four-way junction DNA binding / negative regulation of translational initiation / regulation of mRNA stability / mRNA regulatory element binding translation repressor activity / positive regulation of RNA splicing ...ornithine decarboxylase inhibitor activity / transcription antitermination factor activity, RNA binding / misfolded RNA binding / Group I intron splicing / RNA folding / four-way junction DNA binding / negative regulation of translational initiation / regulation of mRNA stability / mRNA regulatory element binding translation repressor activity / positive regulation of RNA splicing / transcription elongation factor complex / regulation of DNA-templated transcription elongation / DNA endonuclease activity / transcription antitermination / DNA-templated transcription termination / maintenance of translational fidelity / mRNA 5'-UTR binding / regulation of translation / ribosome biogenesis / ribosomal small subunit biogenesis / ribosomal small subunit assembly / small ribosomal subunit / cytosolic small ribosomal subunit / small ribosomal subunit rRNA binding / cytoplasmic translation / tRNA binding / negative regulation of translation / rRNA binding / ribosome / structural constituent of ribosome / translation / response to antibiotic / mRNA binding / RNA binding / zinc ion binding / membrane / cytosol / cytoplasm 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  | ||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.88 Å | ||||||||||||
 データ登録者 データ登録者 | Afsar M / Shukla A / Ramachandran R | ||||||||||||
| 資金援助 |  インド, 3件 インド, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2024 ジャーナル: Nucleic Acids Res / 年: 2024タイトル: Bacterial Rps3 counters oxidative and UV stress by recognizing and processing AP-sites on mRNA via a novel mechanism. 著者: Mohammad Afsar / Ankita Shukla / Faiz Ali / Rahul Kumar Maurya / Suman Bharti / Nelam Kumar / Mohammad Sadik / Surabhi Chandra / Huma Rahil / Sanjay Kumar / Imran Ansari / Farheen Jahan / ...著者: Mohammad Afsar / Ankita Shukla / Faiz Ali / Rahul Kumar Maurya / Suman Bharti / Nelam Kumar / Mohammad Sadik / Surabhi Chandra / Huma Rahil / Sanjay Kumar / Imran Ansari / Farheen Jahan / Saman Habib / Tanweer Hussain / Manju Yasoda Krishnan / Ravishankar Ramachandran /  要旨: Lesions and stable secondary structures in mRNA severely impact the translation efficiency, causing ribosome stalling and collisions. Prokaryotic ribosomal proteins Rps3, Rps4 and Rps5, located in ...Lesions and stable secondary structures in mRNA severely impact the translation efficiency, causing ribosome stalling and collisions. Prokaryotic ribosomal proteins Rps3, Rps4 and Rps5, located in the mRNA entry tunnel, form the mRNA helicase center and unwind stable mRNA secondary structures during translation. However, the mechanism underlying the detection of lesions on translating mRNA is unclear. We used Cryo-EM, biochemical assays, and knockdown experiments to investigate the apurinic/apyrimidinic (AP) endoribonuclease activity of bacterial ribosomes on AP-site containing mRNA. Our biochemical assays show that Rps3, specifically the 130RR131 motif, is important for recognizing and performing the AP-endoribonuclease activity. Furthermore, structural analysis revealed cleaved mRNA product in the 30S ribosome entry tunnel. Additionally, knockdown studies in Mycobacterium tuberculosis confirmed the protective role of Rps3 against oxidative and UV stress. Overall, our results show that prokaryotic Rps3 recognizes and processes AP-sites on mRNA via a novel mechanism that is distinct from eukaryotes. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_36854.map.gz emd_36854.map.gz | 59.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-36854-v30.xml emd-36854-v30.xml emd-36854.xml emd-36854.xml | 37.8 KB 37.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_36854.png emd_36854.png | 159.6 KB | ||
| マスクデータ |  emd_36854_msk_1.map emd_36854_msk_1.map | 64 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-36854.cif.gz emd-36854.cif.gz | 9.2 KB | ||
| その他 |  emd_36854_half_map_1.map.gz emd_36854_half_map_1.map.gz emd_36854_half_map_2.map.gz emd_36854_half_map_2.map.gz | 49.5 MB 49.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-36854 http://ftp.pdbj.org/pub/emdb/structures/EMD-36854 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-36854 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-36854 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8k3oMC  8k4eC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_36854.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_36854.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.38 Å | ||||||||||||||||||||||||||||||||||||
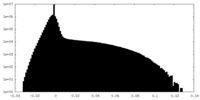
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_36854_msk_1.map emd_36854_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
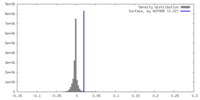
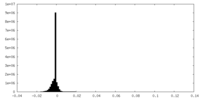
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_36854_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
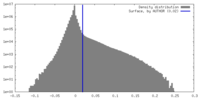
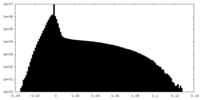
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_36854_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
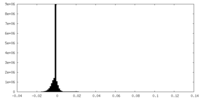
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : 30S ribosome with cleaved AP-mRNA
+超分子 #1: 30S ribosome with cleaved AP-mRNA
+分子 #1: 30S ribosomal protein S2
+分子 #2: 30S ribosomal protein S3
+分子 #3: 30S ribosomal protein S4
+分子 #4: 30S ribosomal protein S5
+分子 #5: 30S ribosomal protein S6, fully modified isoform
+分子 #6: 30S ribosomal protein S7
+分子 #7: 30S ribosomal protein S8
+分子 #8: 30S ribosomal protein S9
+分子 #9: 30S ribosomal protein S10
+分子 #10: 30S ribosomal protein S11
+分子 #11: 30S ribosomal protein S12
+分子 #12: 30S ribosomal protein S13
+分子 #13: 30S ribosomal protein S15
+分子 #14: 30S ribosomal protein S16
+分子 #15: 30S ribosomal protein S17
+分子 #16: 30S ribosomal protein S18
+分子 #17: 30S ribosomal protein S19
+分子 #18: 30S ribosomal protein S20
+分子 #20: 30S ribosomal protein S21
+分子 #22: 30S ribosomal protein S14
+分子 #19: Cleaved AP-mRNA
+分子 #21: 16S rRNA
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.2 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | モデル: Quantifoil R2/2 / 材質: COPPER / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: CONTINUOUS / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | 位相板: VOLTA PHASE PLATE |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: COUNTING / 平均電子線量: 1.42 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY PDBモデル - PDB ID: |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.88 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 77582 |
| 初期 角度割当 | タイプ: ANGULAR RECONSTITUTION |
| 最終 角度割当 | タイプ: ANGULAR RECONSTITUTION |
 ムービー
ムービー コントローラー
コントローラー











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)