+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of the intact photosynthetic light-harvesting antenna-reaction center complex from a green sulfur bacterium | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Green sulfur bacterium / Reaction center / FMO protein / Energy transfer / PHOTOSYNTHESIS | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報thylakoid / bacteriochlorophyll binding / iron-sulfur cluster binding / photosynthesis / electron transfer activity / heme binding / metal ion binding / membrane / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Chlorobaculum tepidum TLS (バクテリア) Chlorobaculum tepidum TLS (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.9 Å | |||||||||
 データ登録者 データ登録者 | Chen JH / Zhang X | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: J Integr Plant Biol / 年: 2023 ジャーナル: J Integr Plant Biol / 年: 2023タイトル: Cryo-electron microscopy structure of the intact photosynthetic light-harvesting antenna-reaction center complex from a green sulfur bacterium. 著者: Jing-Hua Chen / Weiwei Wang / Chen Wang / Tingyun Kuang / Jian-Ren Shen / Xing Zhang /   要旨: The photosynthetic reaction center complex (RCC) of green sulfur bacteria (GSB) consists of the membrane-imbedded RC core and the peripheric energy transmitting proteins called Fenna-Matthews-Olson ...The photosynthetic reaction center complex (RCC) of green sulfur bacteria (GSB) consists of the membrane-imbedded RC core and the peripheric energy transmitting proteins called Fenna-Matthews-Olson (FMO). Functionally, FMO transfers the absorbed energy from a huge peripheral light-harvesting antenna named chlorosome to the RC core where charge separation occurs. In vivo, one RC was found to bind two FMOs, however, the intact structure of RCC as well as the energy transfer mechanism within RCC remain to be clarified. Here we report a structure of intact RCC which contains a RC core and two FMO trimers from a thermophilic green sulfur bacterium Chlorobaculum tepidum at 2.9 Å resolution by cryo-electron microscopy. The second FMO trimer is attached at the cytoplasmic side asymmetrically relative to the first FMO trimer reported previously. We also observed two new subunits (PscE and PscF) and the N-terminal transmembrane domain of a cytochrome-containing subunit (PscC) in the structure. These two novel subunits possibly function to facilitate the binding of FMOs to RC core and to stabilize the whole complex. A new bacteriochlorophyll (numbered as 816) was identified at the interspace between PscF and PscA-1, causing an asymmetrical energy transfer from the two FMO trimers to RC core. Based on the structure, we propose an energy transfer network within this photosynthetic apparatus. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_34307.map.gz emd_34307.map.gz | 141.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-34307-v30.xml emd-34307-v30.xml emd-34307.xml emd-34307.xml | 37.2 KB 37.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_34307.png emd_34307.png | 112.9 KB | ||
| Filedesc metadata |  emd-34307.cif.gz emd-34307.cif.gz | 9.3 KB | ||
| その他 |  emd_34307_half_map_1.map.gz emd_34307_half_map_1.map.gz emd_34307_half_map_2.map.gz emd_34307_half_map_2.map.gz | 139.3 MB 139.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-34307 http://ftp.pdbj.org/pub/emdb/structures/EMD-34307 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-34307 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-34307 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8gwaMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_34307.map.gz / 形式: CCP4 / 大きさ: 149.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_34307.map.gz / 形式: CCP4 / 大きさ: 149.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.92 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_34307_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
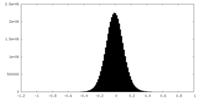
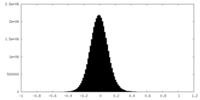
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_34307_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
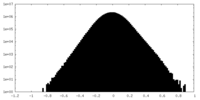
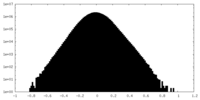
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : GsbRC-2FMO complex
+超分子 #1: GsbRC-2FMO complex
+分子 #1: Bacteriochlorophyll a protein
+分子 #2: P840 reaction center 17 kDa protein
+分子 #3: Photosystem P840 reaction center iron-sulfur protein
+分子 #4: Photosystem P840 reaction center, large subunit
+分子 #5: unkown protein
+分子 #6: Ric1 protein
+分子 #7: Cytochrome c
+分子 #8: BACTERIOCHLOROPHYLL A
+分子 #9: CARDIOLIPIN
+分子 #10: IRON/SULFUR CLUSTER
+分子 #11: Bacteriochlorophyll A isomer
+分子 #12: Chlorophyll A ester
+分子 #13: [(2R,3S,4S,5R,6R)-6-[(10E,12E,14E)-2,6,10,14,19,23-hexamethyl-25-...
+分子 #14: 1,2-DIPALMITOYL-PHOSPHATIDYL-GLYCEROLE
+分子 #15: 1,2-DISTEAROYL-MONOGALACTOSYL-DIGLYCERIDE
+分子 #16: CALCIUM ION
+分子 #17: 2-[(1E,3E,5E,7E,9E,11E,13E,15E,17E,19E)-3,7,12,16,20,24-hexamethy...
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 温度 | 最低: 80.0 K / 最高: 90.0 K |
| 特殊光学系 | 球面収差補正装置: 2.7mm / 色収差補正装置: 2.7mm / エネルギーフィルター - 名称: TFS Selectris / エネルギーフィルター - スリット幅: 10 eV |
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 撮影したグリッド数: 1 / 実像数: 2297 / 平均露光時間: 8.0 sec. / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 152200 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.5 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 130000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)