+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | The state 1 of Omicron Spike with bispecific antibody FD01 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Omicron / Spike / Bispecific antibody / Viral protein | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont-mediated disruption of host tissue / Maturation of spike protein / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / host extracellular region / symbiont-mediated-mediated suppression of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion / positive regulation of viral entry into host cell ...symbiont-mediated disruption of host tissue / Maturation of spike protein / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / host extracellular region / symbiont-mediated-mediated suppression of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion / positive regulation of viral entry into host cell / membrane fusion / host cell endoplasmic reticulum-Golgi intermediate compartment membrane / Attachment and Entry / entry receptor-mediated virion attachment to host cell / receptor-mediated virion attachment to host cell / host cell surface receptor binding / symbiont-mediated suppression of host innate immune response / endocytosis involved in viral entry into host cell / receptor ligand activity / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / symbiont entry into host cell / virion attachment to host cell / host cell plasma membrane / SARS-CoV-2 activates/modulates innate and adaptive immune responses / virion membrane / membrane / identical protein binding / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
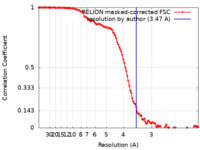
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.47 Å | |||||||||
 データ登録者 データ登録者 | Zhang X / Zhan WQ / Chen ZG / Sun L | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell Discov / 年: 2022 ジャーナル: Cell Discov / 年: 2022タイトル: Combating the SARS-CoV-2 Omicron (BA.1) and BA.2 with potent bispecific antibodies engineered from non-Omicron neutralizing antibodies. 著者: Yingdan Wang / Xiang Zhang / Yunping Ma / Yanqun Wang / Wuqiang Zhan / Qinwen Zheng / Meng Zhang / Ping Ji / Mei Liu / Qianying Liu / Tingting Sun / Tongyu Zhu / Yumei Wen / Lei Sun / Jincun ...著者: Yingdan Wang / Xiang Zhang / Yunping Ma / Yanqun Wang / Wuqiang Zhan / Qinwen Zheng / Meng Zhang / Ping Ji / Mei Liu / Qianying Liu / Tingting Sun / Tongyu Zhu / Yumei Wen / Lei Sun / Jincun Zhao / Fan Wu / Zhenguo Chen / Jinghe Huang /  要旨: The highly mutated and transmissible Omicron (BA.1) and its more contagious lineage BA.2 have provoked serious concerns over their decreased sensitivity to the current COVID-19 vaccines and evasion ...The highly mutated and transmissible Omicron (BA.1) and its more contagious lineage BA.2 have provoked serious concerns over their decreased sensitivity to the current COVID-19 vaccines and evasion from most anti-SARS-CoV-2 neutralizing antibodies (NAbs). In this study, we explored the possibility of combating the Omicron and BA.2 by constructing bispecific antibodies based on non-Omicron NAbs. We engineered 10 IgG-like bispecific antibodies with non-Omicron NAbs named GW01, 16L9, 4L12, and REGN10987 by fusing the single-chain variable fragments (scFvs) of two antibodies through a linker and then connecting them to the Fc region of IgG1. Surprisingly, 8 out of 10 bispecific antibodies showed high binding affinities to the Omicron receptor-binding domain (RBD) and exhibited extreme breadth and potency against pseudotyped SARS-CoV-2 variants of concern (VOCs) including Omicron and BA.2, with geometric mean of 50% inhibitory concentration (GM IC) values ranging from 4.5 ng/mL to 103.94 ng/mL, as well as the authentic BA.1.1. Six bispecific antibodies containing the cross-NAb GW01 not only neutralized Omicron and BA.2, but also neutralized the sarbecoviruses including SARS-CoV and SARS-related coronaviruses (SARSr-CoVs) RS3367 and WIV1, with GM IC ranging from 11.6 ng/mL to 103.9 ng/mL. Mapping analyses of 42 spike (S) variant single mutants of Omicron and BA.2 elucidated that these bispecific antibodies accommodated the S371L/F mutations, which were resistant to most of the non-Omicron NAbs. A cryo-electron microscopy (cryo-EM) structure study of the representative bispecific antibody GW01-16L9 (FD01) in its native full-length IgG form in complex with the Omicron S trimer revealed 5 distinct trimers and one novel trimer dimer conformation. 16L9 scFv binds the receptor-binding motif (RBM), while GW01 scFv binds a epitope outside the RBM. Two scFvs of the bispecific antibody synergistically induced the RBD-down conformation into 3 RBD-up conformation, improved the affinity between IgG and the Omicron RBD, induced the formation of trimer dimer, and inhibited RBD binding to ACE2. The trimer dimer conformation might induce the aggregation of virions and contribute to the neutralization ability of FD01. These novel bispecific antibodies are strong candidates for the treatment and prevention of infection with the Omicron, BA.2, VOCs, and other sarbecoviruses. Engineering bispecific antibodies based on non-Omicron NAbs could turn the majority of NAbs into a powerful arsenal to aid the battle against the pandemic. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_32655.map.gz emd_32655.map.gz | 86.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-32655-v30.xml emd-32655-v30.xml emd-32655.xml emd-32655.xml | 15.4 KB 15.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_32655_fsc.xml emd_32655_fsc.xml | 11.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_32655.png emd_32655.png | 73.7 KB | ||
| Filedesc metadata |  emd-32655.cif.gz emd-32655.cif.gz | 6.8 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-32655 http://ftp.pdbj.org/pub/emdb/structures/EMD-32655 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32655 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32655 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7woqMC  7wopC  7worC  7wosC  7wouC  7wovC  7wowC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_32655.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_32655.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.064 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Omicron Spike with 16L9 Fv
| 全体 | 名称: Omicron Spike with 16L9 Fv |
|---|---|
| 要素 |
|
-超分子 #1: Omicron Spike with 16L9 Fv
| 超分子 | 名称: Omicron Spike with 16L9 Fv / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|
-超分子 #2: Omicron Spike
| 超分子 | 名称: Omicron Spike / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
-超分子 #3: 16L9 Fv
| 超分子 | 名称: 16L9 Fv / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Spike glycoprotein
| 分子 | 名称: Spike glycoprotein / タイプ: protein_or_peptide / ID: 1 詳細: residues 682-685 are substitution at furin cleavage site. T4 fibritin trimerization motif, twin strep II tag and 8-His were introduced at C-terminal. コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 142.506 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MFVFLVLLPL VSSQCVNLTT RTQLPPAYTN SFTRGVYYPD KVFRSSVLHS TQDLFLPFFS NVTWFHVISG TNGTKRFDNP VLPFNDGVY FASIEKSNII RGWIFGTTLD SKTQSLLIVN NATNVVIKVC EFQFCNDPFL DHKNNKSWME SEFRVYSSAN N CTFEYVSQ ...文字列: MFVFLVLLPL VSSQCVNLTT RTQLPPAYTN SFTRGVYYPD KVFRSSVLHS TQDLFLPFFS NVTWFHVISG TNGTKRFDNP VLPFNDGVY FASIEKSNII RGWIFGTTLD SKTQSLLIVN NATNVVIKVC EFQFCNDPFL DHKNNKSWME SEFRVYSSAN N CTFEYVSQ PFLMDLEGKQ GNFKNLREFV FKNIDGYFKI YSKHTPIIVR EPEDLPQGFS ALEPLVDLPI GINITRFQTL LA LHRSYLT PGDSSSGWTA GAAAYYVGYL QPRTFLLKYN ENGTITDAVD CALDPLSETK CTLKSFTVEK GIYQTSNFRV QPT ESIVRF PNITNLCPFD EVFNATRFAS VYAWNRKRIS NCVADYSVLY NLAPFFTFKC YGVSPTKLND LCFTNVYADS FVIR GDEVR QIAPGQTGNI ADYNYKLPDD FTGCVIAWNS NKLDSKVSGN YNYLYRLFRK SNLKPFERDI STEIYQAGNK PCNGV AGFN CYFPLRSYSF RPTYGVGHQP YRVVVLSFEL LHAPATVCGP KKSTNLVKNK CVNFNFNGLK GTGVLTESNK KFLPFQ QFG RDIADTTDAV RDPQTLEILD ITPCSFGGVS VITPGTNTSN QVAVLYQGVN CTEVPVAIHA DQLTPTWRVY STGSNVF QT RAGCLIGAEY VNNSYECDIP IGAGICASYQ TQTKSHGSAS SVASQSIIAY TMSLGAENSV AYSNNSIAIP TNFTISVT T EILPVSMTKT SVDCTMYICG DSTECSNLLL QYGSFCTQLK RALTGIAVEQ DKNTQEVFAQ VKQIYKTPPI KYFGGFNFS QILPDPSKPS KRSPIEDLLF NKVTLADAGF IKQYGDCLGD IAARDLICAQ KFKGLTVLPP LLTDEMIAQY TSALLAGTIT SGWTFGAGP ALQIPFPMQM AYRFNGIGVT QNVLYENQKL IANQFNSAIG KIQDSLSSTP SALGKLQDVV NHNAQALNTL V KQLSSKFG AISSVLNDIF SRLDPPEAEV QIDRLITGRL QSLQTYVTQQ LIRAAEIRAS ANLAATKMSE CVLGQSKRVD FC GKGYHLM SFPQSAPHGV VFLHVTYVPA QEKNFTTAPA ICHDGKAHFP REGVFVSNGT HWFVTQRNFY EPQIITTDNT FVS GNCDVV IGIVNNTVYD PLQPELDSFK EELDKYFKNH TSPDVDLGDI SGINASVVNI QKEIDRLNEV AKNLNESLID LQEL GKYEQ GSGYIPEAPR DGQAYVRKDG EWVFLSTFLS GLEVLFQGPG GWSHPQFEKG GGSGGGSGGS AWSHPQFEKG GSHHH HHHH H UniProtKB: Spike glycoprotein |
-分子 #2: 16L9 Fv
| 分子 | 名称: 16L9 Fv / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 25.730025 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: QSVLTQPPSA SGSPGQSVTI SCTGTSSDFG GYNSVSWYQQ HPGKAPKLMI YEVSKRPSGV PDRFSGSKSG NTASLTVSGL QAEDEADYY CSSYAGSNNF DVFGTGTKVT VLGGGGSGGG GSGGGGSEVQ LVESGGGLIQ PGGSLRLSCA ASGFTVSSNY M SWVRQAPG ...文字列: QSVLTQPPSA SGSPGQSVTI SCTGTSSDFG GYNSVSWYQQ HPGKAPKLMI YEVSKRPSGV PDRFSGSKSG NTASLTVSGL QAEDEADYY CSSYAGSNNF DVFGTGTKVT VLGGGGSGGG GSGGGGSEVQ LVESGGGLIQ PGGSLRLSCA ASGFTVSSNY M SWVRQAPG KGLEWVSVIY SGGSTYYADS VKGRFTISRD NSENTLYLQM NSLRAEDTAV YYCARGEIQP YYYYGMDVWG QG TTVTVSS |
-分子 #3: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 3 / コピー数: 28 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 58.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)