+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-3247 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Subtomogram average of a piliated type IVa pilus machine in wild-type Myxococcus xanthus cells | |||||||||
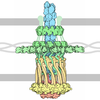
 マップデータ マップデータ | Subtomogram average of a piliated type IVa pilus machine in wild-type Myxococcus xanthus cells | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | type IV pilus / motor / motility / adhesion | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報type IV pilus assembly / type IV pilus-dependent motility / pilus assembly / protein secretion by the type II secretion system / protein secretion / cell outer membrane / cell division / ATP hydrolysis activity / ATP binding / metal ion binding ...type IV pilus assembly / type IV pilus-dependent motility / pilus assembly / protein secretion by the type II secretion system / protein secretion / cell outer membrane / cell division / ATP hydrolysis activity / ATP binding / metal ion binding / membrane / plasma membrane / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Myxococcus xanthus (バクテリア) Myxococcus xanthus (バクテリア) | |||||||||
| 手法 | サブトモグラム平均法 / クライオ電子顕微鏡法 | |||||||||
 データ登録者 データ登録者 | Chang YW / Rettberg LA / Treuner-Lange A / Iwasa J / Sogaard-Andersen L / Jensen GJ | |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2016 ジャーナル: Science / 年: 2016タイトル: Architecture of the type IVa pilus machine. 著者: Yi-Wei Chang / Lee A Rettberg / Anke Treuner-Lange / Janet Iwasa / Lotte Søgaard-Andersen / Grant J Jensen /   要旨: Type IVa pili are filamentous cell surface structures observed in many bacteria. They pull cells forward by extending, adhering to surfaces, and then retracting. We used cryo-electron tomography of ...Type IVa pili are filamentous cell surface structures observed in many bacteria. They pull cells forward by extending, adhering to surfaces, and then retracting. We used cryo-electron tomography of intact Myxococcus xanthus cells to visualize type IVa pili and the protein machine that assembles and retracts them (the type IVa pilus machine, or T4PM) in situ, in both the piliated and nonpiliated states, at a resolution of 3 to 4 nanometers. We found that T4PM comprises an outer membrane pore, four interconnected ring structures in the periplasm and cytoplasm, a cytoplasmic disc and dome, and a periplasmic stem. By systematically imaging mutants lacking defined T4PM proteins or with individual proteins fused to tags, we mapped the locations of all 10 T4PM core components and the minor pilins, thereby providing insights into pilus assembly, structure, and function. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_3247.map.gz emd_3247.map.gz | 3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-3247-v30.xml emd-3247-v30.xml emd-3247.xml emd-3247.xml | 7.7 KB 7.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_3247.tif emd_3247.tif emd_3247_1.tif emd_3247_1.tif | 97.9 KB 60 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-3247 http://ftp.pdbj.org/pub/emdb/structures/EMD-3247 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3247 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3247 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_3247_validation.pdf.gz emd_3247_validation.pdf.gz | 327.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_3247_full_validation.pdf.gz emd_3247_full_validation.pdf.gz | 326.9 KB | 表示 | |
| XML形式データ |  emd_3247_validation.xml.gz emd_3247_validation.xml.gz | 4.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3247 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3247 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3247 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3247 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  3jc8MC  3248C  3249C  3250C  3251C  3252C  3253C  3254C  3255C  3256C  3257C  3258C  3259C  3260C  3261C  3262C  3263C  3264C  3jc9C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_3247.map.gz / 形式: CCP4 / 大きさ: 3.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_3247.map.gz / 形式: CCP4 / 大きさ: 3.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Subtomogram average of a piliated type IVa pilus machine in wild-type Myxococcus xanthus cells | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 これらの図は立方格子座標系で作成されたものです | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 7.8 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
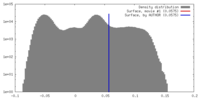
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Wild-type Myxococcus xanthus DK1622 cells
| 全体 | 名称: Wild-type Myxococcus xanthus DK1622 cells |
|---|---|
| 要素 |
|
-超分子 #1000: Wild-type Myxococcus xanthus DK1622 cells
| 超分子 | 名称: Wild-type Myxococcus xanthus DK1622 cells / タイプ: sample / ID: 1000 / Number unique components: 1 |
|---|
-超分子 #1: Type IVa pilus
| 超分子 | 名称: Type IVa pilus / タイプ: organelle_or_cellular_component / ID: 1 / 組換発現: No |
|---|---|
| 由来(天然) | 生物種:  Myxococcus xanthus (バクテリア) / 株: DK1622 Myxococcus xanthus (バクテリア) / 株: DK1622 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | サブトモグラム平均法 |
| 試料の集合状態 | cell |
- 試料調製
試料調製
| 凍結 | 凍結剤: ETHANE-PROPANE MIXTURE / 装置: FEI VITROBOT MARK III |
|---|
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI POLARA 300 |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GATAN エネルギーフィルター - エネルギー下限: 0.0 eV エネルギーフィルター - エネルギー上限: 20.0 eV |
| 日付 | 2013年8月26日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 150 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 倍率(公称値): 27500 |
| 試料ステージ | 試料ホルダーモデル: GATAN LIQUID NITROGEN / Tilt series - Axis1 - Min angle: -60 ° / Tilt series - Axis1 - Max angle: 60 ° |
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 想定した対称性 - 点群: C2 (2回回転対称) / アルゴリズム: OTHER / ソフトウェア - 名称: IMOD, TOMO3D, PEET / 使用したサブトモグラム数: 134 |
|---|
 ムービー
ムービー コントローラー
コントローラー





 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)