+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of human LACTB filament | |||||||||
 マップデータ マップデータ | Refine3D map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | serine protease / filament / tumor suppressor / membrane / mitochondria / beta lactamase / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素 / regulation of lipid metabolic process / lipid metabolic process / peptidase activity / mitochondrion / proteolysis / identical protein binding / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
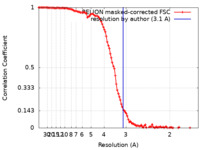
| 手法 | らせん対称体再構成法 / クライオ電子顕微鏡法 / 解像度: 3.1 Å | |||||||||
 データ登録者 データ登録者 | Bennett JA / Steward LR / Aydin H | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: PLoS Biol / 年: 2022 ジャーナル: PLoS Biol / 年: 2022タイトル: The structure of the human LACTB filament reveals the mechanisms of assembly and membrane binding. 著者: Jeremy A Bennett / Lottie R Steward / Johannes Rudolph / Adam P Voss / Halil Aydin /  要旨: Mitochondria are complex organelles that play a central role in metabolism. Dynamic membrane-associated processes regulate mitochondrial morphology and bioenergetics in response to cellular demand. ...Mitochondria are complex organelles that play a central role in metabolism. Dynamic membrane-associated processes regulate mitochondrial morphology and bioenergetics in response to cellular demand. In tumor cells, metabolic reprogramming requires active mitochondrial metabolism for providing key metabolites and building blocks for tumor growth and rapid proliferation. To counter this, the mitochondrial serine beta-lactamase-like protein (LACTB) alters mitochondrial lipid metabolism and potently inhibits the proliferation of a variety of tumor cells. Mammalian LACTB is localized in the mitochondrial intermembrane space (IMS), where it assembles into filaments to regulate the efficiency of essential metabolic processes. However, the structural basis of LACTB polymerization and regulation remains incompletely understood. Here, we describe how human LACTB self-assembles into micron-scale filaments that increase their catalytic activity. The electron cryo-microscopy (cryoEM) structure defines the mechanism of assembly and reveals how highly ordered filament bundles stabilize the active state of the enzyme. We identify and characterize residues that are located at the filament-forming interface and further show that mutations that disrupt filamentation reduce enzyme activity. Furthermore, our results provide evidence that LACTB filaments can bind lipid membranes. These data reveal the detailed molecular organization and polymerization-based regulation of human LACTB and provide new insights into the mechanism of mitochondrial membrane organization that modulates lipid metabolism. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_26595.map.gz emd_26595.map.gz | 98.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-26595-v30.xml emd-26595-v30.xml emd-26595.xml emd-26595.xml | 21 KB 21 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_26595_fsc.xml emd_26595_fsc.xml | 11.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_26595.png emd_26595.png | 101.4 KB | ||
| マスクデータ |  emd_26595_msk_1.map emd_26595_msk_1.map | 125 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-26595.cif.gz emd-26595.cif.gz | 6.5 KB | ||
| その他 |  emd_26595_additional_1.map.gz emd_26595_additional_1.map.gz emd_26595_half_map_1.map.gz emd_26595_half_map_1.map.gz emd_26595_half_map_2.map.gz emd_26595_half_map_2.map.gz | 116.6 MB 98.6 MB 98.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-26595 http://ftp.pdbj.org/pub/emdb/structures/EMD-26595 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26595 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26595 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_26595_validation.pdf.gz emd_26595_validation.pdf.gz | 1.1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_26595_full_validation.pdf.gz emd_26595_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  emd_26595_validation.xml.gz emd_26595_validation.xml.gz | 18.6 KB | 表示 | |
| CIF形式データ |  emd_26595_validation.cif.gz emd_26595_validation.cif.gz | 24.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26595 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26595 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26595 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26595 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7ulwMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_26595.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_26595.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Refine3D map | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.8211 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_26595_msk_1.map emd_26595_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
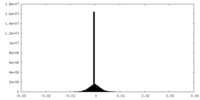
| 投影像・断面図 |
| ||||||||||||
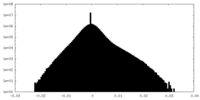
| 密度ヒストグラム |
-追加マップ: Postprocess map
| ファイル | emd_26595_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Postprocess map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Refine3D half map 1
| ファイル | emd_26595_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Refine3D half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Refine3D half map 2
| ファイル | emd_26595_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Refine3D half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : LACTB
| 全体 | 名称: LACTB |
|---|---|
| 要素 |
|
-超分子 #1: LACTB
| 超分子 | 名称: LACTB / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: Uniprot ID: P83111 - HUMAN LACTB, Serine beta-lactamase-like protein LACTB, mitochondrial |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 510 KDa |
-分子 #1: Serine beta-lactamase-like protein LACTB, mitochondrial
| 分子 | 名称: Serine beta-lactamase-like protein LACTB, mitochondrial タイプ: protein_or_peptide / ID: 1 / コピー数: 6 / 光学異性体: LEVO EC番号: 加水分解酵素; プロテアーゼ; ペプチド結合加水分解酵素 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 51.318648 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: APPCSRCFAR AIESSRDLLH RIKDEVGAPG IVVGVSVDGK EVWSEGLGYA DVENRVPCKP ETVMRIASIS KSLTMVALAK LWEAGKLDL DIPVQHYVPE FPEKEYEGEK VSVTTRLLIS HLSGIRHYEK DIKKVKEEKA YKALKMMKEN VAFEQEKEGK S NEKNDFTK ...文字列: APPCSRCFAR AIESSRDLLH RIKDEVGAPG IVVGVSVDGK EVWSEGLGYA DVENRVPCKP ETVMRIASIS KSLTMVALAK LWEAGKLDL DIPVQHYVPE FPEKEYEGEK VSVTTRLLIS HLSGIRHYEK DIKKVKEEKA YKALKMMKEN VAFEQEKEGK S NEKNDFTK FKTEQENEAK CRNSKPGKKK NDFEQGELYL REKFENSIES LRLFKNDPLF FKPGSQFLYS TFGYTLLAAI VE RASGCKY LDYMQKIFHD LDMLTTVQEE NEPVIYNRAR FYVYNKKKRL VNTPYVDNSY KWAGGGFLST VGDLLKFGNA MLY GYQVGL FKNSNENLLP GYLKPETMVM MWTPVPNTEM SWDKEGKYAM AWGVVERKQT YGSCRKQRHY ASHTGGAVGA SSVL LVLPE ELDTETINNK VPPRGIIVSI ICNMQSVGLN STALKIALEF DKDRSD UniProtKB: Serine beta-lactamase-like protein LACTB, mitochondrial |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 濃度 | 0.3 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 200 / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均露光時間: 3.985 sec. / 平均電子線量: 59.58 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.5 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)