+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-21133 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM SPA : Structure of the PCBP2/Stem Loop IVm complex underlying the functionality of the poliovirus type I IRES. | |||||||||
 マップデータ マップデータ | Structure of the PCBP2/Stem Loop | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |   Poliovirus type 1 (strain Mahoney) (ポリオウイルス) / Poliovirus type 1 (strain Mahoney) (ポリオウイルス) /  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.1 Å | |||||||||
 データ登録者 データ登録者 | Wilce MCJ / Wilce JA | |||||||||
| 資金援助 |  オーストラリア, 1件 オーストラリア, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2020 ジャーナル: Nucleic Acids Res / 年: 2020タイトル: Structure of the PCBP2/stem-loop IV complex underlying translation initiation mediated by the poliovirus type I IRES. 著者: Simone A Beckham / Mehdi Y Matak / Matthew J Belousoff / Hariprasad Venugopal / Neelam Shah / Naveen Vankadari / Hans Elmlund / Joseph H C Nguyen / Bert L Semler / Matthew C J Wilce / Jacqueline A Wilce /   要旨: The poliovirus type I IRES is able to recruit ribosomal machinery only in the presence of host factor PCBP2 that binds to stem-loop IV of the IRES. When PCBP2 is cleaved in its linker region by viral ...The poliovirus type I IRES is able to recruit ribosomal machinery only in the presence of host factor PCBP2 that binds to stem-loop IV of the IRES. When PCBP2 is cleaved in its linker region by viral proteinase 3CD, translation initiation ceases allowing the next stage of replication to commence. Here, we investigate the interaction of PCBP2 with the apical region of stem-loop IV (SLIVm) of poliovirus RNA in its full-length and truncated form. CryoEM structure reconstruction of the full-length PCBP2 in complex with SLIVm solved to 6.1 Å resolution reveals a compact globular complex of PCBP2 interacting with the cruciform RNA via KH domains and featuring a prominent GNRA tetraloop. SEC-SAXS, SHAPE and hydroxyl-radical cleavage establish that PCBP2 stabilizes the SLIVm structure, but upon cleavage in the linker domain the complex becomes more flexible and base accessible. Limited proteolysis and REMSA demonstrate the accessibility of the linker region in the PCBP2/SLIVm complex and consequent loss of affinity of PCBP2 for the SLIVm upon cleavage. Together this study sheds light on the structural features of the PCBP2/SLIV complex vital for ribosomal docking, and the way in which this key functional interaction is regulated following translation of the poliovirus genome. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_21133.map.gz emd_21133.map.gz | 8.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-21133-v30.xml emd-21133-v30.xml emd-21133.xml emd-21133.xml | 11.7 KB 11.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_21133.png emd_21133.png | 72.6 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-21133 http://ftp.pdbj.org/pub/emdb/structures/EMD-21133 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21133 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21133 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_21133_validation.pdf.gz emd_21133_validation.pdf.gz | 78.5 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_21133_full_validation.pdf.gz emd_21133_full_validation.pdf.gz | 77.7 KB | 表示 | |
| XML形式データ |  emd_21133_validation.xml.gz emd_21133_validation.xml.gz | 494 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21133 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21133 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21133 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21133 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_21133.map.gz / 形式: CCP4 / 大きさ: 11.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_21133.map.gz / 形式: CCP4 / 大きさ: 11.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Structure of the PCBP2/Stem Loop | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.06 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
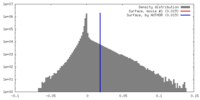
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : truncated stem loop IV of the poliovirus IRES, residues, 278-398 ...
| 全体 | 名称: truncated stem loop IV of the poliovirus IRES, residues, 278-398 in complex with PolyC binding protein 2 |
|---|---|
| 要素 |
|
-超分子 #1: truncated stem loop IV of the poliovirus IRES, residues, 278-398 ...
| 超分子 | 名称: truncated stem loop IV of the poliovirus IRES, residues, 278-398 in complex with PolyC binding protein 2 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Poliovirus type 1 (strain Mahoney) (ポリオウイルス) Poliovirus type 1 (strain Mahoney) (ポリオウイルス)株: Mahoney |
-分子 #1: PolyC Binding Protein 2
| 分子 | 名称: PolyC Binding Protein 2 / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MDTGVIEGGL NVTLTIRLLM HGKEVGSIIG KKGESVKKMR EESGARINIS EGNCPERIIT LAGPTNAIF KAFAMIIDKL EEDISSSMTN STAASRPPVT LRLVVPASQC GSLIGKGGCK I KEIRESTG AQVQVAGDML PNSTERAITI AGIPQSIIEC VKQICVVMLE ...文字列: MDTGVIEGGL NVTLTIRLLM HGKEVGSIIG KKGESVKKMR EESGARINIS EGNCPERIIT LAGPTNAIF KAFAMIIDKL EEDISSSMTN STAASRPPVT LRLVVPASQC GSLIGKGGCK I KEIRESTG AQVQVAGDML PNSTERAITI AGIPQSIIEC VKQICVVMLE TLSQSPPKGV TI PYRPKPS SSPVIFAGGQ DRYSTGSDSA SFPHTTPSMC LNPDLEGPPL EAYTIQGQYA IPQ PDLTKL HQLAMQQSHF PMTHGNTGFS GIESSSPEVK GYWGLDASAQ TTSHELTIPN DLIG CIIGR QGAKINEIRQ MSGAQIKIAN PVEGSTDRQV TITGSAASIS LAQYLINVRL SSETG GMGS SLEHHHHHH |
-分子 #2: Poliovirus (Mahoney) : truncated Stemloop IV from IRES
| 分子 | 名称: Poliovirus (Mahoney) : truncated Stemloop IV from IRES タイプ: rna / ID: 2 詳細: Produced using in vitro transcription : T7 RiboMAX (Promega) |
|---|---|
| 由来(天然) | 生物種:   Poliovirus type 1 (strain Mahoney) (ポリオウイルス) Poliovirus type 1 (strain Mahoney) (ポリオウイルス)株: Mahoney |
| 配列 | 文字列: CGCGCGUUGC GCUCAGCACU CAACCCCAGA GUGUAGCUUA GGCUGAUGAG UCUGGACAUC CCUCACCGGU GACGGUGGUC CAGGCUGCGU UGGCGGCCUA CCUAUGGCUA ACGCCAUGGG ACGCGCG |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | 2D array |
- 試料調製
試料調製
| 濃度 | 0.14 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 詳細: 5 mM HEPES-KOH, 25 mM KCl, 2 mM MgCl2, 2 mM DTT, 4 % glycerol, 0.1 mM EDTA, pH 7.5 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 298 K / 装置: FEI VITROBOT MARK IV / 詳細: 2.5 second blot. |
| 詳細 | A mono disperse sample was applied |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | 位相板: VOLTA PHASE PLATE |
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: OTHER |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | ソフトウェア - 名称: CTFFIND / ソフトウェア - 詳細: CTFFIND |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / アルゴリズム: FOURIER SPACE / 解像度のタイプ: BY AUTHOR / 解像度: 6.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 888988 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
-原子モデル構築 1
| 精密化 | プロトコル: AB INITIO MODEL |
|---|
 ムービー
ムービー コントローラー
コントローラー













 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)