+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | HSV-1 DNA polymerase-processivity factor complex in halted elongation state | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | DNA / Polymerase / Complex / TRANSFERASE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報DNA polymerase activity / DNA polymerase complex / bidirectional double-stranded viral DNA replication / 5'-3' exonuclease activity / ribonuclease H / DNA polymerase processivity factor activity / DNA-templated DNA replication / RNA-DNA hybrid ribonuclease activity / DNA-directed DNA polymerase / DNA-directed DNA polymerase activity ...DNA polymerase activity / DNA polymerase complex / bidirectional double-stranded viral DNA replication / 5'-3' exonuclease activity / ribonuclease H / DNA polymerase processivity factor activity / DNA-templated DNA replication / RNA-DNA hybrid ribonuclease activity / DNA-directed DNA polymerase / DNA-directed DNA polymerase activity / DNA replication / nucleotide binding / host cell nucleus / DNA binding 類似検索 - 分子機能 | |||||||||
| 生物種 |   Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) / synthetic construct (人工物) Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) / synthetic construct (人工物) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.46 Å | |||||||||
 データ登録者 データ登録者 | Gustavsson E / Grunewald K / Elias P / Hallberg BM | |||||||||
| 資金援助 |  スウェーデン, スウェーデン,  ドイツ, 2件 ドイツ, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2024 ジャーナル: Nucleic Acids Res / 年: 2024タイトル: Dynamics of the Herpes simplex virus DNA polymerase holoenzyme during DNA synthesis and proof-reading revealed by Cryo-EM. 著者: Emil Gustavsson / Kay Grünewald / Per Elias / B Martin Hällberg /   要旨: Herpes simplex virus 1 (HSV-1), a double-stranded DNA virus, replicates using seven essential proteins encoded by its genome. Among these, the UL30 DNA polymerase, complexed with the UL42 ...Herpes simplex virus 1 (HSV-1), a double-stranded DNA virus, replicates using seven essential proteins encoded by its genome. Among these, the UL30 DNA polymerase, complexed with the UL42 processivity factor, orchestrates leading and lagging strand replication of the 152 kb viral genome. UL30 polymerase is a prime target for antiviral therapy, and resistance to current drugs can arise in immunocompromised individuals. Using electron cryo-microscopy (cryo-EM), we unveil the dynamic changes of the UL30/UL42 complex with DNA in three distinct states. First, a pre-translocation state with an open fingers domain ready for nucleotide incorporation. Second, a halted elongation state where the fingers close, trapping dATP in the dNTP pocket. Third, a DNA-editing state involving significant conformational changes to allow DNA realignment for exonuclease activity. Additionally, the flexible UL30 C-terminal domain interacts with UL42, forming an extended positively charged surface binding to DNA, thereby enhancing processive synthesis. These findings highlight substantial structural shifts in the polymerase and its DNA interactions during replication, offering insights for future antiviral drug development. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_16907.map.gz emd_16907.map.gz | 3.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-16907-v30.xml emd-16907-v30.xml emd-16907.xml emd-16907.xml | 19.5 KB 19.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_16907.png emd_16907.png | 96.8 KB | ||
| マスクデータ |  emd_16907_msk_1.map emd_16907_msk_1.map | 307.5 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-16907.cif.gz emd-16907.cif.gz | 7.6 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-16907 http://ftp.pdbj.org/pub/emdb/structures/EMD-16907 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16907 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16907 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_16907_validation.pdf.gz emd_16907_validation.pdf.gz | 357.8 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_16907_full_validation.pdf.gz emd_16907_full_validation.pdf.gz | 357.4 KB | 表示 | |
| XML形式データ |  emd_16907_validation.xml.gz emd_16907_validation.xml.gz | 7.2 KB | 表示 | |
| CIF形式データ |  emd_16907_validation.cif.gz emd_16907_validation.cif.gz | 8.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16907 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16907 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16907 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16907 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8oj7MC  8oj6C  8ojaC  8ojbC  8ojcC  8ojdC  9enpC  9enqC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_16907.map.gz / 形式: CCP4 / 大きさ: 307.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_16907.map.gz / 形式: CCP4 / 大きさ: 307.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
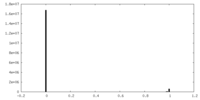
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.85 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_16907_msk_1.map emd_16907_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
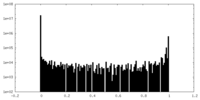
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : HSV-1 DNA polymerase-processivity factor complex in halted elonga...
| 全体 | 名称: HSV-1 DNA polymerase-processivity factor complex in halted elongation state |
|---|---|
| 要素 |
|
-超分子 #1: HSV-1 DNA polymerase-processivity factor complex in halted elonga...
| 超分子 | 名称: HSV-1 DNA polymerase-processivity factor complex in halted elongation state タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 |
|---|---|
| 由来(天然) | 生物種:   Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) |
-分子 #1: DNA polymerase catalytic subunit
| 分子 | 名称: DNA polymerase catalytic subunit / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: DNA-directed DNA polymerase |
|---|---|
| 由来(天然) | 生物種:   Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) |
| 分子量 | 理論値: 136.683844 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MFSGGGGPLS PGGKSAARAA SGFFAPAGPR GASRGPPPCL RQNFYNPYLA PVGTQQKPTG PTQRHTYYSE CDEFRFIAPR VLDEDAPPE KRAGVHDGHL KRAPKVYCGG DERDVLRVGS GGFWPRRSRL WGGVDHAPAG FNPTVTVFHV YDILENVEHA Y GMRAAQFH ...文字列: MFSGGGGPLS PGGKSAARAA SGFFAPAGPR GASRGPPPCL RQNFYNPYLA PVGTQQKPTG PTQRHTYYSE CDEFRFIAPR VLDEDAPPE KRAGVHDGHL KRAPKVYCGG DERDVLRVGS GGFWPRRSRL WGGVDHAPAG FNPTVTVFHV YDILENVEHA Y GMRAAQFH ARFMDAITPT GTVITLLGLT PEGHRVAVHV YGTRQYFYMN KEEVDRHLQC RAPRDLCERM AAALRESPGA SF RGISADH FEAEVVERTD VYYYETRPAL FYRVYVRSGR VLSYLCDNFC PAIKKYEGGV DATTRFILDN PGFVTFGWYR LKP GRNNTL AQPRAPMAFG TSSDVEFNCT ADNLAIEGGM SDLPAYKLMC FDIECKAGGE DELAFPVAGH PEDLVIQISC LLYD LSTTA LEHVLLFSLG SCDLPESHLN ELAARGLPTP VVLEFDSEFE MLLAFMTLVK QYGPEFVTGY NIINFDWPFL LAKLT DIYK VPLDGYGRMN GRGVFRVWDI GQSHFQKRSK IKVNGMVNID MYGIITDKIK LSSYKLNAVA EAVLKDKKKD LSYRDI PAY YAAGPAQRGV IGEYCIQDSL LVGQLFFKFL PHLELSAVAR LAGINITRTI YDGQQIRVFT CLLRLADQKG FILPDTQ GR FRGAGGEAPK RPAAAREDEE RPEEEGEDED EREEGGGERE PEGARETAGR HVGYQGARVL DPTSGFHVNP VVVFDFAS L YPSIIQAHNL CFSTLSLRAD AVAHLEAGKD YLEIEVGGRR LFFVKAHVRE SLLSILLRDW LAMRKQIRSR IPQSSPEEA VLLDKQQAAI KVVCNSVYGF TGVQHGLLPC LHVAATVTTI GREMLLATRE YVHARWAAFE QLLADFPEAA DMRAPGPYSM RIIYGDTDS IFVLCRGLTA AGLTAVGDKM ASHISRALFL PPIKLECEKT FTKLLLIAKK KYIGVIYGGK MLIKGVDLVR K NNCAFINR TSRALVDLLF YDDTVSGAAA ALAERPAEEW LARPLPEGLQ AFGAVLVDAH RRITDPERDI QDFVLTAELS RH PRAYTNK RLAHLTVYYK LMARRAQVPS IKDRIPYVIV AQTREVEETV ARLAALRELD AAAPGDEPAP PAALPSPAKR PRE TPSPAD PPGGASKPRK LLVSELAEDP AYAIAHGVAL NTDYYFSHLL GAACVTFKAL FGNNAKITES LLKRFIPEVW HPPD DVAAR LRTAGFGAVG AGATAEETRR MLHRAFDTLA UniProtKB: DNA polymerase catalytic subunit |
-分子 #2: DNA polymerase processivity factor
| 分子 | 名称: DNA polymerase processivity factor / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) Human alphaherpesvirus 1 strain KOS (ヘルペスウイルス) |
| 分子量 | 理論値: 51.207969 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MTDSPGGVAP ASPVEDASDA SLGQPEEGAP CQVVLQGAEL NGILQAFAPL RTSLLDSLLV MGDRGILIHN TIFGEQVFLP LEHSQFSRY RWRGPTAAFL SLVDQKRSLL SVFRANQYPD LRRVELAITG QAPFRTLVQR IWTTTSDGEA VELASETLMK R ELTSFVVL ...文字列: MTDSPGGVAP ASPVEDASDA SLGQPEEGAP CQVVLQGAEL NGILQAFAPL RTSLLDSLLV MGDRGILIHN TIFGEQVFLP LEHSQFSRY RWRGPTAAFL SLVDQKRSLL SVFRANQYPD LRRVELAITG QAPFRTLVQR IWTTTSDGEA VELASETLMK R ELTSFVVL VPQGTPDVQL RLTRPQLTKV LNATGADSAT PTTFELGVNG KFSVFTTSTC VTFAAREEGV SSSTSTQVQI LS NALTKAG QAAANAKTVY GENTHRTFSV VVDDCSMRAV LRRLQVGGGT LKFFLTTPVP SLCVTATGPN AVSAVFLLKP QKI CLDWLG HSQGSPSAGS SASRASGSEP TDSQDSASDA VSHGDPEDLD GAARAGEAGA LHACPMPSST TRVTPTTKRG RSGG EDARA DTALKKPKTG SPTAPPPADP VPLDTEDDSD AADGTAARPA APDARSGSRY ACYFRDLPTG EASPGAFSAF RGGPQ TPYG FGFP UniProtKB: DNA polymerase processivity factor |
-分子 #3: DNA (53-MER)
| 分子 | 名称: DNA (53-MER) / タイプ: dna / ID: 3 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 16.081343 KDa |
| 配列 | 文字列: (DG)(DC)(DC)(DA)(DC)(DT)(DA)(DC)(DG)(DA) (DC)(DA)(DC)(DC)(DT)(DT)(DG)(DA)(DT)(DC) (DG)(DC)(DC)(DT)(DC)(DG)(DC)(DA)(DG) (DC)(DC)(DG)(DT)(DC)(DC)(DA)(DA)(DC)(DC) (DA) (DA)(DC)(DT)(DC)(DA) ...文字列: (DG)(DC)(DC)(DA)(DC)(DT)(DA)(DC)(DG)(DA) (DC)(DA)(DC)(DC)(DT)(DT)(DG)(DA)(DT)(DC) (DG)(DC)(DC)(DT)(DC)(DG)(DC)(DA)(DG) (DC)(DC)(DG)(DT)(DC)(DC)(DA)(DA)(DC)(DC) (DA) (DA)(DC)(DT)(DC)(DA)(DA)(DT)(DT) (DA)(DG)(DA)(DA)(DOC) |
-分子 #4: DNA (67-MER)
| 分子 | 名称: DNA (67-MER) / タイプ: dna / ID: 4 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 20.845285 KDa |
| 配列 | 文字列: (DA)(DT)(DT)(DT)(DG)(DC)(DT)(DG)(DA)(DC) (DC)(DT)(DT)(DT)(DG)(DT)(DT)(DC)(DT)(DA) (DA)(DT)(DT)(DG)(DA)(DG)(DT)(DT)(DG) (DG)(DT)(DT)(DG)(DG)(DA)(DC)(DG)(DG)(DC) (DT) (DG)(DC)(DG)(DA)(DG) ...文字列: (DA)(DT)(DT)(DT)(DG)(DC)(DT)(DG)(DA)(DC) (DC)(DT)(DT)(DT)(DG)(DT)(DT)(DC)(DT)(DA) (DA)(DT)(DT)(DG)(DA)(DG)(DT)(DT)(DG) (DG)(DT)(DT)(DG)(DG)(DA)(DC)(DG)(DG)(DC) (DT) (DG)(DC)(DG)(DA)(DG)(DG)(DC)(DG) (DA)(DT)(DC)(DA)(DA)(DG)(DG)(DT)(DG)(DT) (DC)(DG) (DT)(DA)(DG)(DT)(DG)(DG)(DC) |
-分子 #5: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 5 / コピー数: 2 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #6: 2'-DEOXYADENOSINE 5'-TRIPHOSPHATE
| 分子 | 名称: 2'-DEOXYADENOSINE 5'-TRIPHOSPHATE / タイプ: ligand / ID: 6 / コピー数: 1 / 式: DTP |
|---|---|
| 分子量 | 理論値: 491.182 Da |
| Chemical component information | 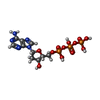 ChemComp-DTP: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.4 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.8 構成要素:
詳細: 20mM HEPES pH7.8, 150mM NaCl, 5mM MgCl2, 2mM DTT | |||||||||||||||
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 120 sec. | |||||||||||||||
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 95 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.46 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: cryoSPARC (ver. 4) / 詳細: cryoSPARC Non-uniform refinement / 使用した粒子像数: 213621 |
| 初期 角度割当 | タイプ: RANDOM ASSIGNMENT / ソフトウェア - 名称: cryoSPARC (ver. 3.3) |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: cryoSPARC (ver. 4) |
 ムービー
ムービー コントローラー
コントローラー



























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)