+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Triple-stranded DNA as a structural element in DNA origami large cuboid object | |||||||||||||||
 マップデータ マップデータ | large cuboid DNA origami object | |||||||||||||||
 試料 試料 |
| |||||||||||||||
 キーワード キーワード | DNA Origami / Triplex forming Oligo / Triplex / TFO / DNA / DNA nanotechnology | |||||||||||||||
| 生物種 | synthetic construct (人工物) /  Phage M13mp18 (ファージ) Phage M13mp18 (ファージ) | |||||||||||||||
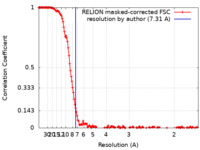
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.31 Å | |||||||||||||||
 データ登録者 データ登録者 | Sachenbacher K / Khoshouei A / Honemann MN / Engelen W / Feigl E / Dietz H | |||||||||||||||
| 資金援助 | European Union,  ドイツ, ドイツ,  オランダ, 4件 オランダ, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: ACS Nano / 年: 2023 ジャーナル: ACS Nano / 年: 2023タイトル: Triple-Stranded DNA As a Structural Element in DNA Origami. 著者: Ken Sachenbacher / Ali Khoshouei / Maximilian Nicolas Honemann / Wouter Engelen / Elija Feigl / Hendrik Dietz /  要旨: Molecular self-assembly with DNA origami offers an attractive route to fabricate arbitrary three-dimensional nanostructures. In DNA origami, B-form double-helical DNA domains (dsDNA) are commonly ...Molecular self-assembly with DNA origami offers an attractive route to fabricate arbitrary three-dimensional nanostructures. In DNA origami, B-form double-helical DNA domains (dsDNA) are commonly linked with covalent phosphodiester strand crossovers to build up three-dimensional objects. To expand the palette of structural motifs in DNA origami, here we describe hybrid duplex-triplex DNA motifs as pH-dependent building blocks in DNA origami. We investigate design rules for incorporating triplex forming oligonucleotides and noncanonical duplex-triplex crossovers in multilayer DNA origami objects. We use single-particle cryoelectron microscopy to elucidate the structural basis of triplex domains and of duplex-triplex crossovers. We find that duplex-triplex crossovers can complement and fully replace the canonical duplex-duplex crossovers within DNA origami objects, for example, to increase the crossover density for potentially greater rigidity and reduced interhelical spacing, and to create connections at sites where conventional crossovers may be undesirable. We also show the pH-induced formation of a DNA origami object stabilized entirely by triplex-mediated strand crossovers. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_16213.map.gz emd_16213.map.gz | 51.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-16213-v30.xml emd-16213-v30.xml emd-16213.xml emd-16213.xml | 16.6 KB 16.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_16213_fsc.xml emd_16213_fsc.xml | 15.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_16213.png emd_16213.png | 90.4 KB | ||
| その他 |  emd_16213_half_map_1.map.gz emd_16213_half_map_1.map.gz emd_16213_half_map_2.map.gz emd_16213_half_map_2.map.gz | 242.3 MB 242.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-16213 http://ftp.pdbj.org/pub/emdb/structures/EMD-16213 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16213 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16213 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_16213_validation.pdf.gz emd_16213_validation.pdf.gz | 935.1 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_16213_full_validation.pdf.gz emd_16213_full_validation.pdf.gz | 934.7 KB | 表示 | |
| XML形式データ |  emd_16213_validation.xml.gz emd_16213_validation.xml.gz | 22.8 KB | 表示 | |
| CIF形式データ |  emd_16213_validation.cif.gz emd_16213_validation.cif.gz | 30.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16213 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16213 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16213 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16213 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_16213.map.gz / 形式: CCP4 / 大きさ: 303.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_16213.map.gz / 形式: CCP4 / 大きさ: 303.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | large cuboid DNA origami object | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.85 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: large cuboid DNA origami object / half map 1
| ファイル | emd_16213_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | large cuboid DNA origami object / half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: large cuboid DNA origami object / half map 2
| ファイル | emd_16213_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | large cuboid DNA origami object / half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : DNA Nanostructure
| 全体 | 名称: DNA Nanostructure |
|---|---|
| 要素 |
|
-超分子 #1: DNA Nanostructure
| 超分子 | 名称: DNA Nanostructure / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
-超分子 #2: Scaffold DNA single-strand
| 超分子 | 名称: Scaffold DNA single-strand / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Phage M13mp18 (ファージ) Phage M13mp18 (ファージ) |
-超分子 #3: staple oligonucleotides
| 超分子 | 名称: staple oligonucleotides / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 / 詳細: 5 mM Tris, 1 mM EDTA, 5 mM NaCl and 5 mM MgCl2 |
|---|---|
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 293 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: INTEGRATING / デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 5.0 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 75000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)