+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of mouse Pannexin 1 purified in Salipro nanoparticles | |||||||||
 マップデータ マップデータ | DeepEMhancer sharpened map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Membrane transporter / ATP-release channel / inflammation / immune function / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Electric Transmission Across Gap Junctions / The NLRP3 inflammasome / ATP transmembrane transporter activity / ATP transport / leak channel activity / positive regulation of interleukin-1 alpha production / bleb / monoatomic anion transmembrane transport / monoatomic anion channel activity / gap junction ...Electric Transmission Across Gap Junctions / The NLRP3 inflammasome / ATP transmembrane transporter activity / ATP transport / leak channel activity / positive regulation of interleukin-1 alpha production / bleb / monoatomic anion transmembrane transport / monoatomic anion channel activity / gap junction / gap junction channel activity / positive regulation of macrophage cytokine production / response to ATP / response to ischemia / positive regulation of interleukin-1 beta production / calcium channel activity / actin filament binding / calcium ion transport / cell-cell signaling / actin binding / protease binding / scaffold protein binding / transmembrane transporter binding / signaling receptor binding / endoplasmic reticulum membrane / structural molecule activity / endoplasmic reticulum / protein-containing complex / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
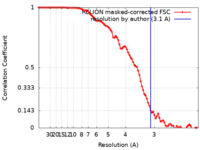
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.1 Å | |||||||||
 データ登録者 データ登録者 | Drulyte I | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Sci Rep / 年: 2023 ジャーナル: Sci Rep / 年: 2023タイトル: Direct cell extraction of membrane proteins for structure-function analysis. 著者: Ieva Drulyte / Aspen Rene Gutgsell / Pilar Lloris-Garcerá / Michael Liss / Stefan Geschwindner / Mazdak Radjainia / Jens Frauenfeld / Robin Löving /    要旨: Membrane proteins are the largest group of therapeutic targets in a variety of disease areas and yet, they remain particularly difficult to investigate. We have developed a novel one-step approach ...Membrane proteins are the largest group of therapeutic targets in a variety of disease areas and yet, they remain particularly difficult to investigate. We have developed a novel one-step approach for the incorporation of membrane proteins directly from cells into lipid Salipro nanoparticles. Here, with the pannexin1 channel as a case study, we demonstrate the applicability of this method for structure-function analysis using SPR and cryo-EM. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_15110.map.gz emd_15110.map.gz | 57 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-15110-v30.xml emd-15110-v30.xml emd-15110.xml emd-15110.xml | 19.8 KB 19.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_15110_fsc.xml emd_15110_fsc.xml | 9.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_15110.png emd_15110.png | 124.7 KB | ||
| Filedesc metadata |  emd-15110.cif.gz emd-15110.cif.gz | 6.3 KB | ||
| その他 |  emd_15110_additional_1.map.gz emd_15110_additional_1.map.gz emd_15110_half_map_1.map.gz emd_15110_half_map_1.map.gz emd_15110_half_map_2.map.gz emd_15110_half_map_2.map.gz | 48.9 MB 49.4 MB 49.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-15110 http://ftp.pdbj.org/pub/emdb/structures/EMD-15110 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15110 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15110 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_15110_validation.pdf.gz emd_15110_validation.pdf.gz | 669.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_15110_full_validation.pdf.gz emd_15110_full_validation.pdf.gz | 668.8 KB | 表示 | |
| XML形式データ |  emd_15110_validation.xml.gz emd_15110_validation.xml.gz | 16.1 KB | 表示 | |
| CIF形式データ |  emd_15110_validation.cif.gz emd_15110_validation.cif.gz | 21.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15110 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15110 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15110 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15110 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8a3bMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_15110.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_15110.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | DeepEMhancer sharpened map | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.0905 Å | ||||||||||||||||||||||||||||||||||||
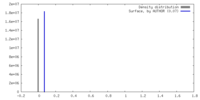
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: Unsharpened map
| ファイル | emd_15110_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
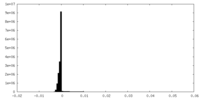
| 密度ヒストグラム |
-ハーフマップ: Half map 2
| ファイル | emd_15110_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
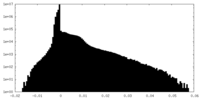
| 密度ヒストグラム |
-ハーフマップ: Half map 1
| ファイル | emd_15110_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
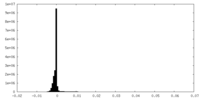
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Salipro-mPANX1
| 全体 | 名称: Salipro-mPANX1 |
|---|---|
| 要素 |
|
-超分子 #1: Salipro-mPANX1
| 超分子 | 名称: Salipro-mPANX1 / タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 353 KDa |
-分子 #1: Pannexin-1
| 分子 | 名称: Pannexin-1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 7 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 50.475434 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MSDYKDDDDK GGGGSMAIAH LATEYVFSDF LLKEPTEPKF KGLRLELAVD KMVTCIAVGL PLLLISLAFA QEISIGTQIS CFSPSSFSW RQAAFVDSYC WAAVQQKSSL QSESGNLPLW LHKFFPYILL LFAILLYLPA LFWRFSAAPH LCSDLKFIME E LDKVYNRA ...文字列: MSDYKDDDDK GGGGSMAIAH LATEYVFSDF LLKEPTEPKF KGLRLELAVD KMVTCIAVGL PLLLISLAFA QEISIGTQIS CFSPSSFSW RQAAFVDSYC WAAVQQKSSL QSESGNLPLW LHKFFPYILL LFAILLYLPA LFWRFSAAPH LCSDLKFIME E LDKVYNRA IKAAKSARDL DLRDGPGPPG VTENVGQSLW EISESHFKYP IVEQYLKTKK NSSHLIMKYI SCRLVTFVVI LL ACIYLSY YFSLSSLSDE FLCSIKSGVL KNDSTIPDRF QCKLIAVGIF QLLSLINLIV YALLIPVVVY TFFIPFRQKT DIL KVYEIL PTFDVLHFKS EGYNDLSLYN LFLEENISEL KSYKCLKVLE NIKSNGQGID PMLLLTNLGM IKMDIIDGKI PTSL QTKGE DQGSQRVEFK DLDLSSEAAA NNGEKNSRQR LLNPSCLEVL FQ UniProtKB: Pannexin-1 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2.5 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 / 詳細: 50 mM HEPES at pH 7.5, 150 mM NaCl |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 45 sec. / 前処理 - 雰囲気: AIR 詳細: Grids were glow-discharged using 20 mAmp current for 45 sec and charge set to positive. |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK IV 詳細: To overcome preferred orientation, 0.5 mM fluorinated Fos-Choline 8 was added to the sample just before the grid freezing. Blot parameter: blot force +20, blot time 10 s, waiting time 30s. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: TFS Selectris X / エネルギーフィルター - スリット幅: 10 eV |
| 詳細 | Titan Krios G4 was used with fringe-free imaging and aberration-free image shifts. Nominal pixel size for 165kx 0.75 A, calibrated pixel size 0.727 A. |
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 撮影したグリッド数: 1 / 実像数: 7955 / 平均露光時間: 4.16 sec. / 平均電子線量: 40.24 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 165000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: RECIPROCAL / プロトコル: RIGID BODY FIT |
|---|---|
| 得られたモデル |  PDB-8a3b: |
 ムービー
ムービー コントローラー
コントローラー




 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)