+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Ligand bound state of a brocolli-pepper aptamer FRET tile | |||||||||
 マップデータ マップデータ | Map sharpened with b-factor of 160 | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | RNA origami aptamer fret / RNA | |||||||||
| 生物種 | synthetic construct (人工物) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.43 Å | |||||||||
 データ登録者 データ登録者 | McRae EKS / Vallina NS / Hansen BK / Boussebayle A / Andersen ES | |||||||||
| 資金援助 |  デンマーク, 1件 デンマーク, 1件
| |||||||||
 引用 引用 |  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2018 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2018タイトル: ISOLDE: a physically realistic environment for model building into low-resolution electron-density maps. 著者: Tristan Ian Croll /  要旨: This paper introduces ISOLDE, a new software package designed to provide an intuitive environment for high-fidelity interactive remodelling/refinement of macromolecular models into electron-density ...This paper introduces ISOLDE, a new software package designed to provide an intuitive environment for high-fidelity interactive remodelling/refinement of macromolecular models into electron-density maps. ISOLDE combines interactive molecular-dynamics flexible fitting with modern molecular-graphics visualization and established structural biology libraries to provide an immersive interface wherein the model constantly acts to maintain physically realistic conformations as the user interacts with it by directly tugging atoms with a mouse or haptic interface or applying/removing restraints. In addition, common validation tasks are accelerated and visualized in real time. Using the recently described 3.8 Å resolution cryo-EM structure of the eukaryotic minichromosome maintenance (MCM) helicase complex as a case study, it is demonstrated how ISOLDE can be used alongside other modern refinement tools to avoid common pitfalls of low-resolution modelling and improve the quality of the final model. A detailed analysis of changes between the initial and final model provides a somewhat sobering insight into the dangers of relying on a small number of validation metrics to judge the quality of a low-resolution model. #1:  ジャーナル: Acta Crystallogr D Struct Biol / 年: 2018 ジャーナル: Acta Crystallogr D Struct Biol / 年: 2018タイトル: Rea-space refinement in PHENIX for cryo-EM and crystallography. 著者: Afonine PV / Poon BK / Read RJ / Sobolev OV / Terwilliger TC / Urzhumtsev A / Adams PD #3:  ジャーナル: Nat Methods / 年: 2017 ジャーナル: Nat Methods / 年: 2017タイトル: cryoSPARC: algorithms for rapid unsupervised cryo-EM structure determination. 著者: Punjani A / Rubinstein JL / Fleet DJ / Brubaker MA | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_14740.map.gz emd_14740.map.gz | 36.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-14740-v30.xml emd-14740-v30.xml emd-14740.xml emd-14740.xml | 23.5 KB 23.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_14740_fsc.xml emd_14740_fsc.xml | 7.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_14740.png emd_14740.png | 29.6 KB | ||
| マスクデータ |  emd_14740_msk_1.map emd_14740_msk_1.map | 38.4 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-14740.cif.gz emd-14740.cif.gz | 6.2 KB | ||
| その他 |  emd_14740_additional_1.map.gz emd_14740_additional_1.map.gz emd_14740_half_map_1.map.gz emd_14740_half_map_1.map.gz emd_14740_half_map_2.map.gz emd_14740_half_map_2.map.gz | 19.2 MB 35.7 MB 35.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-14740 http://ftp.pdbj.org/pub/emdb/structures/EMD-14740 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14740 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14740 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_14740_validation.pdf.gz emd_14740_validation.pdf.gz | 850.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_14740_full_validation.pdf.gz emd_14740_full_validation.pdf.gz | 850.5 KB | 表示 | |
| XML形式データ |  emd_14740_validation.xml.gz emd_14740_validation.xml.gz | 15.1 KB | 表示 | |
| CIF形式データ |  emd_14740_validation.cif.gz emd_14740_validation.cif.gz | 18.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14740 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14740 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14740 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14740 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_14740.map.gz / 形式: CCP4 / 大きさ: 38.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_14740.map.gz / 形式: CCP4 / 大きさ: 38.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Map sharpened with b-factor of 160 | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.29 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_14740_msk_1.map emd_14740_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Unsharpened map
| ファイル | emd_14740_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map B
| ファイル | emd_14740_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map A
| ファイル | emd_14740_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Ligand bound state of a brocolli-pepper aptamer FRET tile
| 全体 | 名称: Ligand bound state of a brocolli-pepper aptamer FRET tile |
|---|---|
| 要素 |
|
-超分子 #1: Ligand bound state of a brocolli-pepper aptamer FRET tile
| 超分子 | 名称: Ligand bound state of a brocolli-pepper aptamer FRET tile タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 120 KDa |
-分子 #1: brocolli-pepper aptamer
| 分子 | 名称: brocolli-pepper aptamer / タイプ: rna / ID: 1 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 120.700953 KDa |
| 配列 | 文字列: GGAUACGUCU ACGCUCAGUG ACGGACUCUC UUCGGAGAGU CUGACAUCCG AACCAUACAC GGAUGUGCCU CGCCGAACAG UCUACGGCG AGCUUAAGCG CUGGGGACGC CCAACGCAUC ACAAAGACUG AGUGAUGAAC CAGAAGUAUG GACUGGUUGC G UUGGUGGA ...文字列: GGAUACGUCU ACGCUCAGUG ACGGACUCUC UUCGGAGAGU CUGACAUCCG AACCAUACAC GGAUGUGCCU CGCCGAACAG UCUACGGCG AGCUUAAGCG CUGGGGACGC CCAACGCAUC ACAAAGACUG AGUGAUGAAC CAGAAGUAUG GACUGGUUGC G UUGGUGGA GACGGUCGGG UCCAGUUCGC UGUCGAGUAG AGUGUGGGCU CCAUCGACGC CGCUUUAAGG UCCCCAAUCG UG GCGUGUC GGCCUGCUUC GGCAGGCACU GGCGCCGGGA CCUUGAAGAG AUGAGAUUUC GAUCUCAUCU UUGGGUGUCU CUG GUGCUU GAGGGCCCUG UGUUCGCACA GGGCCGCUCA CUGGGUGUGG ACGUAUCC |
-分子 #2: 4-[(~{Z})-1-cyano-2-[5-[2-hydroxyethyl(methyl)amino]thieno[3,2-b]...
| 分子 | 名称: 4-[(~{Z})-1-cyano-2-[5-[2-hydroxyethyl(methyl)amino]thieno[3,2-b]thiophen-2-yl]ethenyl]benzenecarbonitrile タイプ: ligand / ID: 2 / コピー数: 1 / 式: J93 |
|---|---|
| 分子量 | 理論値: 365.472 Da |
| Chemical component information | 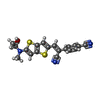 ChemComp-J93: |
-分子 #3: 4-(3,5-difluoro-4-hydroxybenzyl)-1,2-dimethyl-1H-imidazol-5-ol
| 分子 | 名称: 4-(3,5-difluoro-4-hydroxybenzyl)-1,2-dimethyl-1H-imidazol-5-ol タイプ: ligand / ID: 3 / コピー数: 1 / 式: 1TU |
|---|---|
| 分子量 | 理論値: 254.233 Da |
| Chemical component information | 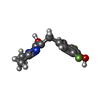 ChemComp-1TU: |
-分子 #4: POTASSIUM ION
| 分子 | 名称: POTASSIUM ION / タイプ: ligand / ID: 4 / コピー数: 1 / 式: K |
|---|---|
| 分子量 | 理論値: 39.098 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2.5 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 詳細: 40mM HEPES pH 7.5, 5mM MgCl2, 50mM KCl. Filtered through 0.22 um filter. |
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 45 sec. / 前処理 - 雰囲気: OTHER / 前処理 - 気圧: 0.00045000000000000004 kPa / 詳細: 15mA of current. |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 288 K / 装置: LEICA EM GP 詳細: 3 uL sample, blotted onto double layer of whatman filter paper for 6 seconds.. |
| 詳細 | Sample was purified by size exclusion chromatography. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 5354 / 平均電子線量: 60.0 e/Å2 詳細: Collected with a calibrated pixel size of 0.647 Angstrom |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm 最小 デフォーカス(公称値): 0.7000000000000001 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー







 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)