+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1294 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Three-dimensional structure of the native spliceosome by cryo-electron microscopy. | |||||||||
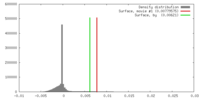
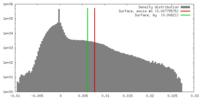
 マップデータ マップデータ | Biological isosurface is at density value 0.007 | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 22.0 Å | |||||||||
 データ登録者 データ登録者 | Azubel M / Wolf SG / Sperling J / Sperling R | |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2004 ジャーナル: Mol Cell / 年: 2004タイトル: Three-dimensional structure of the native spliceosome by cryo-electron microscopy. 著者: Maia Azubel / Sharon G Wolf / Joseph Sperling / Ruth Sperling /  要旨: Splicing of pre-mRNA occurs in a multicomponent macromolecular machine--the spliceosome. The spliceosome can be assembled in vitro by a stepwise assembly of a number of snRNPs and additional proteins ...Splicing of pre-mRNA occurs in a multicomponent macromolecular machine--the spliceosome. The spliceosome can be assembled in vitro by a stepwise assembly of a number of snRNPs and additional proteins on exogenously added pre-mRNA. In contrast, splicing in vivo occurs in preformed particles where endogenous pre-mRNAs are packaged with all five spliceosomal U snRNPs (penta-snRNP) together with other splicing factors. Here we present a three-dimensional image reconstruction by cryo-electron microscopy of native spliceosomes, derived from cell nuclei, at a resolution of 20 angstroms. The structure revealed an elongated globular particle made up of two distinct subunits connected to each other leaving a tunnel in between. We show here that the larger subunit is a suitable candidate to accommodate the penta-snRNP, and that the tunnel could accommodate the pre-mRNA component of the spliceosome. The features this structure reveals provide new insight into the global architecture of the native splicing machine. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1294.map.gz emd_1294.map.gz | 3.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1294-v30.xml emd-1294-v30.xml emd-1294.xml emd-1294.xml | 9 KB 9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  1294.gif 1294.gif | 31.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1294 http://ftp.pdbj.org/pub/emdb/structures/EMD-1294 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1294 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1294 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1294.map.gz / 形式: CCP4 / 大きさ: 3.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1294.map.gz / 形式: CCP4 / 大きさ: 3.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Biological isosurface is at density value 0.007 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 5.25 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : native spliceosome
| 全体 | 名称: native spliceosome |
|---|---|
| 要素 |
|
-超分子 #1000: native spliceosome
| 超分子 | 名称: native spliceosome / タイプ: sample / ID: 1000 / 集合状態: monomeric / Number unique components: 1 |
|---|---|
| 分子量 | 実験値: 4.8 MDa / 手法: STEM mass measurement |
-超分子 #1: native spliceosome
| 超分子 | 名称: native spliceosome / タイプ: organelle_or_cellular_component / ID: 1 / 組換発現: No |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) / 別称: human / 細胞: HeLa / Organelle: Nucleus / 細胞中の位置: nucleus Homo sapiens (ヒト) / 別称: human / 細胞: HeLa / Organelle: Nucleus / 細胞中の位置: nucleus |
| 分子量 | 理論値: 4.8 MDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| グリッド | 詳細: lacey (SPI) or Quantifoil grids |
|---|---|
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / 装置: HOMEMADE PLUNGER / 詳細: Vitrification instrument: I. Talmon plunger 手法: the samples were incubated in Teflon wells under charged lipid monolayers for 20 min., picked up on grids, rinsed, blotted and plunged into liquid ethane. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F20 |
|---|---|
| 温度 | 最低: 95 K / 最高: 100 K / 平均: 97 K |
| アライメント法 | Legacy - 非点収差: correction at 100,000 to 250,000 times mag |
| 詳細 | magnification with calibrated camera postmag factor was 93,620 |
| 撮影 | カテゴリ: CCD / フィルム・検出器のモデル: GENERIC TVIPS / デジタル化 - サンプリング間隔: 24 µm / 平均電子線量: 10 e/Å2 / 詳細: TVIPS Biocam 1k X 1k CCD camera / ビット/ピクセル: 16 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2 mm / 最大 デフォーカス(公称値): 4.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 62000 |
| 試料ステージ | 試料ホルダー: side entry liquid nitrogen-cooled cryo specimen holder 試料ホルダーモデル: GATAN LIQUID NITROGEN |
| 実験機器 |  モデル: Tecnai F20 / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | 詳細: phase correction, each particle |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 22.0 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: Spider / 詳細: see Supplemental material at Molecular Cell website / 使用した粒子像数: 7500 |
| 最終 角度割当 | 詳細: see Supplemental material at Molecular Cell website. |
 ムービー
ムービー コントローラー
コントローラー










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)