+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1065 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Visualization of release factor 3 on the ribosome during termination of protein synthesis. | |||||||||
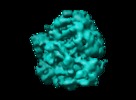
 マップデータ マップデータ | Cryo-EM map of the E.coli 70S/RF3 complex, state 2 | |||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 | Peptide chain release factor 3 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / ネガティブ染色法 / 解像度: 17.5 Å | |||||||||
 データ登録者 データ登録者 | Klaholz BP | |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2004 ジャーナル: Nature / 年: 2004タイトル: Visualization of release factor 3 on the ribosome during termination of protein synthesis. 著者: Bruno P Klaholz / Alexander G Myasnikov / Marin Van Heel /  要旨: Termination of protein synthesis by the ribosome requires two release factor (RF) classes. The class II RF3 is a GTPase that removes class I RFs (RF1 or RF2) from the ribosome after release of the ...Termination of protein synthesis by the ribosome requires two release factor (RF) classes. The class II RF3 is a GTPase that removes class I RFs (RF1 or RF2) from the ribosome after release of the nascent polypeptide. RF3 in the GDP state binds to the ribosomal class I RF complex, followed by an exchange of GDP for GTP and release of the class I RF. As GTP hydrolysis triggers release of RF3 (ref. 4), we trapped RF3 on Escherichia coli ribosomes using a nonhydrolysable GTP analogue. Here we show by cryo-electron microscopy that the complex can adopt two different conformational states. In 'state 1', RF3 is pre-bound to the ribosome, whereas in 'state 2' RF3 contacts the ribosome GTPase centre. The transfer RNA molecule translocates from the peptidyl site in state 1 to the exit site in state 2. This translocation is associated with a large conformational rearrangement of the ribosome. Because state 1 seems able to accommodate simultaneously both RF3 and RF2, whose position is known from previous studies, we can infer the release mechanism of class I RFs. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1065.map.gz emd_1065.map.gz | 2.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1065-v30.xml emd-1065-v30.xml emd-1065.xml emd-1065.xml | 10.8 KB 10.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  1065.gif 1065.gif | 18.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1065 http://ftp.pdbj.org/pub/emdb/structures/EMD-1065 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1065 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1065 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_1065_validation.pdf.gz emd_1065_validation.pdf.gz | 234.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_1065_full_validation.pdf.gz emd_1065_full_validation.pdf.gz | 234 KB | 表示 | |
| XML形式データ |  emd_1065_validation.xml.gz emd_1065_validation.xml.gz | 5.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1065 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1065 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1065 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1065 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1065.map.gz / 形式: CCP4 / 大きさ: 6.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1065.map.gz / 形式: CCP4 / 大きさ: 6.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM map of the E.coli 70S/RF3 complex, state 2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.419 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : 70S - RF3 complex E.coli
| 全体 | 名称: 70S - RF3 complex E.coli |
|---|---|
| 要素 |
|
-超分子 #1000: 70S - RF3 complex E.coli
| 超分子 | 名称: 70S - RF3 complex E.coli / タイプ: sample / ID: 1000 詳細: two functional states within a single sample of homogeneous composition, separated by image processing techniques, state 2 集合状態: monomer / Number unique components: 4 |
|---|---|
| 分子量 | 理論値: 2.5 MDa |
-超分子 #1: 70S
| 超分子 | 名称: 70S / タイプ: complex / ID: 1 / Name.synonym: 70S / Ribosome-details: ribosome-prokaryote: ALL |
|---|
-分子 #1: messenger RNA
| 分子 | 名称: messenger RNA / タイプ: rna / ID: 1 / Name.synonym: mRNA / 分類: OTHER / Structure: SINGLE STRANDED / Synthetic?: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 配列 | 文字列: GGGCCCUUGU UAACAAUUAA GGAGGUAUAC UAUGUUUACG AUUUAAUUGC AGAAAAAAAA AAAAAAAAAA AAA |
-分子 #2: isoleucin transfer RNA
| 分子 | 名称: isoleucin transfer RNA / タイプ: rna / ID: 2 / Name.synonym: Ile-tRNA / 分類: TRANSFER / Structure: SINGLE STRANDED / Synthetic?: No |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #3: release factor 3
| 分子 | 名称: release factor 3 / タイプ: protein_or_peptide / ID: 3 / Name.synonym: RF3 / 詳細: PrfC gene / 集合状態: monomer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種: Escherichia coli MKH13 / 組換プラスミド: pOSEX3 |
| 配列 | InterPro: Peptide chain release factor 3 |
-実験情報
-構造解析
| 手法 | ネガティブ染色法, クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.15 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 / 詳細: polymix buffer |
| 染色 | タイプ: NEGATIVE / 詳細: no staining, cryo-EM with holey carbon grids |
| グリッド | 詳細: 300 mesh Cu/Rh |
| 凍結 | 凍結剤: ETHANE / 装置: HOMEMADE PLUNGER / 詳細: Vitrification instrument: home-made cryo-plunger / 手法: Blot for 2 seconds before plunging |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI/PHILIPS CM200FEG |
|---|---|
| アライメント法 | Legacy - 非点収差: lens astigmatism was corrected at 60,000 times magnification |
| 日付 | 2001年12月19日 |
| 撮影 | カテゴリ: FILM / フィルム・検出器のモデル: KODAK SO-163 FILM / デジタル化 - スキャナー: OTHER / デジタル化 - サンプリング間隔: 3 µm / 実像数: 44 / 平均電子線量: 10 e/Å2 / 詳細: IMAGE SCIENCE PATCHWORK DENSITOMETER / ビット/ピクセル: 12 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 48000 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.1 mm / 最大 デフォーカス(公称値): 2.8 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 50000 |
| 試料ステージ | 試料ホルダー: Side entry liquid nitrogen-cooled cryo specimen holder 試料ホルダーモデル: GATAN LIQUID NITROGEN |
- 画像解析
画像解析
| CTF補正 | 詳細: individual particles |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 17.5 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: IMAGIC / 詳細: exact filtered back-projection / 使用した粒子像数: 10011 |
| 最終 角度割当 | 詳細: beta gamma |
| 最終 2次元分類 | クラス数: 246 |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





















