+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9fp5 | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Coxsackievirus A9 bound with CL213. | ||||||||||||
 要素 要素 | (Capsid protein ...) x 4 | ||||||||||||
 キーワード キーワード | VIRUS / Antiviral / capsid stabilizer / hydrophobic pocket / cryoEM | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / nucleoside-triphosphate phosphatase / channel activity / monoatomic ion transmembrane transport ...symbiont-mediated suppression of host cytoplasmic pattern recognition receptor signaling pathway via inhibition of RIG-I activity / picornain 2A / symbiont-mediated suppression of host mRNA export from nucleus / symbiont genome entry into host cell via pore formation in plasma membrane / picornain 3C / T=pseudo3 icosahedral viral capsid / host cell cytoplasmic vesicle membrane / nucleoside-triphosphate phosphatase / channel activity / monoatomic ion transmembrane transport / DNA replication / RNA helicase activity / endocytosis involved in viral entry into host cell / symbiont-mediated activation of host autophagy / RNA-directed RNA polymerase / cysteine-type endopeptidase activity / viral RNA genome replication / RNA-directed RNA polymerase activity / DNA-templated transcription / virion attachment to host cell / host cell nucleus / structural molecule activity / ATP hydrolysis activity / proteolysis / RNA binding / zinc ion binding / ATP binding / membrane 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Coxsackievirus A9 (コクサッキーウイルス) Coxsackievirus A9 (コクサッキーウイルス) | ||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.5 Å | ||||||||||||
 データ登録者 データ登録者 | Plavec, Z. / Butcher, S.J. / Mitchell, C. / Buckner, C. | ||||||||||||
| 資金援助 |  フィンランド, 3件 フィンランド, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: J Med Chem / 年: 2024 ジャーナル: J Med Chem / 年: 2024タイトル: SAR Analysis of Novel Coxsackie virus A9 Capsid Binders. 著者: Chiara Tammaro / Zlatka Plavec / Laura Myllymäki / Cristopher Mitchell / Sara Consalvi / Mariangela Biava / Alessia Ciogli / Aušra Domanska / Valtteri Leppilampi / Cienna Buckner / Simone ...著者: Chiara Tammaro / Zlatka Plavec / Laura Myllymäki / Cristopher Mitchell / Sara Consalvi / Mariangela Biava / Alessia Ciogli / Aušra Domanska / Valtteri Leppilampi / Cienna Buckner / Simone Manetto / Pietro Sciò / Antonio Coluccia / Mira Laajala / Giulio M Dondio / Chiara Bigogno / Varpu Marjomäki / Sarah J Butcher / Giovanna Poce /   要旨: Enterovirus infections are common in humans, yet there are no approved antiviral treatments. In this study we concentrated on inhibition of one of the (EV-B), namely Coxsackievirus A9 (CVA9), using ...Enterovirus infections are common in humans, yet there are no approved antiviral treatments. In this study we concentrated on inhibition of one of the (EV-B), namely Coxsackievirus A9 (CVA9), using a combination of medicinal chemistry, virus inhibition assays, structure determination from cryogenic electron microscopy and molecular modeling, to determine the structure activity relationships for a promising class of novel -phenylbenzylamines. Of the new 29 compounds synthesized, 10 had half maximal effective concentration (EC) values between 0.64-10.46 μM, and of these, 7 had 50% cytotoxicity concentration (CC) values higher than 200 μM. In addition, this new series of compounds showed promising physicochemical properties and act through capsid stabilization, preventing capsid expansion and subsequent release of the genome. #1: ジャーナル: Protein Sci / 年: 2021 タイトル: UCSF ChimeraX: Structure visualization for researchers, educators, and developers. 著者: Eric F Pettersen / Thomas D Goddard / Conrad C Huang / Elaine C Meng / Gregory S Couch / Tristan I Croll / John H Morris / Thomas E Ferrin /   要旨: UCSF ChimeraX is the next-generation interactive visualization program from the Resource for Biocomputing, Visualization, and Informatics (RBVI), following UCSF Chimera. ChimeraX brings (a) ...UCSF ChimeraX is the next-generation interactive visualization program from the Resource for Biocomputing, Visualization, and Informatics (RBVI), following UCSF Chimera. ChimeraX brings (a) significant performance and graphics enhancements; (b) new implementations of Chimera's most highly used tools, many with further improvements; (c) several entirely new analysis features; (d) support for new areas such as virtual reality, light-sheet microscopy, and medical imaging data; (e) major ease-of-use advances, including toolbars with icons to perform actions with a single click, basic "undo" capabilities, and more logical and consistent commands; and (f) an app store for researchers to contribute new tools. ChimeraX includes full user documentation and is free for noncommercial use, with downloads available for Windows, Linux, and macOS from https://www.rbvi.ucsf.edu/chimerax. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9fp5.cif.gz 9fp5.cif.gz | 279.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9fp5.ent.gz pdb9fp5.ent.gz | 227.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  9fp5.json.gz 9fp5.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/fp/9fp5 https://data.pdbj.org/pub/pdb/validation_reports/fp/9fp5 ftp://data.pdbj.org/pub/pdb/validation_reports/fp/9fp5 ftp://data.pdbj.org/pub/pdb/validation_reports/fp/9fp5 | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  50636MC  8s7jC  9exiC  9fa9C  9fczC  9fgnC  9fo2C  9fo5C C: 同じ文献を引用 ( M: このデータのモデリングに利用したマップデータ |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 | x 60
|
- 要素
要素
-Capsid protein ... , 4種, 4分子 ABCD
| #1: タンパク質 | 分子量: 33869.020 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)  Coxsackievirus A9 (コクサッキーウイルス) Coxsackievirus A9 (コクサッキーウイルス)細胞株: GMK / 株: Griggs / 組織: kidney / 参照: UniProt: P21404 |
|---|---|
| #2: タンパク質 | 分子量: 28885.518 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)  Coxsackievirus A9 (コクサッキーウイルス) Coxsackievirus A9 (コクサッキーウイルス)細胞株: GMK / 株: Griggs / 組織: kidney / 参照: UniProt: P21404 |
| #3: タンパク質 | 分子量: 26335.072 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)  Coxsackievirus A9 (コクサッキーウイルス) Coxsackievirus A9 (コクサッキーウイルス)細胞株: GMK / 株: Griggs / 組織: kidney / 参照: UniProt: P21404 |
| #4: タンパク質 | 分子量: 7352.039 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)  Coxsackievirus A9 (コクサッキーウイルス) Coxsackievirus A9 (コクサッキーウイルス)細胞株: GMK / 株: Griggs / 組織: kidney / 参照: UniProt: P21404 |
-非ポリマー , 2種, 2分子 
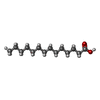

| #5: 化合物 | ChemComp-PLM / |
|---|---|
| #6: 化合物 | ChemComp-MYR / |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | N |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Human coxsackievirus A9 (strain Griggs) / タイプ: VIRUS 詳細: Coxsackievirus A9 was propagated on green monkey kidney cells and purified on a sucrose gradient. Entity ID: #1-#4 / 由来: NATURAL |
|---|---|
| 分子量 | 値: 8 MDa / 実験値: NO |
| 由来(天然) | 生物種:  Human coxsackievirus A9 (strain Griggs) (コクサッキーウイルス) Human coxsackievirus A9 (strain Griggs) (コクサッキーウイルス)株: Griggs |
| ウイルスについての詳細 | 中空か: NO / エンベロープを持つか: NO / 単離: STRAIN / タイプ: VIRION |
| 天然宿主 | 生物種: Homo sapiens |
| ウイルス殻 | 名称: icosahedral capsid / 直径: 300 nm / 三角数 (T数): 1 |
| 緩衝液 | pH: 7.2 |
| 試料 | 濃度: 0.07 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES 詳細: CL213 stock solution in DMSO was diluted in PBS containing 2mM MgCl2 for final concentration of 1 mg/ml. 10 ul of purified CVA9 with the concentration of 0.7 mg/ml was mixed with 4 ul of ...詳細: CL213 stock solution in DMSO was diluted in PBS containing 2mM MgCl2 for final concentration of 1 mg/ml. 10 ul of purified CVA9 with the concentration of 0.7 mg/ml was mixed with 4 ul of CL213 diluted in PBS containing 2mM MgCl2 to a final concentration of CL213 of 0.28 mg/ml. The virus-compound mixture was incubated for 1 hour in 37 C. The final molar concentration of the virus was approximately 71 nM and CL213 concentration was approximately 7.8 mM. |
| 試料支持 | グリッドの材料: COPPER / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: Quantifoil R1.2/1.3 |
| 急速凍結 | 装置: LEICA EM GP / 凍結剤: ETHANE / 湿度: 80 % / 凍結前の試料温度: 295 K 詳細: Sample was incubated for 15 s on the grid before blotted from the front for 1.5 s. |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2000 nm / 最小 デフォーカス(公称値): 400 nm |
| 撮影 | 電子線照射量: 40 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 216957 | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: I (正20面体型対称) | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.5 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 90678 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | B value: 70 | ||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 8AT5 Accession code: 8AT5 / Source name: PDB / タイプ: experimental model |
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj












