+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8wrz | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cry-EM structure of cannabinoid receptor-arrestin 2 complex | ||||||||||||||||||
 要素 要素 |
| ||||||||||||||||||
 キーワード キーワード | MEMBRANE PROTEIN / complex / GPCR | ||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報renal water retention / Defective AVP does not bind AVPR2 and causes neurohypophyseal diabetes insipidus (NDI) / Vasopressin-like receptors / cannabinoid signaling pathway / regulation of penile erection / retrograde trans-synaptic signaling by endocannabinoid / regulation of systemic arterial blood pressure by vasopressin / vasopressin receptor activity / cannabinoid receptor activity / angiotensin receptor binding ...renal water retention / Defective AVP does not bind AVPR2 and causes neurohypophyseal diabetes insipidus (NDI) / Vasopressin-like receptors / cannabinoid signaling pathway / regulation of penile erection / retrograde trans-synaptic signaling by endocannabinoid / regulation of systemic arterial blood pressure by vasopressin / vasopressin receptor activity / cannabinoid receptor activity / angiotensin receptor binding / negative regulation of mast cell activation / trans-synaptic signaling by endocannabinoid, modulating synaptic transmission / negative regulation of fatty acid beta-oxidation / negative regulation of dopamine secretion / positive regulation of acute inflammatory response to antigenic stimulus / regulation of feeding behavior / negative regulation of serotonin secretion / Activation of SMO / hemostasis / regulation of presynaptic cytosolic calcium ion concentration / telencephalon development / negative regulation of action potential / positive regulation of systemic arterial blood pressure / negative regulation of interleukin-8 production / Class A/1 (Rhodopsin-like receptors) / positive regulation of blood pressure / positive regulation of fever generation / regulation of metabolic process / arrestin family protein binding / G protein-coupled receptor internalization / axonal fasciculation / enzyme inhibitor activity / positive regulation of intracellular signal transduction / Lysosome Vesicle Biogenesis / regulation of synaptic transmission, GABAergic / positive regulation of Rho protein signal transduction / Golgi Associated Vesicle Biogenesis / negative regulation of NF-kappaB transcription factor activity / stress fiber assembly / negative regulation of Notch signaling pathway / pseudopodium / regulation of insulin secretion / negative regulation of interleukin-6 production / positive regulation of receptor internalization / G protein-coupled receptor signaling pathway, coupled to cyclic nucleotide second messenger / endocytic vesicle / GABA-ergic synapse / maternal process involved in female pregnancy / clathrin-coated pit / positive regulation of vasoconstriction / regulation of synaptic transmission, glutamatergic / cellular response to hormone stimulus / negative regulation of protein ubiquitination / activation of adenylate cyclase activity / visual perception / negative regulation of blood pressure / Activated NOTCH1 Transmits Signal to the Nucleus / response to nutrient / GTPase activator activity / response to cocaine / response to cytokine / G protein-coupled receptor binding / G protein-coupled receptor activity / electron transport chain / peptide binding / insulin-like growth factor receptor binding / Signaling by high-kinase activity BRAF mutants / response to nicotine / clathrin-coated endocytic vesicle membrane / MAP2K and MAPK activation / cytoplasmic vesicle membrane / adenylate cyclase-modulating G protein-coupled receptor signaling pathway / adenylate cyclase-activating G protein-coupled receptor signaling pathway / memory / positive regulation of neuron projection development / Vasopressin regulates renal water homeostasis via Aquaporins / Signaling by RAF1 mutants / Signaling by moderate kinase activity BRAF mutants / Paradoxical activation of RAF signaling by kinase inactive BRAF / Signaling downstream of RAS mutants / Signaling by BRAF and RAF1 fusions / protein transport / actin cytoskeleton / Cargo recognition for clathrin-mediated endocytosis / Thrombin signalling through proteinase activated receptors (PARs) / glucose homeostasis / Clathrin-mediated endocytosis / presynaptic membrane / growth cone / G alpha (i) signalling events / cytoplasmic vesicle / ubiquitin-dependent protein catabolic process / G alpha (s) signalling events / spermatogenesis / proteasome-mediated ubiquitin-dependent protein catabolic process / response to ethanol / mitochondrial outer membrane / response to lipopolysaccharide / periplasmic space / transcription coactivator activity 類似検索 - 分子機能 | ||||||||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト)Phage display vector pTDisp (その他)  | ||||||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.6 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Wang, Y.X. / Wang, T. / Wu, L.J. / Hua, T. / Liu, Z.J. | ||||||||||||||||||
| 資金援助 |  中国, 5件 中国, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Protein Cell / 年: 2024 ジャーナル: Protein Cell / 年: 2024タイトル: Cryo-EM structure of cannabinoid receptor CB1-β-arrestin complex. 著者: Yuxia Wang / Lijie Wu / Tian Wang / Junlin Liu / Fei Li / Longquan Jiang / Zhongbo Fan / Yanan Yu / Na Chen / Qianqian Sun / Qiwen Tan / Tian Hua / Zhi-Jie Liu /  | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8wrz.cif.gz 8wrz.cif.gz | 175.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8wrz.ent.gz pdb8wrz.ent.gz | 131.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8wrz.json.gz 8wrz.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8wrz_validation.pdf.gz 8wrz_validation.pdf.gz | 1.1 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8wrz_full_validation.pdf.gz 8wrz_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  8wrz_validation.xml.gz 8wrz_validation.xml.gz | 38.6 KB | 表示 | |
| CIF形式データ |  8wrz_validation.cif.gz 8wrz_validation.cif.gz | 55.1 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/wr/8wrz https://data.pdbj.org/pub/pdb/validation_reports/wr/8wrz ftp://data.pdbj.org/pub/pdb/validation_reports/wr/8wrz ftp://data.pdbj.org/pub/pdb/validation_reports/wr/8wrz | HTTPS FTP |
-関連構造データ
| 関連構造データ |  37795MC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 44271.508 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: ARRB1 Homo sapiens (ヒト) / 遺伝子: ARRB1発現宿主:  参照: UniProt: P49407 |
|---|---|
| #2: 抗体 | 分子量: 28693.922 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現) Phage display vector pTDisp (その他) 発現宿主:  |
| #3: タンパク質 | 分子量: 53577.543 Da / 分子数: 1 / Mutation: M29W, H124I, T210I, E273K, T283V, R340E / 由来タイプ: 組換発現 詳細: The chimera of Cytochrome b-562, linker, and Cannabinoid receptor 1 由来: (組換発現)   Homo sapiens (ヒト) Homo sapiens (ヒト)遺伝子: cybC, CNR1 / 発現宿主:  Homo sapiens (ヒト) / 株 (発現宿主): CNR1 / 参照: UniProt: P0ABE7, UniProt: P21554 Homo sapiens (ヒト) / 株 (発現宿主): CNR1 / 参照: UniProt: P0ABE7, UniProt: P21554 |
| #4: タンパク質・ペプチド | 分子量: 2920.651 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: AVPR2 Homo sapiens (ヒト) / 遺伝子: AVPR2発現宿主:  株 (発現宿主): CNR / 参照: UniProt: P30518 |
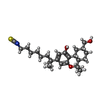
| #5: 化合物 | ChemComp-8D0 / ( |
| 研究の焦点であるリガンドがあるか | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Cry-EM structure of cannabinoid receptor-arrestin 2 complex タイプ: COMPLEX / Entity ID: #1-#4 / 由来: MULTIPLE SOURCES |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 由来(組換発現) | 生物種:  |
| 緩衝液 | pH: 7.5 |
| 試料 | 濃度: 1.5 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 277 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2000 nm / 最小 デフォーカス(公称値): 1000 nm |
| 撮影 | 電子線照射量: 60 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 実像数: 25847 |
- 解析
解析
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 3次元再構成 | 解像度: 3.6 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 130058 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: RIGID BODY FIT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj