+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8syi | ||||||
|---|---|---|---|---|---|---|---|
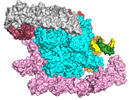
| タイトル | Cyanobacterial RNAP-EC | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | TRANSCRIPTION / Transcription regulation RNAP NusG cryo-EM | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報transcription elongation-coupled chromatin remodeling / DNA-directed RNA polymerase complex / regulation of DNA-templated transcription elongation / transcription antitermination / DNA-templated transcription termination / ribonucleoside binding / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / protein dimerization activity / DNA-templated transcription ...transcription elongation-coupled chromatin remodeling / DNA-directed RNA polymerase complex / regulation of DNA-templated transcription elongation / transcription antitermination / DNA-templated transcription termination / ribonucleoside binding / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / protein dimerization activity / DNA-templated transcription / magnesium ion binding / DNA binding / zinc ion binding / cytoplasm / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア)synthetic construct (人工物) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.94 Å | ||||||
 データ登録者 データ登録者 | Qayyum, M.Z. / Imashimizu, M. / Leanca, M. / Vishwakarma, R.K. / Bradley Riaz, A. / Yuzenkova, Y. / Murakami, K.S. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2024 ジャーナル: Proc Natl Acad Sci U S A / 年: 2024タイトル: Structure and function of the Si3 insertion integrated into the trigger loop/helix of cyanobacterial RNA polymerase. 著者: M Zuhaib Qayyum / Masahiko Imashimizu / Miron Leanca / Rishi K Vishwakarma / Amber Riaz-Bradley / Yulia Yuzenkova / Katsuhiko S Murakami /    要旨: Cyanobacteria and evolutionarily related chloroplasts of algae and plants possess unique RNA polymerases (RNAPs) with characteristics that distinguish them from canonical bacterial RNAPs. The largest ...Cyanobacteria and evolutionarily related chloroplasts of algae and plants possess unique RNA polymerases (RNAPs) with characteristics that distinguish them from canonical bacterial RNAPs. The largest subunit of cyanobacterial RNAP (cyRNAP) is divided into two polypeptides, β'1 and β'2, and contains the largest known lineage-specific insertion domain, Si3, located in the middle of the trigger loop and spanning approximately half of the β'2 subunit. In this study, we present the X-ray crystal structure of Si3 and the cryo-EM structures of the cyRNAP transcription elongation complex plus the NusG factor with and without incoming nucleoside triphosphate (iNTP) bound at the active site. Si3 has a well-ordered and elongated shape that exceeds the length of the main body of cyRNAP, fits into cavities of cyRNAP in the absence of iNTP bound at the active site and shields the binding site of secondary channel-binding proteins such as Gre and DksA. A small transition from the trigger loop to the trigger helix upon iNTP binding results in a large swing motion of Si3; however, this transition does not affect the catalytic activity of cyRNAP due to its minimal contact with cyRNAP, NusG, or DNA. This study provides a structural framework for understanding the evolutionary significance of these features unique to cyRNAP and chloroplast RNAP and may provide insights into the molecular mechanism of transcription in specific environment of photosynthetic organisms and organelle. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8syi.cif.gz 8syi.cif.gz | 915.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8syi.ent.gz pdb8syi.ent.gz | 593.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8syi.json.gz 8syi.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8syi_validation.pdf.gz 8syi_validation.pdf.gz | 1.3 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8syi_full_validation.pdf.gz 8syi_full_validation.pdf.gz | 1.3 MB | 表示 | |
| XML形式データ |  8syi_validation.xml.gz 8syi_validation.xml.gz | 96.9 KB | 表示 | |
| CIF形式データ |  8syi_validation.cif.gz 8syi_validation.cif.gz | 153.4 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/sy/8syi https://data.pdbj.org/pub/pdb/validation_reports/sy/8syi ftp://data.pdbj.org/pub/pdb/validation_reports/sy/8syi ftp://data.pdbj.org/pub/pdb/validation_reports/sy/8syi | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-DNA-directed RNA polymerase subunit ... , 5種, 6分子 ABCDZE
| #1: タンパク質 | 分子量: 33814.891 Da / 分子数: 2 / 由来タイプ: 組換発現 由来: (組換発現)  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア)遺伝子: rpoA, Synpcc7942_2209 / 発現宿主:  #2: タンパク質 | | 分子量: 123428.547 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア)遺伝子: rpoB, Synpcc7942_1522 / 発現宿主:  #3: タンパク質 | | 分子量: 71054.367 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア)遺伝子: rpoC1, Synpcc7942_1523 / 発現宿主:  #4: タンパク質 | | 分子量: 144006.031 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア)遺伝子: rpoC2, Synpcc7942_1524 / 発現宿主:  #5: タンパク質 | | 分子量: 8787.966 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア)遺伝子: rpoZ, Synpcc7942_1710 / 発現宿主:  |
|---|
-DNA鎖 , 2種, 2分子 NT
| #7: DNA鎖 | 分子量: 12202.790 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
|---|---|
| #9: DNA鎖 | 分子量: 12251.828 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
-タンパク質 / RNA鎖 , 2種, 2分子 GR
| #6: タンパク質 | 分子量: 23117.375 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア)遺伝子: nusG, Synpcc7942_0635 / 発現宿主:  |
|---|---|
| #8: RNA鎖 | 分子量: 6509.968 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
-非ポリマー , 2種, 3分子 


| #10: 化合物 | ChemComp-MG / |
|---|---|
| #11: 化合物 |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: CyRNAP-Elongation Complex / タイプ: COMPLEX / Entity ID: #1-#9 / 由来: RECOMBINANT |
|---|---|
| 由来(天然) | 生物種:  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア) |
| 由来(組換発現) | 生物種:  |
| 緩衝液 | pH: 8 / 詳細: 40mM Tris-HCl 200mM KCl 1mM EDTA 1mM DTT |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: OTHER / 最大 デフォーカス(公称値): 2500 nm / 最小 デフォーカス(公称値): 750 nm |
| 撮影 | 電子線照射量: 45 e/Å2 フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) |
- 解析
解析
| CTF補正 | タイプ: PHASE FLIPPING ONLY | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 2.94 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 176309 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 精密化 | 交差検証法: NONE 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2 | ||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 78.07 Å2 | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー






 PDBj
PDBj

































































