+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8imy | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of GPI-T (inactive mutant) with GPI and proULBP2, a proprotein substrate | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | MEMBRANE PROTEIN / cryo-EM / glycosylphosphatidylinositol / GPI / GPI anchored protein / GPI-AP / membrane protein complex / proprotein | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報GPI-anchor transamidase activity / attachment of GPI anchor to protein / GPI-anchor transamidase complex / GPI anchor biosynthetic process / protein retention in ER lumen / Attachment of GPI anchor to uPAR / natural killer cell lectin-like receptor binding / Post-translational modification: synthesis of GPI-anchored proteins / 加水分解酵素 / natural killer cell mediated cytotoxicity ...GPI-anchor transamidase activity / attachment of GPI anchor to protein / GPI-anchor transamidase complex / GPI anchor biosynthetic process / protein retention in ER lumen / Attachment of GPI anchor to uPAR / natural killer cell lectin-like receptor binding / Post-translational modification: synthesis of GPI-anchored proteins / 加水分解酵素 / natural killer cell mediated cytotoxicity / natural killer cell activation / regulation of receptor signaling pathway via JAK-STAT / protein disulfide isomerase activity / tubulin binding / bioluminescence / generation of precursor metabolites and energy / antigen processing and presentation of endogenous peptide antigen via MHC class I via ER pathway, TAP-independent / antigen processing and presentation of endogenous peptide antigen via MHC class Ib / neuron differentiation / positive regulation of T cell mediated cytotoxicity / cytoplasmic vesicle / protein-containing complex assembly / neuron apoptotic process / immune response / external side of plasma membrane / intracellular membrane-bounded organelle / centrosome / endoplasmic reticulum membrane / cell surface / endoplasmic reticulum / mitochondrion / proteolysis / extracellular space / extracellular region / membrane / plasma membrane / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) Clavularia sp. (無脊椎動物) Clavularia sp. (無脊椎動物) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.22 Å | ||||||
 データ登録者 データ登録者 | Li, T. / Xu, Y. / Qu, Q. / Li, D. | ||||||
| 資金援助 |  中国, 1件 中国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2023 ジャーナル: Nat Commun / 年: 2023タイトル: Structures of liganded glycosylphosphatidylinositol transamidase illuminate GPI-AP biogenesis. 著者: Yidan Xu / Tingting Li / Zixuan Zhou / Jingjing Hong / Yulin Chao / Zhini Zhu / Ying Zhang / Qianhui Qu / Dianfan Li /  要旨: Many eukaryotic receptors and enzymes rely on glycosylphosphatidylinositol (GPI) anchors for membrane localization and function. The transmembrane complex GPI-T recognizes diverse proproteins at a ...Many eukaryotic receptors and enzymes rely on glycosylphosphatidylinositol (GPI) anchors for membrane localization and function. The transmembrane complex GPI-T recognizes diverse proproteins at a signal peptide region that lacks consensus sequence and replaces it with GPI via a transamidation reaction. How GPI-T maintains broad specificity while preventing unintentional cleavage is unclear. Here, substrates- and products-bound human GPI-T structures identify subsite features that enable broad proprotein specificity, inform catalytic mechanism, and reveal a multilevel safeguard mechanism against its promiscuity. In the absence of proproteins, the catalytic site is invaded by a locally stabilized loop. Activation requires energetically unfavorable rearrangements that transform the autoinhibitory loop into crucial catalytic cleft elements. Enzyme-proprotein binding in the transmembrane and luminal domains respectively powers the conformational rearrangement and induces a competent cleft. GPI-T thus integrates various weak specificity regions to form strong selectivity and prevent accidental activation. These findings provide important mechanistic insights into GPI-anchored protein biogenesis. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8imy.cif.gz 8imy.cif.gz | 509.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8imy.ent.gz pdb8imy.ent.gz | 380.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8imy.json.gz 8imy.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8imy_validation.pdf.gz 8imy_validation.pdf.gz | 3.2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8imy_full_validation.pdf.gz 8imy_full_validation.pdf.gz | 3.3 MB | 表示 | |
| XML形式データ |  8imy_validation.xml.gz 8imy_validation.xml.gz | 93.5 KB | 表示 | |
| CIF形式データ |  8imy_validation.cif.gz 8imy_validation.cif.gz | 129.7 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/im/8imy https://data.pdbj.org/pub/pdb/validation_reports/im/8imy ftp://data.pdbj.org/pub/pdb/validation_reports/im/8imy ftp://data.pdbj.org/pub/pdb/validation_reports/im/8imy | HTTPS FTP |
-関連構造データ
| 関連構造データ |  35576MC  8imxC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 4種, 4分子 GKUD
| #1: タンパク質 | 分子量: 96990.352 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Homo sapiens (ヒト), (組換発現) Homo sapiens (ヒト), (組換発現)  Clavularia sp. (無脊椎動物) Clavularia sp. (無脊椎動物)遺伝子: GPAA1, GAA1 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: O43292, UniProt: Q9U6Y3 Homo sapiens (ヒト) / 参照: UniProt: O43292, UniProt: Q9U6Y3 |
|---|---|
| #2: タンパク質 | 分子量: 73426.992 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Homo sapiens (ヒト), (組換発現) Homo sapiens (ヒト), (組換発現)  Clavularia sp. (無脊椎動物) Clavularia sp. (無脊椎動物)遺伝子: PIGK, GPI8 / 発現宿主:  Homo sapiens (ヒト) Homo sapiens (ヒト)参照: UniProt: Q92643, UniProt: Q9U6Y3, 加水分解酵素 |
| #3: タンパク質 | 分子量: 80691.539 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Homo sapiens (ヒト), (組換発現) Homo sapiens (ヒト), (組換発現)  Clavularia sp. (無脊椎動物) Clavularia sp. (無脊椎動物)遺伝子: PIGU, CDC91L1, PSEC0205, UNQ3055/PRO9875 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: Q9H490, UniProt: Q9U6Y3 Homo sapiens (ヒト) / 参照: UniProt: Q9H490, UniProt: Q9U6Y3 |
| #6: タンパク質 | 分子量: 28790.344 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: ULBP2, N2DL2, RAET1H, UNQ463/PRO791 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: ULBP2, N2DL2, RAET1H, UNQ463/PRO791 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: Q9BZM5 Homo sapiens (ヒト) / 参照: UniProt: Q9BZM5 |
-GPI transamidase component PIG- ... , 2種, 2分子 TS
| #4: タンパク質 | 分子量: 92825.766 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Homo sapiens (ヒト), (組換発現) Homo sapiens (ヒト), (組換発現)  Clavularia sp. (無脊椎動物) Clavularia sp. (無脊椎動物)遺伝子: PIGT, CGI-06, PSEC0163, UNQ716/PRO1379 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: Q969N2, UniProt: Q9U6Y3 Homo sapiens (ヒト) / 参照: UniProt: Q969N2, UniProt: Q9U6Y3 |
|---|---|
| #5: タンパク質 | 分子量: 90421.062 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  Homo sapiens (ヒト), (組換発現) Homo sapiens (ヒト), (組換発現)  Clavularia sp. (無脊椎動物) Clavularia sp. (無脊椎動物)遺伝子: PIGS, UNQ1873/PRO4316 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: Q96S52, UniProt: Q9U6Y3 Homo sapiens (ヒト) / 参照: UniProt: Q96S52, UniProt: Q9U6Y3 |
-糖 , 3種, 4分子 


| #7: 多糖 | 2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose | ||
|---|---|---|---|
| #16: 糖 | | #18: 糖 | ChemComp-PA1 / | |
-非ポリマー , 10種, 34分子 














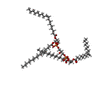
| #8: 化合物 | ChemComp-AJP / | ||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| #9: 化合物 | ChemComp-6OU / [( #10: 化合物 | ChemComp-Y01 / #11: 化合物 | ChemComp-MG / | #12: 化合物 | ChemComp-05E / | #13: 化合物 | #14: 化合物 | ChemComp-CA / | #15: 化合物 | ChemComp-LBN / | #17: 化合物 | ChemComp-81Q / [( | #19: 化合物 | ChemComp-80T / [( | |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Complex of GPI-T (inactive mutant) with GPI and proULBP2 タイプ: COMPLEX / Entity ID: #1-#6 / 由来: MULTIPLE SOURCES | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 値: 463 kDa/nm / 実験値: NO | ||||||||||||||||||||
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||||||||||
| 由来(組換発現) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||||||||||
| 緩衝液 | pH: 8 / 詳細: 0.1 % Digitonin, 150 mM NaCl, 20 mM Tris-HCl pH 8.0 | ||||||||||||||||||||
| 緩衝液成分 |
| ||||||||||||||||||||
| 試料 | 濃度: 25 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | ||||||||||||||||||||
| 試料支持 | グリッドの材料: GOLD / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: Quantifoil R1.2/1.3 | ||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 277 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 105000 X / 倍率(補正後): 53648 X / 最大 デフォーカス(公称値): 2500 nm / 最小 デフォーカス(公称値): 1000 nm / Cs: 2.7 mm / C2レンズ絞り径: 50 µm / アライメント法: COMA FREE |
| 試料ホルダ | 凍結剤: NITROGEN 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 2 sec. / 電子線照射量: 52 e/Å2 / フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 1 / 実像数: 4555 |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.18.2_3874: / 分類: 精密化 | ||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||
| 画像処理 | 詳細: The images were high-pass filtered and normalized | ||||||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 2981565 | ||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.22 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 176889 / アルゴリズム: FOURIER SPACE / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj














