+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8f86 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SIRT6 bound to an H3K9Ac nucleosome | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 要素 要素 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 キーワード キーワード | GENE REGULATION / nucleosome / SIRTUIN6 / histone deacylation / H3K9Ac | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報histone H3K56 deacetylase activity, NAD-dependent / ketone biosynthetic process / histone H3K18 deacetylase activity, NAD-dependent / histone H3K9 deacetylase activity, hydrolytic mechanism / histone H3K9 deacetylase activity, NAD-dependent / protein delipidation / NAD+-protein-lysine ADP-ribosyltransferase activity / chromosome, subtelomeric region / regulation of lipid catabolic process / positive regulation of protein localization to chromatin ...histone H3K56 deacetylase activity, NAD-dependent / ketone biosynthetic process / histone H3K18 deacetylase activity, NAD-dependent / histone H3K9 deacetylase activity, hydrolytic mechanism / histone H3K9 deacetylase activity, NAD-dependent / protein delipidation / NAD+-protein-lysine ADP-ribosyltransferase activity / chromosome, subtelomeric region / regulation of lipid catabolic process / positive regulation of protein localization to chromatin / NAD+-protein-arginine ADP-ribosyltransferase activity / DNA damage sensor activity / NAD-dependent protein demyristoylase activity / NAD-dependent protein depalmitoylase activity / positive regulation of stem cell differentiation / negative regulation of D-glucose import across plasma membrane / positive regulation of chondrocyte proliferation / transposable element silencing / protein acetyllysine N-acetyltransferase / protein deacetylation / NAD-dependent protein lysine deacetylase activity / pericentric heterochromatin formation / histone deacetylase activity, NAD-dependent / positive regulation of blood vessel branching / cardiac muscle cell differentiation / protein localization to site of double-strand break / positive regulation of vascular endothelial cell proliferation / negative regulation of glycolytic process / TORC2 complex binding / negative regulation of protein import into nucleus / regulation of protein secretion / regulation of double-strand break repair via homologous recombination / positive regulation of stem cell proliferation / positive regulation of double-strand break repair / negative regulation of gene expression, epigenetic / lncRNA binding / NAD+-protein mono-ADP-ribosyltransferase activity / DNA repair-dependent chromatin remodeling / positive regulation of stem cell population maintenance / positive regulation of telomere maintenance / negative regulation of cellular senescence / regulation of lipid metabolic process / 転移酵素; グリコシル基を移すもの; 五炭糖残基を移すもの / negative regulation of transcription elongation by RNA polymerase II / NAD+ poly-ADP-ribosyltransferase activity / NAD+ binding / negative regulation of gluconeogenesis / positive regulation of fat cell differentiation / subtelomeric heterochromatin formation / pericentric heterochromatin / response to UV / regulation of protein localization to plasma membrane / nucleosome binding / site of DNA damage / negative regulation of protein localization to chromatin / nucleotidyltransferase activity / 転移酵素; アシル基を移すもの; アミノアシル基以外のアシル基を移すもの / positive regulation of protein export from nucleus / determination of adult lifespan / circadian regulation of gene expression / chromatin DNA binding / regulation of circadian rhythm / base-excision repair / Pre-NOTCH Transcription and Translation / protein destabilization / positive regulation of fibroblast proliferation / protein import into nucleus / positive regulation of insulin secretion / structural constituent of chromatin / transcription corepressor activity / nucleosome / double-strand break repair / positive regulation of proteasomal ubiquitin-dependent protein catabolic process / heterochromatin formation / nucleosome assembly / glucose homeostasis / positive regulation of cold-induced thermogenesis / site of double-strand break / Processing of DNA double-strand break ends / damaged DNA binding / chromatin remodeling / protein heterodimerization activity / negative regulation of cell population proliferation / chromatin binding / chromatin / negative regulation of transcription by RNA polymerase II / endoplasmic reticulum / protein homodimerization activity / DNA binding / zinc ion binding / nucleoplasm / nucleus 類似検索 - 分子機能 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 生物種 | synthetic construct (人工物)  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.1 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 データ登録者 データ登録者 | Markert, J. / Whedon, S. / Wang, Z. / Cole, P. / Farnung, L. | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 資金援助 | 1件
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 引用 引用 |  ジャーナル: J Am Chem Soc / 年: 2023 ジャーナル: J Am Chem Soc / 年: 2023タイトル: Structural Basis of Sirtuin 6-Catalyzed Nucleosome Deacetylation. 著者: Zhipeng A Wang / Jonathan W Markert / Samuel D Whedon / Maheeshi Yapa Abeywardana / Kwangwoon Lee / Hanjie Jiang / Carolay Suarez / Hening Lin / Lucas Farnung / Philip A Cole /  要旨: The reversible acetylation of histone lysine residues is controlled by the action of acetyltransferases and deacetylases (HDACs), which regulate chromatin structure and gene expression. The sirtuins ...The reversible acetylation of histone lysine residues is controlled by the action of acetyltransferases and deacetylases (HDACs), which regulate chromatin structure and gene expression. The sirtuins are a family of NAD-dependent HDAC enzymes, and one member, sirtuin 6 (Sirt6), influences DNA repair, transcription, and aging. Here, we demonstrate that Sirt6 is efficient at deacetylating several histone H3 acetylation sites, including its canonical site Lys9, in the context of nucleosomes but not free acetylated histone H3 protein substrates. By installing a chemical warhead at the Lys9 position of histone H3, we trap a catalytically poised Sirt6 in complex with a nucleosome and employ this in cryo-EM structural analysis. The structure of Sirt6 bound to a nucleosome reveals extensive interactions between distinct segments of Sirt6 and the H2A/H2B acidic patch and nucleosomal DNA, which accounts for the rapid deacetylation of nucleosomal H3 sites and the disfavoring of histone H2B acetylation sites. These findings provide a new framework for understanding how HDACs target and regulate chromatin. | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8f86.cif.gz 8f86.cif.gz | 383.1 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8f86.ent.gz pdb8f86.ent.gz | 290.2 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8f86.json.gz 8f86.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/f8/8f86 https://data.pdbj.org/pub/pdb/validation_reports/f8/8f86 ftp://data.pdbj.org/pub/pdb/validation_reports/f8/8f86 ftp://data.pdbj.org/pub/pdb/validation_reports/f8/8f86 | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  28915MC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 5種, 9分子 AEBFCGDHK
| #1: タンパク質 | 分子量: 15271.863 Da / 分子数: 2 / 由来タイプ: 組換発現 由来: (組換発現) 発現宿主:  #2: タンパク質 | 分子量: 11263.231 Da / 分子数: 2 / 由来タイプ: 組換発現 由来: (組換発現) 発現宿主:  #3: タンパク質 | 分子量: 13978.241 Da / 分子数: 2 / 由来タイプ: 組換発現 由来: (組換発現) 発現宿主:  #4: タンパク質 | 分子量: 13524.752 Da / 分子数: 2 / 由来タイプ: 組換発現 由来: (組換発現) 発現宿主:  #7: タンパク質 | | 分子量: 39152.863 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: SIRT6, SIR2L6 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: SIRT6, SIR2L6 / 発現宿主:  参照: UniProt: Q8N6T7, 転移酵素; アシル基を移すもの; アミノアシル基以外のアシル基を移すもの, protein acetyllysine N-acetyltransferase, 転移酵素; ...参照: UniProt: Q8N6T7, 転移酵素; アシル基を移すもの; アミノアシル基以外のアシル基を移すもの, protein acetyllysine N-acetyltransferase, 転移酵素; グリコシル基を移すもの; 五炭糖残基を移すもの |
|---|
-DNA鎖 , 2種, 2分子 IJ
| #5: DNA鎖 | 分子量: 57400.559 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現) synthetic construct (人工物) / 発現宿主:  |
|---|---|
| #6: DNA鎖 | 分子量: 56831.191 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現) synthetic construct (人工物) / 発現宿主:  |
-非ポリマー , 2種, 2分子 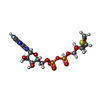


| #8: 化合物 | ChemComp-ZSL / [( |
|---|---|
| #9: 化合物 | ChemComp-ZN / |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: SIRT6 bound to H3K9Ac / タイプ: COMPLEX / Entity ID: #1-#7 / 由来: MULTIPLE SOURCES |
|---|---|
| 分子量 | 実験値: NO |
| 緩衝液 | pH: 7.5 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: OTHER |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1700 nm / 最小 デフォーカス(公称値): 700 nm |
| 撮影 | 電子線照射量: 50.45 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.20.1_4487: / 分類: 精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア | 名称: PHENIX / カテゴリ: モデル精密化 | ||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 95205 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: RIGID BODY FIT / 空間: REAL | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj










































