+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8dut | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Duplex-G-quadruplex-duplex (DGD) class_1 | ||||||
 要素 要素 | (Duplex-G-quadruplex-duplex (46-MER)) x 2 | ||||||
 キーワード キーワード | DNA / G-quadruplex / promoter / duplex | ||||||
| 機能・相同性 | DNA / DNA (> 10) 機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 | synthetic construct (人工物) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 7.4 Å | ||||||
 データ登録者 データ登録者 | Monsen, R.C. / Chua, E.Y.D. / Hopkins, J.B. / Chaires, J.B. / Trent, J.O. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2023 ジャーナル: Nucleic Acids Res / 年: 2023タイトル: Structure of a 28.5 kDa duplex-embedded G-quadruplex system resolved to 7.4 Å resolution with cryo-EM. 著者: Robert C Monsen / Eugene Y D Chua / Jesse B Hopkins / Jonathan B Chaires / John O Trent /  要旨: Genomic regions with high guanine content can fold into non-B form DNA four-stranded structures known as G-quadruplexes (G4s). Extensive in vivo investigations have revealed that promoter G4s are ...Genomic regions with high guanine content can fold into non-B form DNA four-stranded structures known as G-quadruplexes (G4s). Extensive in vivo investigations have revealed that promoter G4s are transcriptional regulators. Little structural information exists for these G4s embedded within duplexes, their presumed genomic environment. Here, we report the 7.4 Å resolution structure and dynamics of a 28.5 kDa duplex-G4-duplex (DGD) model system using cryo-EM, molecular dynamics, and small-angle X-ray scattering (SAXS) studies. The DGD cryo-EM refined model features a 53° bend induced by a stacked duplex-G4 interaction at the 5' G-tetrad interface with a persistently unstacked 3' duplex. The surrogate complement poly dT loop preferably stacks onto the 3' G-tetrad interface resulting in occlusion of both 5' and 3' tetrad interfaces. Structural analysis shows that the DGD model is quantifiably more druggable than the monomeric G4 structure alone and represents a new structural drug target. Our results illustrate how the integration of cryo-EM, MD, and SAXS can reveal complementary detailed static and dynamic structural information on DNA G4 systems. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8dut.cif.gz 8dut.cif.gz | 74.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8dut.ent.gz pdb8dut.ent.gz | 52.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8dut.json.gz 8dut.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8dut_validation.pdf.gz 8dut_validation.pdf.gz | 874.5 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8dut_full_validation.pdf.gz 8dut_full_validation.pdf.gz | 908.5 KB | 表示 | |
| XML形式データ |  8dut_validation.xml.gz 8dut_validation.xml.gz | 20.1 KB | 表示 | |
| CIF形式データ |  8dut_validation.cif.gz 8dut_validation.cif.gz | 27.6 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/du/8dut https://data.pdbj.org/pub/pdb/validation_reports/du/8dut ftp://data.pdbj.org/pub/pdb/validation_reports/du/8dut ftp://data.pdbj.org/pub/pdb/validation_reports/du/8dut | HTTPS FTP |
-関連構造データ
| 関連構造データ |  27726MC  27725  27727 M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 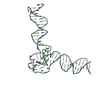
|
|---|---|
| 1 |
|
- 要素
要素
| #1: DNA鎖 | 分子量: 14086.031 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
|---|---|
| #2: DNA鎖 | 分子量: 14407.232 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: 2D ARRAY / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: synthetic duplex-G-quadruplex-duplex construct mimicking a promoter G4 タイプ: COMPLEX / Entity ID: all / 由来: NATURAL | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 実験値: NO | ||||||||||||||||||||
| 由来(天然) | 生物種: synthetic construct (人工物) | ||||||||||||||||||||
| 緩衝液 | pH: 7.2 | ||||||||||||||||||||
| 緩衝液成分 |
| ||||||||||||||||||||
| 試料 | 濃度: 2.5 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES / 詳細: Sample was monodisperse. | ||||||||||||||||||||
| 試料支持 | グリッドの材料: GOLD / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: UltrAuFoil R1.2/1.3 | ||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 278 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2700 nm / 最小 デフォーカス(公称値): 800 nm / Cs: 2.7 mm |
| 試料ホルダ | 凍結剤: HELIUM 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 撮影 | 平均露光時間: 0.4 sec. / 電子線照射量: 68.54 e/Å2 フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 実像数: 12175 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 画像処理 | 詳細: Selected images were dose-weighted and corrected for beam-induced motion. | ||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 666328 | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 7.4 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 110105 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 原子モデル構築 | B value: 557.2 / プロトコル: FLEXIBLE FIT / 空間: REAL / Target criteria: map correlation |
 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj






































